Actividades Transversales EDCTI Anteriores
Universidad de Granada | Escuela de Posgrado | Administración electrónicaBuscar
Actividades Transversales EDCTI Anteriores
Descargar versión en PDFCurso 2023/2024
Inteligencia Artificial en 360º
- Descripción breve
Es notorio que la Inteligencia Artificial (I.A.) permea todas las áreas de conocimiento y puede tener un impacto relevante en cuestiones sociales y económicas. Sin embargo, también es notorio que en muchos casos no se tiene conocimiento riguroso de sus potencialidades y limitaciones, entendiéndose más como un arcano con nombre bonito que como una disciplina científica bien asentada, que puede proporcionar soluciones a problemas para los que no las hay en todos los ámbitos del saber, y muy particularmente para muchas de las líneas de investigación más avanzadas (en las que se inscriben las tesis doctorales).
De cara a abrir ventanas de oportunidad para la investigación a partir de técnicas y modelos basados en I.A., es fundamental que los doctorandos conozcan de qué hablamos cuando hablamos de esa materia, cuáles son sus limitaciones y cuales sus perspectivas a corto plazo, desde un punto de vista científico, solido y riguroso.
En esta actividad de carácter esencialmente transversal y de máximo rigor científico, se plantea como objetivo principal clarificar las cuestiones básicas asociadas con la I.A., desterrar algunos de los mitos más usuales y proveer una explicación clara y sencilla de las principales técnicas que permiten la construcción de sistemas basados en IA.
- Ponentes
• David A. Pelta Mochcovsky. Dpto de Ciencias de la Computación e Inteligencia Artificial. ETSI Informática y de Telecomunicación
• Carlos Cruz Corona. Dpto de Ciencias de la Computación e Inteligencia Artificial. ETSI Informática y de Telecomunicación
• José Luis Verdegay Galdeano. Dpto de Ciencias de la Computación e Inteligencia Artificial. ETSI Informática y de Telecomunicación
• Jorge Sergio Igor Zwir Nawrocki. ETSI Informática y de Telecomunicación
• Margarita Robles Carrillo. Facultad de Derecho UGR
• Rocío Romero Zaliz. ETSI Informática y de Telecomunicación
- Perfil
Dirigido a estudiantes de las 3 Escuelas de Doctorado (EDCTI, EDCS y EDHCSJ).
- Contenidos (Programa preliiminar sujeto a cambios menores antes del comienzo del curso)
• Un recorrido histórico por la IA.
• Representación del conocimiento.
• “Machine Learning”.
• Métodos de Búsqueda y Optimización.
• Procesamiento del lenguaje natural.
• Técnica de Recuperación de la Información.
• Procesamiento de Imágenes y Video.
• Robótica e IA.
- Plazo de solicitud: del 5 al 17 de marzo de 2024
- Forma de solicitud: a través de este FORMULARIO
- Sesiones: 9, 11, 16, 18 y 23 de abril 2024
- Horario: de 16 a 20h
- Seminario de Aplicaciones de IA en fecha por confirmar
- Nº de plazas: 30 presenciales con evaluación / Modalidad online: sin límite de plazas
- Lugar : aula 0.1 de la Escuela Técnica Superior de Ing. Informática y de Telecomunicación
La modalidad principal del curso es presencial. Los participantes presenciales que superen la evaluación, obtendrán un diploma de aprovechamiento del curso. En caso contrario, se emitirá un diploma de asistencia (se requiere una asistencia mínima al 75% de las sesiones).
Previo registro, las sesiones del curso se podrán seguir de manera online. Los participantes en esta modalidad que hayan asistido, al menos, al 75% de las sesiones, podrán solicitar un diploma de asistencia.
- Evaluación:
La superación del curso requerirá:
1) la asistencia a (al menos) el 75% de las sesiones.
2) Realización de un informe bibliográfico.
Se podrá plantear de acuerdo a las dos vías siguientes:
a) Dado un problema de interés provisto por el/la estudiante, el informe recogerá que técnicas de IA se han aplicado para su resolución.
b) Dada una técnica de interés para el/la estudiante (por ej. técnicas de aprendizaje), el informe recogerá que problemas de su área se han resuelto con dicha técnica.
Los responsables del curso estarán abiertos a otras propuestas de trabajo.
Técnicas estadísticas avanzadas aplicadas en Ciencias Experimentales: fundamentos, interpretación e implementación en R
Ponentes:
• Dra. D.ª Beatriz Cobo Rodríguez.
• Dr. D. Ramón Ferri García.
• Dr. D. Christian Acal González.
Justificación académica del curso: :
Es incuestionable la importancia que en las últimas décadas ha experimentado la aplicación de numerosas técnicas probabilístico-estadísticas en múltiples campos de aplicación. La razón última de ello viene motivada por la necesidad de describir y explicar la evolución de fenómenos, no sólo desde un punto de vista cualitativo sino cuantitativo, a la vez que se hace imprescindible en múltiples ocasiones poder inferir comportamientos futuros de los sistemas que son objeto de estudio.
Continuando la línea del curso de Técnicas Estadísticas Básicas, el objetivo del curso es doble: por un lado, complementar algunos aspectos relativos a técnicas ya introducidas en el curso precedente y, por otro, presentar otras técnicas de carácter más avanzado y que son de amplio uso en múltiples campos de aplicación. Se hará hincapié sobre los fundamentos, condiciones de aplicabilidad e interpretación de resultados que ayuden a una mejor descripción de los fenómenos estudiados por los alumnos en el desarrollo de sus investigaciones. Otro de los objetivos del curso es el de mostrar la implementación de estas técnicas mediante R, introduciendo al alumno en el empleo de uno de los programas que mayor difusión ha adquirido en los últimos años.
Lugar de realización: Aula de informática O-04 (zona de Matemáticas de la facultad de Ciencias).
Plazas: 25
Duración: 25 horas
Modalidad: Presencial
Periodo de impartición: Del 3 al 7 de junio de 2024
Horario: De 09:00h a 14:00h
Plazo de solicitud: Del 9 al 15 de mayo de 2024
Forma de solicitud: A través del siguiente FORMULARIO
Programa:
1. Estudios avanzados en regresión lineal (Profa. Beatriz Cobo). Sesión: 3 de junio.• Diagnosis del modelo: análisis de residuos (normalidad, heterocedasticidad, autocorrelación).
• Observaciones influyentes y atípicos. Medidas para la detección.
• Multicolinealidad.
Modelos de regresión generalizados (Prof. Ramón Ferri). Sesión: 4 de junio.• Regresion de Poisson.
• Regresión de Cox.
• Regresión logística binaria y multinomial.
Introducción a las técnicas de muestreo (Prof. Ramón Ferri). Sesión: 5 de junio.• Muestreo aleatorio simple.
• Muestreo con probabilidades desiguales.
• Muestreo estratificado.
• Muestreo por conglomerados.
• Métodos de captura-recaptura.
Modelos de análisis de la varianza paramétricos y no paramétricos (Prof. Christian Acal). Sesión: 6 de junio.• Anova de 1 vía, comprobación de supuestos. Interpretación.
• Anova de 2 vías con y sin interacción.
• Análisis de la varianza multivariante.
• Anova con medidas repetidas.
Introducción al análisis de fiabilidad (Prof. Christian Acal). Sesión: 7 de junio.• Modelos de fallo.
• Distribuciones continuas.
• Test de K-S.
• Comparación de modelos.
Actividades paralelas:
Se propondrá a los alumnos la realización de ejemplos de aplicación para la realización de prácticas individualizadas y tutorizadas de forma personalizada. Esta parte constituirá la evaluación final que determinará el grado de aprovechamiento del curso. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado.
Python avanzado para ciencia e ingeniería
- Profesorado: José Vicente Pérez Peña (UGR)
- Duración: 20 horas presenciales.
- Fechas: 10, 11, 12, 13, 17, 18, 19, 20, 24, 25 de junio 2024
- Horario: De 09:00 h a 11:00 h.
- Lugar: Aula Juan Campos de la Facultad de Ciencias (Presencial)
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
- Plazo de inscripción: 14 a 19 de mayo de 2024.
- Forma de inscripción: Mediante el siguiente FORMULARIO
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad. Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes. La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos. Una lista completa de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Manejo de matrices multidimensionales con numpy
2.- Funciones básicas para la creación y utilización de matrices de numpy
3.- Lectura-escritura en disco de datos
4.- Creación y representación de funciones matemáticas
5.- Creación de distintos gráficos con matplotlib
6.- Modificación de símbolos y leyendas
7.- Análisis de imagen con scipy
El alumno será capaz de:
1.- Crear y modificar gráficos
2.- Integrar LaTeX directamente en un gráfico
3.- Representar funciones y resolver ecuaciones matemáticas
4.- Entender la documentación de las librerías de Python
5.- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
- Programa formativo:
Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas. Representación de nube de puntos Representación de histogramas y boxplots. Definiendo colores y símbolos. Añadiendo leyendas y etiquetas. Control de ejes. Representación de múltiples figuras.
Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage.
Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Introducción a Python: Elementos básicos del lenguaje
- Profesorado: Patricia Ruano Roca (UGR)
- Duración: 20 horas presenciales
- Fechas y horario: lunes a viernes del 8 al 19 de julio 2024. Horario de 12:00 h a 14:00 h.
- Modalidad: Virtual
- Lugar: Virtual.
- Plazas y perfil: 15 plazas/edición. Dirigido preferentemente a alumnos/as de primer año de doctorado.
- Inscripción: del 2 al 4 de julio 2024 a través del siguiente FORMULARIO
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje esté ganando cada vez más popularidad entre científicos e ingenieros.
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Los elementos básicos de un lenguaje de programación
2.- Tipos de variables y su manipulación
3.- Manipulación de listas, tuplas y diccionarios
4.- Flujos condicionales if y recursivos for
5.- Funciones básicas del lenguaje
6.- Creación de funciones propias
7.- Control de código y manejo excepciones
El alumno será capaz de:
1.- Crear scripts en python para resolver problemas
2.- Leer y analizar un programa escrito en Python
3.- Manejar los principales entornos de programación con IPython (Spyder y Jupyter)
4.- Leer y escribir datos en ficheros de texto
5.- Diseñar algoritmos para la resolución secuencial de problemas
6.- Depurar programas y reconocer los principales tipos de errores
- Programa:
Tema 1. Introducción (1h) Introducción a los lenguajes de programación Historia de Python Descarga e instalación de anaconda. La consola de Python. Partes principales del IDE Spyder.
Tema 2. Tipos básicos, variables y expresiones (4h) Tipos de datos en Python. Variables, operadores y expresiones. Instalar, importar y utilizar módulos en Python. Listas, tuplas y diccionarios.
Tema 3. Operadores y funciones (4h) Operador lógico if. Bucles for. Bucles while. Creación y utilización de funciones en Python.
Tema 4. Operación de entrada/salida y optimización de código (3h) Lectura de ficheros de texto. Escritura en archivos de texto. Módulos os y sys. Control de ficheros y directorios. Optimización de código. Tipos de errores principales en Python. Control de código y manejo excepciones.
Curso 2022/2023
Python avanzado para ciencia e ingeniería
- Profesorado: José Vicente Pérez Peña (UGR)
- Duración: 20 horas presenciales.
- Fechas y horario: SE CANCELA LA CELEBRACIÓN DE ESTE CURSO
- Lugar: por determinar (Presencial)
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
- Plazo de inscripción: por determinar.
- Forma de inscripción: a través de este FORMULARIO (se activará una vez empiece el plazo de solicitud)
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad. Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes. La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos. Una lista completa de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Manejo de matrices multidimensionales con numpy
2.- Funciones básicas para la creación y utilización de matrices de numpy
3.- Lectura-escritura en disco de datos
4.- Creación y representación de funciones matemáticas
5.- Creación de distintos gráficos con matplotlib
6.- Modificación de símbolos y leyendas
7.- Análisis de imagen con scipy
El alumno será capaz de:
1.- Crear y modificar gráficos
2.- Integrar LaTeX directamente en un gráfico
3.- Representar funciones y resolver ecuaciones matemáticas
4.- Entender la documentación de las librerías de Python
5.- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
- Programa formativo:
Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas. Representación de nube de puntos Representación de histogramas y boxplots. Definiendo colores y símbolos. Añadiendo leyendas y etiquetas. Control de ejes. Representación de múltiples figuras.
Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage.
Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Resonancia Magnética Nuclear, GERMN
Curso destinado a alumnos de TFM y doctorado con un enfoque práctico hacia la interpretación de espectros 1D y 2D.
- Programa:
Tema I. Origen de la señal de RMN y núcleos activos en RMN. Desplazamiento químico. Integración. Factores que afectan al desplazamiento químico: efectos inductivos, mesómeros, cargas netas, anisotropía, campos eléctricos, van der Waals, enlaces de hidrógeno, efecto isotópico, efecto del medio. 2 h.
Tema II. El acoplamiento escalar. Espectros de primer orden: notación, tipos de acoplamientos (nJ, n ≥ 2), efecto tejado, árboles de desdoblamiento. Equivalencia química y equivalencia magnética. Relaciones entre estructura y magnitud relativa de los acoplamientos nJHH. Acoplamientos heteronucleares. Desacoplamiento homo y heteronuclear. Acoplamientos de orden superior a 1. 3 h.
Tema III. Concepto de relajación y factores de los que depende. Relación entre tiempos de relajación y estructura. El efecto Overhauser nuclear. Relación entre NOE y estructura. 1 h.
Tema IV. RMN dinámica: escalas de tiempo en RMN, efectos en el desplazamiento químico y en las constantes de acoplamiento. 1 h.
Tema V. RMN-13C{1H}: medida de espectros (efecto del desacoplamientos de 1H). Desplazamiento químico. Factores que afectan al desplazamiento químico. Edición de espectros. 2 h.
Tema VI. Introducción a la RMN bidimensional. Tipos de espectros y ejemplo de aplicación (resolución de problema estructural analizando COSY, HSQC y NOESY, sin otros concimientos previos). 1 h.
Tema VII. Espectros COSY, COSYDQF, TOCSY (incluido TOCSY selectivo), HSQC, HMQC, HMBC, NOESY, HOESY. 2 h.
- Objetivos. Al finalizar el curso el alumno deberá saber: Las estrategias de asignación estructural mediante la medida de espectros de RMN de alta resolución. La obtención de información estructural derivada de los efectos de relajación y de los procesos dinámicos que afecten a la molécula problema.
- Tipo de docencia. En línea, mediante la plataforma virtual Blackboard.
- Profesor. Fernando López Ortiz, Universidad de Almería
- Con la colaboración de: Real Sociedad Española de Química (grupo especializado en resonancia magnética nuclear)
- Fechas. 7 - 28 de noviembre de 9 a 11 h según se indica en la planificación siguiente:
- Planificación:
| Lunes 7 | Jueves 10 | Lunes 21 | Jueves 24 | Lunes 28 | Jueves 1 |
|---|---|---|---|---|---|
| Tema I/2 h | Tema II/2 h | Tema II/1 h | Tema IV/1 h | Tema V/1 h | Tema VII/2 h |
| Tema III/1 h | Tema V/1 h | Tema VI/1 h |
- Forma y plazo de inscripción: del 17 al 28 de octubre de 2022 a través del siguiente FORMULARIO
- Evaluación. No se contemplan exámenes. En su lugar se puede proporcionar un certificado de participación si se ha asistido al menos al 80 % del curso.
Multivariate Exploratory Data Analysis (MEDA): Understanding by looking at data
- Date: 14-18 november 2022
- Participants: 30
- Place: aula B1 ETSIIT( E.T.S. de Ingenierías Informática y de Telecomunicación )
- Deadline for application: 17 october- 6 november 2022
- How to apply: Use this APLICATION FORM.
- NOTES
- The course will be held presentially. Prof. Bro will intervene by virtual connection
- The course will be held in English.
It is necessary to have at least a B1 level (preferably B2 or higher). You can indicate in the “Observations” section your level of English and, if it is the case, if you have a certificate. / Este curso se impartirá íntegramente en inglés. Es necesario contar como mínimo con un nivel B1 (preferentemente B2 o superior). Pude indicar en el apartado “Observaciones” su conocimientos de inglés y en su caso si dispone de certificado para acreditarlo.
- It is requiered basic knowledge of MatLab. Those students who can provide certification of that knowledge will have preference in admission.
- Own laptop required
- Course Goal
Do you have complicate data? Difficult to understand? With thousands of variables/observations? Or with too little observations? Missing data? Time series? Multiple sources? Big Data?
The course goal is to introduce the students to very powerful data visualization techniques to look into your data set. There is a bunch of Machine Learning (ML) methods that can do difficult tasks (like classification, modelling and prediction) using a black-box approach over data, deep learning being a popular example. This course shows a totally different approach to handling data, using ML only as an instrument (as a means) to understand your data. MEDA will show you how to look into your data set, regardless its complexity, so that you can find groups of individuals and classify them, understand relationships among measured quantities, detect anomalies, find parsimonious models, etc.
The course is led by Professor Rasmus Bro, world leading professor on data analysis in biological and food sciences, and his collaborator at the UGR Dr. José Camacho, specialist on data analysis in Big Data and Exploratory Data Analysis.
- Teaching hours: 30
- Teachers:
Professor Bro is a prominent figure in the field of data analysis and in particular in multivariate analysis. During the last two decades, Prof. Bro has been a principal actor in the development of multivariate analysis in chemical and biological applications in the chemometrics area, in which according to google scholar is the second top researcher. His vast research work is outstanding, presenting an H index equal to 78. Prof. Bro is the author of the most referenced tutorial of PARAFAC (2843 citations), the developer of an extensively used multi-way version of Partial Least Squares (N-PLS) and co-author of more than 200 publications mainly related to the use of multi-way analysis in real life applications. His contributions to the use of constrained modelling are also very relevant, including the use of sparse methodologies for data analysis, and he has co-authored relevant articles to the problem of data fusion, a main challenge in Big Data analyses. The international influence in the community of his course “Multi-way Analysis” and his monograph “Multi-way Analysis: applications in the chemical sciences” is widely recognized. Prof. Bro has taught courses on data analysis in dozens of public and private organizations around the world. From 2001, he is the head of ODIN, an industrial research consortium offering courses, workshops, international contacts and student collaboration.
José Camacho is full professor in the Department of Signal Theory, Networking and Communications and researcher in the Information and Communication Technologies Research Centre, CITIC for its initials in Spanish, both at the University of Granada, Spain. His research interests include exploratory data analysis, anomaly detection and optimization with multivariate techniques applied to data of very different nature, including personalized medicine and communication networks. He is especially interested in the use of exploratory data analysis to Big Data.
- Examination:
Every person analyze their own data under supervision of the teacher and writes a report. The report must be short and concise. A short description of the data and their background must be provided. A short description of aim of the present work must be provided. This aim is not necessarily the overall aim of the project from which the data stem (although this is of course nice). Rather the purpose should be chosen in order to test and evaluate the students’ ability to use the methods taught at the course. It is important to discuss in detail how the models have been critically used for the stated purposes.
- Schedule:
Day 1: PCA (Prof. Bro & Dr. Camacho)
| 8:30-9:30 | Welcome (Bro & Camacho) |
| 9:30-10:00 | Introduction and algebra without tears |
| 10:00-11:15 | Principal Component Analysis – PCA |
| 11:15-11:30 | Break |
| 11:30-12:00 | Software introduction (demos/hands-on) |
| 12:00-12:30 | Exercises – PCA |
| 12:30-13:30 | Validation, outliers – PCA |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises – PCA |
Day 2: PLS (Prof. Bro)
| 9:00-9:15 | PCA summary |
| 9:15-10:30 | Multivariate calibration - PLS |
| 10:30-10:45 | Break |
| 10:45-11:30 | Exercises – Multivariate calibration |
| 11:30-13:00 | Validation and outliers incl. exercises |
| 13:00-15:00 | Lunch |
| 15:00-16:00 | Preprocessing and nice to know |
| 16:00-16:15 | Break |
| 16:15-18:00 | Competition! |
Day 3: MEDA Toolbox (Dr. Camacho)
| 9:00-10:00 | Introduction to the MEDA Toolbox |
| 10:00-11:15 | Using the command line interface |
| 11:15-11:30 | Break |
| 11:30-12:30 | Advanced Exploratory Data Analysis |
| 12:30-13:30 | Exercises & Examples |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 4: Big Data (Dr. Camacho)
| 9:00-11:00 | Extensions to Big Data: Big Observations |
| 11:00-11:30 | Break |
| 11:30-12:30 | Exercises |
| 12:30-13:30 | Extensions to Big Data: Big Variables |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 5: Playing with your data I (Prof. Bro & Dr. Camacho)
Time will be devoted to analyze your own data under the supervision of the course monitors, who will guide you through different analysis techniques to pursue your goals.
| 9:00-14:00 | Playing with your data |
4th EUROMBR Summer School on Microfluidic (EUROMBR 2023)
- Esta escuela de verano está destinada, principalmente, a estudiantes de doctorado en las áreas de química, ingeniería química, bioquímica, biotecnología y farmacia, y su objetivo es la formación de jóvenes investigadores en el uso de los sistemas de microfluídica para la resolución de problemas reales, principalmente en los campos de desarrollo de bioprocesos (microbiorreactores) y biomedicina. Por ello, esta escuela contará con dos cursos prácticos paralelos:
- Training Course on Bioprocess Development of Microbiorreactors, de 5 días de duración (11 al 15
de septiembre)
- Training Course on Medical Applications of Microfluidics (11 al 13 de septiembre).
En cada uno de estos cursos se tratarán tanto aspectos teóricos como prácticos, destacando la realización de una gran cantidad de horas prácticas de laboratorio.
Toda la información sobre el programa se puede consultar en la web https://eurombr.ugr.es/ .
- Contacto: Jorge F. Fernández Sánchez (--LOGIN--94d036a22f173df1cceed7ff0f4b704eugr[dot]es y --LOGIN--651bcea8a333ddd63b793ace6d75aa97ugr[dot]es ).
- Inscripción: hasta el 15 de julio de 2023
El número de plazas es limitado, por lo que se atenderán las inscripciones por orden de registro.
- Precio:
- Training Course on Bioprocess Development of Microbiorreactors: 300 €
- Training Course on Medical Applications of Microfluidics: 200 €
Las inscripciones con fecha posterior al 15 de julio tendrán un sobrecargo. La cuota de inscripción al curso incluye la participación en las conferencias y sesiones prácticas de laboratorio, los materiales necesarios para llevar a cabo las diferentes actividades, cóctel de bienvenida, cafés, almuerzos, excursión y cóctel en un Carmen.
TALLER TEÓRICO-PRÁCTICO SOBRE FENÓMENOS INTERFACIALES
El dia 13 de Septiembre de 2023 se celebrará en la facultad de Ciencias de la Universidad de Granada el TALLER TEÓRICO-PRÁCTICO SOBRE FENÓMENOS INTERFACIALES, como actividad previa al VI Congreso de Jóvenes Investigadores e Investigadoras en Coloides e Interfases (JICI6, https://wpd.ugr.es/~jici6/).
Este taller pretende cubrir los fundamentos de la ciencia de superficies e interfases en una jornada con contenidos teóricos y clases prácticas en laboratorios especializados. El objetivo del taller es proporcionar una visión global de la potencialidad y multidisciplinariedad de los fenómenos interfaciales en la actualidad.
El proceso de inscripción está abierto hasta el 19 de mayo de 2023, inclusive.
Puedes encontrar toda la información, formulario de inscripción y novedades del evento en la página web:
http://wpd.ugr.es/~jici6/taller-teorico-practico-de-fenomenos-interfaciales/
AGORA AEROSOL TRAINING COURSE: CHARACTERIZATION OF ATMOSPHERIC AEROSOL USING IN-SITU AND REMOTE SENSING TECHNIQUES
Lugar y fecha:
Andalusian Global ObseRvatory of the Atmosphere, Instituto de Investigación del Sistema Tierra de Andalucía, Granada, Spain. June 12-17, 2023.
Descripción breve:
El proyecto ATMO-ACCESS apoya actividades innovadoras de formación y educación relacionadas con las infraestructuras de investigación atmosférica. Es crucial para el éxito futuro de las instalaciones atmosféricas europeas garantizar que las nuevas generaciones de investigadores adquieran conocimientos y habilidades para aprovechar todas las herramientas esenciales para su investigación. Esta capacitación en AGORA Aerosol Training School es la primera de tres sesiones innovadoras para agregar la dimensión de capacitación a las infraestructuras de investigación utilizando acceso físico, remoto y virtual.
Grupo objetivo:
El curso de formación está destinado principalmente a investigadores y técnicos del campo atmosférico. Los alumnos deben tener conocimientos previos sobre las ciencias de los aerosoles, al menos en una de las técnicas de medición de aerosoles. Podrían ser estudiantes de master, estudiantes de doctorado, científicos o técnicos que inician su carrera. Se requieren buenas habilidades de comunicación en inglés.
Número de participantes: 25
Contenidos del curso y resultados del aprendizaje:
Las conferencias brindan conocimientos fundamentales en técnicas novedosas y avanzadas para medir las propiedades de los aerosoles, cubriendo in situ, sensores remotos e instrumentos de laboratorio. Este curso de formación híbrido se realizará de forma presencial en el Observatorio Global de la Atmósfera de Andalucía (AGORA) en Granada (España), e incluirá una visita a la estación de Sierra Nevada y formación práctica en algunos instrumentos novedosos de aerosoles. Se combina con actividades a distancia la semana anterior (1,5 h al día, 2 días) y posterior al curso (3 h al día, 5 días). Las conferencias presenciales interactivas están previstas del lunes 12 al viernes 16 de junio (8:30 - 17:30). Todos los participantes obtendrán un certificado por su participación.
Ponentes:
Dr. Lucas Alados-Arboledas, University of Granada (Spain)
Dr. Andrés Alastuey, IDAEA-CSIC (Spain)
Dr. Elisabeth Andrews, NOAA (United States)
Dr. Martine Collaud-Coen, MeteoSwiss (Switzerland)
Dr. Oleg Dubovik, Centre National de la Recherche Scientifique (France)
Dr. Martin Gysel-Beer, Paul Scherrer Institute (Switzerland)
Dr. Stelios Kazadzis, World Radiation Center (Switzerland)
Dr. Anton Lopatin, GRASP SAS (France)
Dr. Griša Močnik, University of Nova Gorica (Slovenia)
Dr. Francisco Navas-Guzmán, University of Granada (Spain)
Dr. Doina Nicolae, INOE (Romania)
Dr. Gloria Titos, University of Granada (Spain)
Dr. Antonio Valenzuela, University of Granada (Spain)
Coordinadores: Dr. Lucas Alados Arboledas (alados@ugr.es) y Juan Luis Guerrero Rascado (rascado@ugr.es)
Más información en: https://atmosphere.ugr.es/en/about/presentation/agora_aerosol_training_course
Tecnología del vacío y sus aplicaciones. Espectrometría de masas cuadrupolar y Análisis de gases
Curso destinado a estudiantes de doctorado y master, usuarios y responsables de mantenimiento de sistemas de alto y ultra alto vacío: XPS, STM, sistemas de análisis de gases acoplados a termobalanzas, equipos de quimisorción.
- Programa
Día 1. Tecnología del vacío. (3,5 h aula)
1) Descripción aplicaciones en procesos industriales: envasado de alimentos, aeronáutica y aeroespacial, energía fotovoltaica y termosolar, crecimiento de capas finas: metalización faros coches, espejos telescopios, vidrios arquitectónicos.
2) Descripción aplicaciones en investigación: nanotecnología y aceleradores de partículas.
3) Actividades StartUp
Dia 2. Espectrometría de masas cuadrupolar (2,5 h aula / 1 h visita CIC)
1) Espectros de gases residuales en cámara de alto y ultra alto vacío.
2) Sistemas análisis de gases - Descripción aplicaciones.
3) Generación hidrógeno verde.
- Duración: 7 horas.
- Tipo de docencia: Presencial. Facultad de Ciencias - Sala de Medios Audio-Visuales (ubicada en el vestíbulo de la Facultad de Ciencias). Visita al Centro de Instrumentación Científica de la Universidad de Granada.
- Profesor: César Atienza. Experto en Tecnología del vacío y desarrollo de sistemas especiales. Ha impartido cursos y seminarios de Tecnología de Vacío, espectrometría de masas cuadrupolar y sistemas de análisis de gases en diversas universidades españolas y centros de investigación.
- Fechas: 13 y 14 de abril 2023.
- Horario: jueves 13 de 10:00 a 13:00 h y viernes 14 de 10:00 a 12:00h y de 12:00 a 13:00 h visita al Centro de Instrumentación Científica.
- Forma y plazo de inscripción: de 20 a 28 de marzo a través del siguiente FORMULARIO
- Evaluación: No se contemplan exámenes. En su lugar se puede proporcionar un certificado de participación si se ha asistido al menos al 80 % del curso.
Curso 2021/2022
Python avanzado para ciencia e ingeniería
- Profesorado: José Vicente Pérez Peña (UGR)
- Duración: 20 horas presenciales.
- Fechas y horario: 27, 28, 29 de Abril, 3, 4, 5, 6, 18, 19, 20 de Mayo 2022. De 16:00 a 18:00h.
- Lugar: Aula Juan Campos de la Facultad de Ciencias (Presencial)
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
- Plazo de inscripción: del 1 al 17 de abril de 2022
- Forma de inscripción: a través de este FORMULARIO
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad. Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes. La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos. Una lista completa de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Manejo de matrices multidimensionales con numpy
2.- Funciones básicas para la creación y utilización de matrices de numpy
3.- Lectura-escritura en disco de datos
4.- Creación y representación de funciones matemáticas
5.- Creación de distintos gráficos con matplotlib
6.- Modificación de símbolos y leyendas
7.- Análisis de imagen con scipy
El alumno será capaz de:
1.- Crear y modificar gráficos
2.- Integrar LaTeX directamente en un gráfico
3.- Representar funciones y resolver ecuaciones matemáticas
4.- Entender la documentación de las librerías de Python
5.- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
- Programa formativo:
Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas. Representación de nube de puntos Representación de histogramas y boxplots. Definiendo colores y símbolos. Añadiendo leyendas y etiquetas. Control de ejes. Representación de múltiples figuras.
Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage.
Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Introducción a Python: Elementos básicos del lenguaje
- Profesorado: Patricia Ruano Roca (UGR)
- Duración: 20 horas presenciales
- Fechas y horario: 23, 24, 25, 30, 31 de Mayo y 1, 2, 6, 7, 8 de Junio de 16:00 a 18:00 h
- Lugar: Aula Juan Campos de la Facultad de Ciencias (Presencial)
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas/edición. Dirigido preferentemente a alumnos/as de primer año de doctorado.
- Inscripción: Del 28 de abril al 10 de mayo mediante este FORMULARIO.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje esté ganando cada vez más popularidad entre científicos e ingenieros.
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Los elementos básicos de un lenguaje de programación
2.- Tipos de variables y su manipulación
3.- Manipulación de listas, tuplas y diccionarios
4.- Flujos condicionales if y recursivos for
5.- Funciones básicas del lenguaje
6.- Creación de funciones propias
7.- Control de código y manejo excepciones
El alumno será capaz de:
1.- Crear scripts en python para resolver problemas
2.- Leer y analizar un programa escrito en Python
3.- Manejar los principales entornos de programación con IPython (Spyder y Jupyter)
4.- Leer y escribir datos en ficheros de texto
5.- Diseñar algoritmos para la resolución secuencial de problemas
6.- Depurar programas y reconocer los principales tipos de errores
- Programa:
Tema 1. Introducción (1h) Introducción a los lenguajes de programación Historia de Python Descarga e instalación de anaconda. La consola de Python. Partes principales del IDE Spyder.
Tema 2. Tipos básicos, variables y expresiones (4h) Tipos de datos en Python. Variables, operadores y expresiones. Instalar, importar y utilizar módulos en Python. Listas, tuplas y diccionarios.
Tema 3. Operadores y funciones (4h) Operador lógico if. Bucles for. Bucles while. Creación y utilización de funciones en Python.
Tema 4. Operación de entrada/salida y optimización de código (3h) Lectura de ficheros de texto. Escritura en archivos de texto. Módulos os y sys. Control de ficheros y directorios. Optimización de código. Tipos de errores principales en Python. Control de código y manejo excepciones.
Scientific writing
A cargo del Centro de Lenguas Modernas
Duración: 30 h
- 20 h instrucción-producción
- 10 h tutorización individual
Fechas
- 1ª edición: 4 - 25 abril 2022
- 2ª edición: 16 - 30 mayo 2022
- 3ª edición: 13 - 29 junio 2022
Horario
- de 9:00 h a 11:00 h
Lugar
- Instrucción-producción: online sobre plataforma Moodle: AulaVirtual CLM
- Tutorización individual: medios electrónicos
Plazo de inscripción
- Curso 1ª edición: 7 - 17 marzo 2022
- Curso 2ª edición: del 25 de abril al 2 de mayo 2022r
- Curso 3ª edición: de 23 a 30 de mayo
Forma de inscripción
A través del formulario accesible en el siguiente:
ENLACE DE INSCRIPCIÓN
Plazas
- 25 plazas por curso
Selección y requisitos
- La selección se realizará atendiendo a los puntos siguientes y por estricto orden de llegada de solicitudes.
- Matrícula en segundo año o superior (quedan excluidos alumnos de primer año).
- El solicitante deberá indicar en el formulario de solicitud si dispone de certificado de un nivel lingüístico en inglés igual o superior a B2. En caso de ser seleccionado, deberá enviar antes de empezar el curso dicho certificado a --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es . En caso de no hacerlo, perderá el puesto.
- Tendrán preferencia los que acrediten B2 o superior. No obstante, en caso de plazas vacantes el CLM llevará a cabo una prueba de nivel por orden de llegada de solicitudes hasta cubrir las plazas.
- No se guardarán plazas en lista de espera para ediciones subsiguientes en el mismo curso académico y en cursos siguientes.
Programa de la actividad
- 1. Introduction.
1.1 English as a lingua franca in the scientific world. 1.2 Types of papers.
- 2. Organization.
2.1 Sections. 2.2 Content. 2.3 Format and Layout. 2.4 Common errors.
- 3. Language.
3.1 Syntax and sentence structure. 3.2 Semantics and terminology. 3.3 Style and punctuation. 3.4 Common errors.
- 4 Strategies.
4.1 Keeping notes, annotations, notekeeping systems. 4.2 Keeping track of references. 4.3 Translation: problems and pitfalls. 4.4 Revising. 4.5 Expectations: Style guides, avoiding plagiarism, bibliography. 4.6 Useful links and tools.
Escritura de textos científicos con LaTeX y control de versiones con Git
- Profesorado: Miguel Burgos Poyatos. Dpto. de Genética. Facultad de Ciencias.
- Duración del curso (horas teóricas/prácticas): 20 horas en modalidad virtual + 20 horas no presenciales/trabajo personal
- Calendario y horario: 7, 9, 11, 14, 16, 18 y 21 de marzo 2022 en clases de 3 horas
- Lugar de impartición: Virtual
- Plazas y perfil (año de matriculación en doctorado):
Se ofertan 20 plazas. Es posible inscribirse durante cualquier año del doctorado. El taller está abierto tanto a doctorandos, tanto a tiempo completo como parcial.
- Necesidad de acreditación de conocimientos previos: No es necesario acreditar conocimientos previos.
- Evaluación:
Los alumnos crean un repositorio Git para el curso en http://bitbucket.org donde trabajan durante todo el taller y lo comparten con el profesor que, de esta forma puede seguir todo el trabajo que realizan los alumnos tanto durante las horas presenciales como en las no presenciales. Además, un Foro en la plataforma MOODLE permite la comunicación entre todos los participantes y la resolución de dudas y cuestiones de forma abierta y visible para todos los alumnos. Al final del taller el repositorio deberá contener la presentación de un texto científico que incluya bibliografía y diversos tipos de índices así como el historial de cambios de los archivos generados y situados bajo el control de Git. Siendo evaluado por el profesor responsable de la actividad.
- Inscripción:
La inscripción se realizará a través del siguiente ENLACE (se activará al inicio del plazo de inscripción)
- Plazo de solicitud: Del 14 al 20 de febrero de 2022
Para inscribirse hay que registrarse como usuario de la plataforma tras picar sobre el enlace del curso. Esto puede hacerse en cualquier momento aunque no esté abierto el plazo de matrícula. Cuando se abra, al picar sobre el curso se tendrá la posibilidad de inscribirse hasta que se complete el número de inscripciones.
- Justificación académica:
El taller está directamente enfocado a la escritura de la Tesis Doctoral. Los alumnos aprenden a utilizar el sistema de composición de textos LaTeX para escribir textos científicos, manejo automático de la bibliografía, y generar documentos en distintos formatos a partir del código fuente. Asimismo aprenden a utilizar el sistema de control de versiones Git, que resulta de especial interés para la administración de trabajo colaborativo, como la redacción conjunta de artículos de investigación o las correcciones de la memoria de la Tesis doctoral por parte de sus directores, por lo que es recomendable que tanto alumnos como sus directores asistan conjuntamente a este taller.
LaTeX Avanzado
Curso 2021/2022
Hay vida después de Word y PowerPoint!. Este curso está orientado al uso avanzado de LaTeX (software libre), para el maquetado de alta calidad de documentos técnicos y científicos. Se profundizará en la elaboración de material gráfico de interés en diferentes áreas de la Ciencia, Tecnología, e Ingeniería. Está especialmente orientado a alumnos de Doctorado y Master que necesitan publicar artículos, informes técnicos, proyectos, Tesis o Libros.
- Modo de solicitud: del 1 al 23 de marzo 2022 a través del siguiente enlace: LaTeX Avanzado: Aplicación en Ciencias, Tecnologías e Ingenierías
- Fechas y horario: 4 a 8, 19 a 22 de abril y lunes 25 de Abril 2022 de 10-12hrs.
- Plazas: 20.
- Lugar: 4 a 8, 21, 22 y 25 de abril en aula O09 Facultad de Ciencias, 19 y 20 abril en el aula O06 Facultad de Ciencias
- Motivación:
El curso surge para dotar al alumnado de doctorado y máster de unas herramientas informáticas apropiadas para aumentar su productividad científica. Tiene como objetivo facilitar el proceso de elaboración de los resultados de investigación, haciendo hincapié en la generación de material gráfico. LaTeX es la herramienta ideal, pero debido a la gran cantidad de opciones disponibles, puede parecer difícil de dominar. Este curso tiene como principal objetivo guiar al alumnado de una manera sencilla y gradual para que se conviertan en usuario avanzado de LaTeX.
- Requisitos previos:
Conocimientos básicos de LaTeX. Que preferentemente deberían incluir: instalación, compilación, visor/editor de documentos. Se recomienda saber elaborar un documento básico, y conocer funcionalidades elementales como: tablas, bloques, comandos básicos, etc.
- Perfil:
El curso está dirigido a estudiantes de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías (EDCTI)
- Contenidos:
- Módulo 1: Maquetación de textos en LaTeX y Beamer para presentaciones.
- Módulo 2: Gráficos Vectoriales y uso de paquetes CTAN en LaTeX Ciencias, Tecnologías e Ingenierías.
- Módulo 3: Herramientas avanzadas en plantillas de LaTeX
- Duración:
20 hrs lectivas presenciales (teórico prácticas), y 32 hrs de trabajo del alumno (2 créditos ECTS). Clases de 2 hrs/diarias. Horario de mañana durante 2 semanas.
- Profesorado responsable:
- Jose A. Dobado Catedrático de Univ.). Dpto. Química Orgánica. Fac. de Ciencias.
- Isaac Vidal Daza (Escala Técnica Informática). Apoyo a la Docencia. CSIRC
- Evaluación:
La superación del curso requerirá:
- Asistencia de al menos 70 % de las sesiones (50 % puntuación).
- Elaboración de un documento maquetado con LaTeX (25 % puntuación).
- Defensa oral con Beamer del trabajo realizado. (25 % puntuación).
- Objetivos de Aprendizaje:
- Adquirir un nivel avanzado en la maquetación de textos científicos.
- Desarrollo de destrezas informáticas orientadas a la mejora de la productividad en el desarrollo de las tareas investigadoras.
- Programa:
MÓDULO 1: Uso Avanzado de LaTeX para maquetación de textos y Beamer para presentaciones (8 hrs)
Día 1: LaTeX avanzado (2 hrs)
- diseño de tablas, trabajo con imágenes y creación de gráficos
- ecuaciones y fórmulas
- funcionalidades avanzadas en LaTeX
Día 2: Generación de presentaciones con Beamer (2 hrs)
- uso de temas y apariencia, organización de contenido
- creación de diapositivas, ventanas, bloques y entornos
- plantillas de presentaciones y contenido dinámico
Día 3: Bases de datos con Biber y BibTeX (2 hrs)
- estilos bibliográficos, personalización
- bases de datos bibliográficas
- uso de internas/externas/varias
Día 4: Uso de plantillas con LaTeX para el maquetado de los resultados de la investigación (2 hrs)
- Plantillas de artículos científicos (ACS, RSC, Wiley, Elsevier, etc.)
MÓDULO 2: Gráficos vectoriales y uso de paquetes de LaTeX en Ciencias, Tecnologías e Ingeniería (6 hrs)
Día 5: PGF/TikZ (2 hrs)
- elementos básicos, líneas, caminos, sombreado, formas, colores
- otros comandos: nodos, variables, contadores, ciclos, recorte, alcance
- uso de librerías y ejemplos de dibujos
Días 6-7: Paquetes CTAN de CIENCIAS, TECNOLOGÍAS E INGENIERÍAS (4 hrs)
- dibujo de fórmulas química, reacciones y moléculas.
- gráficas de alineado de nucleótidos, péptidos, etc
- dibujo de circuitos eléctricos.
- escritura de algoritmos, códigos y diagramas de flujo
- dibujo de diagramas en ingeniería civil y de una planta química
MÓDULO 3: Herramientas avanzadas en plantillas de LaTeX y presentación de trabajos (6 hrs)
Días 8-9: Maquetación avanzada en LaTeX (4 hrs)
- Tesis Doctorales
- técnicas avanzadas de índices y glosarios
Día 10: Presentación de trabajos (2 hrs)
- mini-exposiciones de trabajos orales y escritos
- discusión de resultados
- Contacto:
Jose A. Dobado Facultad de ciencias
http://www.ugr.es/local/dobado
dobado@ugr.es
Inteligencia Artificial en 360º
- Descripción breve
Es notorio que la Inteligencia Artificial (I.A.) permea todas las áreas de conocimiento y puede tener un impacto relevante en cuestiones sociales y económicas. Sin embargo, también es notorio que en muchos casos no se tiene conocimiento riguroso de sus potencialidades y limitaciones, entendiéndose más como un arcano con nombre bonito que como una disciplina científica bien asentada, que puede proporcionar soluciones a problemas para los que no las hay en todos los ámbitos del saber, y muy particularmente para muchas de las líneas de investigación más avanzadas (en las que se inscriben las tesis doctorales).
De cara a abrir ventanas de oportunidad para la investigación a partir de técnicas y modelos basados en I.A., es fundamental que los doctorandos conozcan de qué hablamos cuando hablamos de esa materia, cuáles son sus limitaciones y cuales sus perspectivas a corto plazo, desde un punto de vista científico, solido y riguroso.
En esta actividad de carácter esencialmente transversal y de máximo rigor científico, se plantea como objetivo principal clarificar las cuestiones básicas asociadas con la I.A., desterrar algunos de los mitos más usuales y proveer una explicación clara y sencilla de las principales técnicas que permiten la construcción de sistemas basados en IA.
- Ponentes
- David A. Pelta Mochcovsky. Dpto de Ciencias de la Computación e Inteligencia Artificial. ETSI Informática y de Telecomunicación
- Carlos Cruz Corona. Dpto de Ciencias de la Computación e Inteligencia Artificial. ETSI Informática y de Telecomunicación
- José Luis Verdegay Galdeano. Dpto de Ciencias de la Computación e Inteligencia Artificial. ETSI Informática y de Telecomunicación
- Perfil
Dirigido a estudiantes de doctorado de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías (EDCTI). En caso de sobrar plazas podrán ofrecerse a doctorandos de las Escuelas de Ciencias de la Salud (EDCS) y Humanidades, Ciencias Sociales y Jurídicas (EDHCSJ) que lo hayan solicitado.
- Contenidos
- Un recorrido histórico por la IA.
- Representación del conocimiento.
- “Machine Learning”.
- Métodos de Búsqueda y Optimización.
- Procesamiento del lenguaje natural.
- Técnica de Recuperación de la Información.
- Procesamiento de Imágenes y Video.
- Robótica e IA.
- Plazo de solicitud: 20 diciembre 2021 a 13 enero 2022
- Forma de solicitud: a través de este FORMULARIO
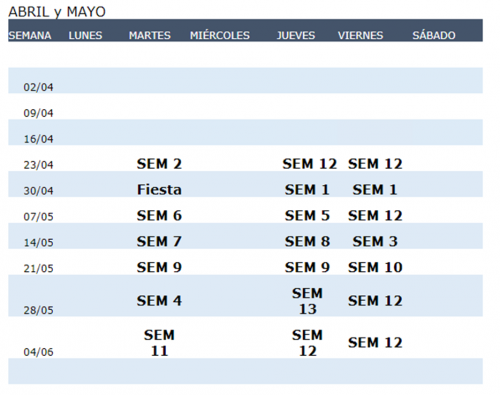
- Sesiones: Lunes 31/1, Jueves 3/2, Lunes 7/2, Jueves 10/2
Horario: 16:00 a 20:00hs
Seminario de Aplicaciones de IA en fecha por confirmar
- Nº de plazas: 30
- Lugar (pendiente de confirmación): Escuela Técnica Superior de Ing. Informática y de Telecomunicación
El curso tendrá modalidad presencial. Los participantes que superen la evaluación, obtendrán un diploma de aprovechamiento del curso. Aquellos participantes que no la superen, obtendrán un diploma de asistencia.
A los solicitantes que no obtengan una plaza, se les ofrecerá la posibilidad de asistir como oyentes mediante conexión en streaming
- Evaluación:
La superación del curso requerirá:
1) la asistencia a (al menos) el 70% de las sesiones.
2) Realización de un informe bibliográfico.
Se podrá plantear de acuerdo a las dos vías siguientes:
a) Dado un problema de interés provisto por el/la estudiante, el informe recogerá que técnicas de IA se han aplicado para su resolución.
b) Dada una técnica de interés para el/la estudiante (por ej. técnicas de aprendizaje), el informe recogerá que problemas de su área se han resuelto con dicha técnica.
Los responsables del curso estarán abiertos a otras propuestas de trabajo.
Técnicas estadísticas básicas aplicadas en Ciencias Experimentales: fundamentos, interpretación e implementación en R
Curso 2021/2022
- Modalidad: presencial
- Lugar: Aula Inf O04, zona de Matemáticas de la Facultad de Ciencias
- Plazas: 25
- Duración: 20 horas
- Periodo de impartición: 20 a 27 enero 2022
- Perfil del estudiante:
20 y 21 de enero: De 9 a 13 horas
24 a 27 de enero: De 9 a 12 horas
- Plazo de solicitud: Del 15 de diciembre 2021 a 10 enero 2022 a través del siguiente formulario:
ENLACE DE INSCRIPCIÓN
2ª EDICIÓN
- Fechas previstas para la actividad: 28 y 29 y 3 a 6 de mayo 2022
28 Y 29 de abril: De 9 a 13 horas
3 a 6 de mayo: De 9 a 12 horas
- Lugar de celebración:
28 de abril de 9 a 13 horas (Aula A20. Facultad de Ciencias)
29 de abril de 9 a 13 horas (Aula O04. Facultad de Ciencias)
3 y 4 de mayo de 9 a 12 horas (Aula O04. Facultad de Ciencias)
5 de mayo de 9 a 12 horas (Aula A20. Facultad de Ciencias)
6 de mayo de 9 a 12 horas (Aula O04. Facultad de Ciencias)
- Justificación académica del curso:
Es incuestionable la importancia que en las últimas décadas ha experimentado la aplicación de numerosas técnicas probabilístico-estadísticas en múltiples campos de aplicación. La razón última de ello viene motivada por la necesidad de describir y explicar la evolución de fenómenos, no sólo desde un punto de vista cualitativo sino cuantitativo, a la vez que se hace imprescindible en múltiples ocasiones poder inferir comportamientos futuros de los sistemas que son objeto de estudio.
El objetivo del curso es presentar una panorámica general, sobre todo desde el punto de vista de la aplicación de las técnicas presentadas en múltiples campos. En ese sentido, la idea principal de esta actividad es ilustrar a los alumnos sobre técnicas y métodos estadísticos mostrando una visión general de sus fundamentos así como una perspectiva de aplicaciones en diversos campos. Se hará especial hincapié sobre los fundamentos, condiciones de aplicabilidad e interpretación de resultados que ayuden a una mejor descripción de los fenómenos estudiados por los alumnos en el desarrollo de sus investigaciones. Otro de los objetivos del curso es el de mostrar la implementación de estas técnicas mediante R, introduciendo al alumno en el empleo de uno de los programas que mayor difusión ha adquirido en los últimos años.
- Programa:
1. Principios generales de inferencia. Modelos básicos: Problema de una muestra. Problema de dos muestras independientes y apareadas. Contrastes paramétricos y no paramétricos para una y dos muestras. M. Mar Rueda. 4 horas. 20 de enero.
2. Análisis de datos categóricos: Independencia y asociación en tablas bidimensionales. Independencia condicional y asociación parcial. Metodología de Mantel-Hanzel. Ana Aguilera. 4 horas. 21 de enero.
3. Modelos de regresión: Fco. De Asis Torres. 6 horas. 24 y 25 de enero.
a. Regresión lineal simple y múltiple.
b. Regresión logística binomial y multinomial. Regresión de Poisson. Regresión de Cox.
4. Técnicas de Análisis Multivariante: Modelo Lineal Multivariante: modelo de Regresión lineal múltiple multivariante y técnicas tipo MANOVA. Técnicas de reducción de dimensiones. Técnicas de clasificación automática. Beatriz Cobo. 6 horas. 26 y 27 de enero.
- Actividades paralelas:
Se propondrá a los alumnos la realización de ejemplos de aplicación para la realización de prácticas individualizadas y tutorizadas de forma personalizada. De forma alternativa, esas prácticas podrían consistir en el asesoramiento estadístico sobre problemas concretos relacionados con el desarrollo de su tesis doctoral. Esta parte constituirá la evaluación final que determinará el grado de aprovechamiento del curso. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado.
- Ponentes:
Dra. María del Mar Rueda García.
Dra. Ana María Aguilera del Pino.
Dra. Beatriz Cobo Rodríguez.
Dr. Francisco de Asís Torres Ruiz.
Multivariate Exploratory Data Analysis (MEDA): Understanding by looking at data(21-22)
- Date: 9-13 May 2022
- Participants: 30
- Deadline for application: 7-25 April 2022
- How to apply: Use this APLICATION FORM.
- NOTES
- The course will be held presentially. Prof. Bro will intervene by virtual connection
- The course will be held in English.
It is necessary to have at least a B1 level (preferably B2 or higher). You can indicate in the “Observations” section your level of English and, if it is the case, if you have a certificate. / Este curso se impartirá íntegramente en inglés. Es necesario contar como mínimo con un nivel B1 (preferentemente B2 o superior). Pude indicar en el apartado “Observaciones” su conocimientos de inglés y en su caso si dispone de certificado para acreditarlo.
- It is requiered basic knowledge of MatLab. Those students who can provide certification of that knowledge will have preference in admission.
- Course Goal
Do you have complicate data? Difficult to understand? With thousands of variables/observations? Or with too little observations? Missing data? Time series? Multiple sources? Big Data?
The course goal is to introduce the students to very powerful data visualization techniques to look into your data set. There is a bunch of Machine Learning (ML) methods that can do difficult tasks (like classification, modelling and prediction) using a black-box approach over data, deep learning being a popular example. This course shows a totally different approach to handling data, using ML only as an instrument (as a means) to understand your data. MEDA will show you how to look into your data set, regardless its complexity, so that you can find groups of individuals and classify them, understand relationships among measured quantities, detect anomalies, find parsimonious models, etc.
The course is led by Professor Rasmus Bro, world leading professor on data analysis in biological and food sciences, and his collaborator at the UGR Dr. José Camacho, specialist on data analysis in Big Data and Exploratory Data Analysis.
- Teaching hours: 30
- Teachers:
Professor Bro is a prominent figure in the field of data analysis and in particular in multivariate analysis. During the last two decades, Prof. Bro has been a principal actor in the development of multivariate analysis in chemical and biological applications in the chemometrics area, in which according to google scholar is the second top researcher. His vast research work is outstanding, presenting an H index equal to 78. Prof. Bro is the author of the most referenced tutorial of PARAFAC (2843 citations), the developer of an extensively used multi-way version of Partial Least Squares (N-PLS) and co-author of more than 200 publications mainly related to the use of multi-way analysis in real life applications. His contributions to the use of constrained modelling are also very relevant, including the use of sparse methodologies for data analysis, and he has co-authored relevant articles to the problem of data fusion, a main challenge in Big Data analyses. The international influence in the community of his course “Multi-way Analysis” and his monograph “Multi-way Analysis: applications in the chemical sciences” is widely recognized. Prof. Bro has taught courses on data analysis in dozens of public and private organizations around the world. From 2001, he is the head of ODIN, an industrial research consortium offering courses, workshops, international contacts and student collaboration.
José Camacho is full professor in the Department of Signal Theory, Networking and Communications and researcher in the Information and Communication Technologies Research Centre, CITIC for its initials in Spanish, both at the University of Granada, Spain. His research interests include exploratory data analysis, anomaly detection and optimization with multivariate techniques applied to data of very different nature, including personalized medicine and communication networks. He is especially interested in the use of exploratory data analysis to Big Data.
- Examination:
Every person analyze their own data under supervision of the teacher and writes a report. The report must be short and concise. A short description of the data and their background must be provided. A short description of aim of the present work must be provided. This aim is not necessarily the overall aim of the project from which the data stem (although this is of course nice). Rather the purpose should be chosen in order to test and evaluate the students’ ability to use the methods taught at the course. It is important to discuss in detail how the models have been critically used for the stated purposes.
- Schedule: ONLINE
Day 1: PCA (Prof. Bro & Dr. Camacho)
| 8:30-9:30 | Welcome (Bro & Camacho) |
| 9:30-10:00 | Introduction and algebra without tears |
| 10:00-11:15 | Principal Component Analysis – PCA |
| 11:15-11:30 | Break |
| 11:30-12:00 | Software introduction (demos/hands-on) |
| 12:00-12:30 | Exercises – PCA |
| 12:30-13:30 | Validation, outliers – PCA |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises – PCA |
Day 2: PLS (Prof. Bro)
| 9:00-9:15 | PCA summary |
| 9:15-10:30 | Multivariate calibration - PLS |
| 10:30-10:45 | Break |
| 10:45-11:30 | Exercises – Multivariate calibration |
| 11:30-13:00 | Validation and outliers incl. exercises |
| 13:00-15:00 | Lunch |
| 15:00-16:00 | Preprocessing and nice to know |
| 16:00-16:15 | Break |
| 16:15-18:00 | Competition! |
Day 3: MEDA Toolbox (Dr. Camacho)
| 9:00-10:00 | Introduction to the MEDA Toolbox |
| 10:00-11:15 | Using the command line interface |
| 11:15-11:30 | Break |
| 11:30-12:30 | Advanced Exploratory Data Analysis |
| 12:30-13:30 | Exercises & Examples |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 4: Big Data (Dr. Camacho)
| 9:00-11:00 | Extensions to Big Data: Big Observations |
| 11:00-11:30 | Break |
| 11:30-12:30 | Exercises |
| 12:30-13:30 | Extensions to Big Data: Big Variables |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 5: Playing with your data I (Prof. Bro & Dr. Camacho)
Time will be devoted to analyze your own data under the supervision of the course monitors, who will guide you through different analysis techniques to pursue your goals.
| 9:00-14:00 | Playing with your data |
Curso de Tecnología del vacío y sus aplicaciones. Espectrometría de masas cuadrupolar y Análisis de gases
Curso destinado a estudiantes de doctorado y master, usuarios y responsables de mantenimiento de sistemas de alto y ultra alto vacío: XPS, STM, sistemas de análisis de gases acoplados a termobalanzas, equipos de quimisorción.
- Programa
Día 1. Tecnología del vacío. (3,5 h aula)
1) Descripción aplicaciones en procesos industriales: envasado de alimentos, aeronáutica y aeroespacial, energía fotovoltaica y termosolar, crecimiento de capas finas: metalización faros coches, espejos telescopios, vidrios arquitectónicos.
2) Descripción aplicaciones en investigación: nanotecnología y aceleradores de partículas.
3) Actividades StartUp
Dia 2. Espectrometría de masas cuadrupolar (2,5 h aula / 1 h visita CIC)
1) Espectros de gases residuales en cámara de alto y ultra alto vacío.
2) Sistemas análisis de gases- Descripción aplicaciones.
3) Generación hidrógeno verde.
- Duración: 7 horas.
- Tipo de docencia: Presencial. Facultad de Ciencias - Aula A20. Visita al Centro de Instrumentación Científica.
- Profesor: César Atienza. Experto en Tecnología del vacío y desarrollo de sistemas especiales. Ha impartido cursos y seminarios de Tecnología de Vacío, espectrometría de masas cuadrupolar y sistemas de análisis de gases en diversas universidades españolas y centros de investigación.
- Fechas: 30 y 31 de mayo 2022 de 9:30 a 13 h.
- Forma y plazo de inscripción: del 25 de abril al 9 de mayo a través del siguiente FORMULARIO
Plazo de solicitud AMPLIADO hasta 16 de mayo 2022
- Evaluación: No se contemplan exámenes. En su lugar se puede proporcionar un certificado de participación si se ha asistido al menos al 80 % del curso.
Creatividad, integridad y comunicación en ciencia
- Profesorado: Isabel Reche Cañabate y Francisco Perfectti Álvarez, Departamentos de Ecología y Genética, Facultad de Ciencias.
- Duración: 30 horas lectivas presenciales y 10 horas de trabajo no presencial y tutoría grupal (presencial).
- Fechas y horario: Miércoles, jueves y viernes de 9 a 12h. los días 12, 13, 14, 19, 20, 21, 26, 27, 28 y 31 de enero de 2022
- Lugar: Sala de Medios Audio-Visuales (Facultad de Ciencias)
- Plazas: 25 plazas.
- Perfil : El curso está dirigido a estudiantes de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías (EDCTI). Se dará preferencia a estudiantes que estén cursando el primer año de doctorado, pero también está abierto a estudiantes de otros años en caso de plazas vacantes. No es necesario acreditar conocimientos previos.
- Plazo de inscripción: del 9 al 22 de diciembre de 2022
- Forma de inscripción: a través del siguiente FORMULARIO
- Justificación académica: Este curso pretende potenciar la creatividad y analizar el proceso de generación de nuevo conocimiento entre los estudiantes de doctorado. Los estudiantes han sido particularmente entrenados en el pensamiento lógico y racional, prestando poca atención al proceso de generación de ideas novedosas. La ciencia se caracteriza por aportar conocimiento contrastable, es decir riguroso y repetible. Crear ciencia exige, por lo tanto, aunar creatividad con rigor metodológico, puesto que para producir nuevo conocimiento científico es necesario plantear hipótesis falsables y preguntas precisas, aplicando la metodología más adecuada con rigor e integridad. Finalmente, además de los desafíos intelectuales inherentes al proceso de crear nuevo conocimiento, éste ha de ser transferido a otros científicos y finalmente a la sociedad. Por lo tanto, este curso se cimienta sobre tres pilares que consideramos esenciales en la generación de conocimiento: Creatividad, Rigor y Comunicación.
- Objetivos educativos: El alumno aprenderá/comprenderá diferentes técnicas para fomentar la creatividad, la estructura social del sistema ciencia-tecnología, las fortalezas y debilidades del método científico, las buenas prácticas de laboratorio, las normas de publicación y la forma de reconocer los posibles conflictos de interés y las técnicas para hacer presentaciones efectivas dependiendo del foro de destino.
El alumno será capaz de: desarrollar su pensamiento crítico y creativo, reconocer conflictos de interés y desarrollar soluciones, mantener un correcto cuaderno de laboratorio, estructurar adecuadamente el contenido de un manuscrito en función de la revista de destino y preparar presentaciones efectivas.
- Programa:
Tema 1: La transición de estudiante a científico/a. Reflexiones sobre el sistema educativo. Elección de un problema científico relevante. La frontera del conocimiento. El sistema académico y científico español.
Tema 2: Creatividad y potencial creativo individual. Curiosidad y Generación de Ideas. Pensamiento creativo: Intuición, entrenamiento y placer. El proceso del descubrimiento.
Tema 3: Estrategias para fomentar la creatividad. Mentalidad de crecimiento, el pensamiento divergente, lateral y asociativo. Serendipia y oportunidad. Los errores como motor de aprendizaje.
Tema 4: Creatividad colectiva. Tormenta de ideas. Inteligencia colectiva como una propiedad emergente en grupos de investigación. Papel de la diversidad y estructura del grupo en la creatividad colectiva.
Tema 5: El método científico y la inferencia fuerte. El método hipotético-deductivo y el método inductivo en la era del bigdata. Generación de múltiples hipótesis y cómo refutar o confirmar las mismas.
Tema 6: Conducta responsable en ciencia. Origen de las buenas prácticas de laboratorio (GLP) y los sistemas de control de calidad. Integridad, plagio y fabricación. Análisis de casos. Ética en los científicos.
Tema 7: Ciencia patológica y pseudociencia. Autoengaño e interpretación ilusoria o errónea de los datos. Casos de estudio: Lysenko y el declive de la genética en la unión soviética. Pseudociencias y responsabilidad social de la ciencia.
Tema 8: La comunicación entre científicos 1. El poster y la comunicación oral. Recursos gráficos y calidad de las figuras. Técnicas de amplificación de la señal frente al ruido. Enfrentándonos al miedo escénico.
Tema 9: La comunicación entre científicos 2. El artículo científico. Importancia del título, el resumen, la calidad de las figuras y la legibilidad del texto. El párrafo como unidad de escritura. Cómo seleccionar la revista adecuada para mi investigación. Importancia de la “cover letter”. Proceso de revisión por pares y cómo aprender del rechazo. Redactar respuestas a los revisores
Curso en línea de resonancia magnética nuclear, GERMN (12 h)
Curso destinado a alumnos de doctorado con un enfoque práctico hacia la interpretación de espectros 1D y 2D.
- Programa:
Tema I. Origen de la señal de RMN y núcleos activos en RMN. Desplazamiento químico. Integración. Factores que afectan al desplazamiento químico: efectos inductivos, mesómeros, cargas netas, anisotropía, campos eléctricos, van der Waals, enlaces de hidrógeno, efecto isotópico, efecto del medio. 2 h.
Tema II. El acoplamiento escalar. Espectros de primer orden: notación, tipos de acoplamientos (nJ, n ≥ 2), efecto tejado, árboles de desdoblamiento. Equivalencia química y equivalencia magnética. Relaciones entre estructura y magnitud relativa de los acoplamientos nJHH. Acoplamientos heteronucleares. Desacoplamiento homo y heteronuclear. Acoplamientos de orden superior a 1. 3 h.
Tema III. Concepto de relajación y factores de los que depende. Relación entre tiempos de relajación y estructura. El efecto Overhauser nuclear. Relación entre NOE y estructura. 1 h.
Tema IV. RMN dinámica: escalas de tiempo en RMN, efectos en el desplazamiento químico y en las constantes de acoplamiento. 1 h.
Tema V. RMN-13C{1H}: medida de espectros (efecto del desacoplamientos de 1H). Desplazamiento químico. Factores que afectan al desplazamiento químico. Edición de espectros. 2 h.
Tema VI. Introducción a la RMN bidimensional. Tipos de espectros y ejemplo de aplicación (resolución de problema estructural analizando COSY, HSQC y NOESY, sin otros concimientos previos). 1 h.
Tema VII. Espectros COSY, COSYDQF, TOCSY (incluido TOCSY selectivo), HSQC, HMQC, HMBC, NOESY, HOESY. 2 h.
- Objetivos. Al finalizar el curso el alumno deberá saber: Las estrategias de asignación estructural mediante la medida de espectros de RMN de alta resolución. La obtención de información estructural derivada de los efectos de relajación y de los procesos dinámicos que afecten a la molécula problema.
- Tipo de docencia. En línea, mediante la plataforma virtual Blackboard.
- Profesor. Fernando López Ortiz, Universidad de Almería
- Con la colaboración de: Real Sociedad Española de Química (grupo especializado en resonancia magnética nuclear)
- Fechas. 14 de octubre a 4 de noviembre, lunes y jueves de 9 a 11 h.
- Forma y plazo de inscripción: del 15 de septiembre al 1 de octubre de 2021 a través del siguiente FORMULARIO
- Planificación:
| Jueves 14 | Lunes 18 | Jueves 21 | Lunes 25 | Jueves 28 | Jueves 04 |
|---|---|---|---|---|---|
| Tema I/2 h | Tema II/2 h | Tema II/1 h | Tema IV/1 h | Tema V/1 h | Tema VII/2 h |
| Tema III/1 h | Tema V/1 h | Tema VI/ 1 h |
- Evaluación. No se contemplan exámenes. En su lugar se puede proporcionar un certificado de participación si se ha asistido al menos al 80 % del curso.
Herramientas de búsqueda y gestión de información para el desarrollo de la Investigación
- Profesores/as que la imparten: Anne-Vinciane Doucet, Antonio Fernández Porcel, Mª Ángeles García Gil, Esteban López García y Daniel Marín Conesa
- Duración: 10-13 horas
- Fechas de realización: 1 al 3 de marzo de 2022
- Plazo de solicitud: del 7 al 13 de febrero de 2022
- Forma de inscripción: mediante el siguiente formulario ENLACE DE INSCRIPCIÓN
- Lugar de realización: Aula B3 del Aulario de Posgrado (Ubicación Avenida de Madrid)
- Horario: de 10:00 a 13:00
- Perfil: Dirigido a alumnos/as de primer año
- Nº Alumnos: 40
- Programa de la actividad:
El curso consta de tres módulos:
1. Perfil de investigador:- El perfil de investigador. Utilidad y necesidad.
- Necesidad de normalización del nombre de investigador.
-Números de identificación: ORCID, ResearcherID (WoS), Author ID (Scopus).
-Perfil y difusión de la investigación: ventajas y “herramientas”: UGR-Investiga, Google Scholar, Academia.edu, ResearchGate. Dialnet.
-El perfil de investigador y la evaluación de la producción científica. ANECA, DEVA y SICA. El CVN.
2. Bases de datos:- Bases de datos en: Ciencias, Tecnologías e Ingenierías y Ciencias de la Salud: JCR-Science, JCR-Social Science, WOS, SCOPUS, Digibug: Repositorio Institucional de la Universidad de Granada, SPI, TESEO
3. Gestores bibliográficos:- Introducción a los gestores bibliográficos
- Gestores bibliográficos: Mendeley, Flow, Endnote
Curso 2020/2021
EDCTI LECTURE SERIES: Communication Technologies for IoT
- Actividad aplazada
- Dr Klaus Mößner. University of Technology Chemnitz & University of Surrey.
- Sala de Conferencias - CITIC-UGR ( localization ).
- Abstract. The talk will look into the communication aspects of IoT deployments, it will discuss the various technologies, the need and levels on which interoperability may be needed and is implemented and will look into how to make sure that there is enough capacity to connect all those sensors and actuators that are at the core of IoT deployments. The session will include communication technologies for IoT from narrow to wideband, and ad hoc to cellular.
- Dr Klaus Mößner is Professor for Communications Engineering at the University of Technology Chemnitz, and also Professor in Cognitive Networks at the Institute for Communication Systems and the 5G Innovation Centre, at the University of Surrey. Klaus was involved in more than 25 projects in the Cognitive Communications, Service provision and IoT areas. He was responsible for the work on cognitive decision-making mechanisms in the CR project ORACLE, led the work on radio awareness in the ICT FP7 project QoSMOS, and led the Speed5G, iKaaS, IoT.est, and SocIoTal projects. Klaus was the founding chair of the IEEE DYSPAN Working Group (WG6) on Sensing Interfaces for future and cognitive communication systems. His research interests include cognitive networks, IoT deployments and sensor data-based knowledge generation, as well as reconfiguration and resource management; he is senior member of the IEEE. At current he does lead the EU-Taiwan project Clear5G investigating the extensions 5G systems need to serve the particular requirements of the Factories of the Future. Klaus is leading a research group investigating algorithms and mechanisms to gain knowledge and understanding of situations in and around autonomous vehicles.
- La inscripción es gratuita (pero necesaria para prever cambios de sala si hay un gran número de solicitudes), a través del siguiente enlace: http://sl.ugr.es/CommunicationTechnologiesForIoT
- Se emitirá un certificado de asistencia para los estudiantes de cualquier programa de doctorado de la UGR que asistan al evento.
Taller de escritura de textos científicos con LaTeX y control de versiones con Git
- Profesorado: Miguel Burgos Poyatos. Dpto. de Genética. Facultad de Ciencias.
- Duración del curso (horas teóricas/prácticas): 20 horas en modalidad virtual + 20 horas no presenciales/trabajo personal
- Calendario y horario: 15, 17, 19, 22, 24, 26 de marzo 2021 de 11:00 a 14:00 y 29 de marzo de 12:00 a 14:00.
- Lugar de impartición: Virtual
- Plazas y perfil (año de matriculación en doctorado):
Se ofertan 20 plazas. Es posible inscribirse durante cualquier año del doctorado. El taller está abierto tanto a doctorandos, tanto a tiempo completo como parcial.
- Necesidad de acreditación de conocimientos previos: No es necesario acreditar conocimientos previos.
- Evaluación:
Los alumnos crean un repositorio Git para el curso en http://bitbucket.org donde trabajan durante todo el taller y lo comparten con el profesor que, de esta forma puede seguir todo el trabajo que realizan los alumnos tanto durante las horas presenciales como en las no presenciales. Además, un Foro en la plataforma MOODLE permite la comunicación entre todos los participantes y la resolución de dudas y cuestiones de forma abierta y visible para todos los alumnos. Al final del taller el repositorio deberá contener la presentación de un texto científico que incluya bibliografía y diversos tipos de índices así como el historial de cambios de los archivos generados y situados bajo el control de Git. Siendo evaluado por el profesor responsable de la actividad.
- Inscripción:
La inscripción se realizará a través del siguiente ENLACE
Clave de matriculación que pedirá la plataforma al inscribirse: texgit2021
Desde el 01/03/2021 hasta completar el límite de plazas.
Para inscribirse hay que registrarse como usuario de la plataforma tras picar sobre el enlace del curso. Esto puede hacerse en cualquier momento aunque no esté abierto el plazo de matrícula. Cuando se abra el 1 de marzo, al picar sobre el curso se tendrá la posibilidad de inscribirse hasta que se complete el número de inscripciones.
- Justificación académica:
El taller está directamente enfocado a la escritura de la Tesis Doctoral. Los alumnos aprenden a utilizar el sistema de composición de textos LaTeX para escribir textos científicos, manejo automático de la bibliografía, y generar documentos en distintos formatos a partir del código fuente. Asimismo aprenden a utilizar el sistema de control de versiones Git, que resulta de especial interés para la administración de trabajo colaborativo, como la redacción conjunta de artículos de investigación o las correcciones de la memoria de la Tesis doctoral por parte de sus directores, por lo que es recomendable que tanto alumnos como sus directores asistan conjuntamente a este taller.
Técnicas estadísticas básicas aplicadas en Ciencias Experimentales: fundamentos, interpretación e implementación en R
Curso 2020/2021
- Modalidad: VIRTUAL
- Plazas: 25
- Duración: 20 horas de asistencia virtual
- Periodo de impartición: 18, 19, 22, 23, 24 y 25 febrero 2021
- Horario:
18 y 19 de febrero: De 9 a 13 horas
22, 23, 24 y 25 de febrero: De 9 a 12
- Plazo de solicitud: Del 22 de enero al 3 de febrero de 2021 a través del formulario accesible siguiente:
ENLACE DE INSCRIPCIÓN
- 2ª edición exclusivamente para suplentes de la primera edición: del 28 de junio a 5 de julio (20 horas en formato virtual).
- Justificación académica del curso:
Es incuestionable la importancia que en las últimas décadas ha experimentado la aplicación de numerosas técnicas probabilístico-estadísticas en múltiples campos de aplicación. La razón última de ello viene motivada por la necesidad de describir y explicar la evolución de fenómenos, no sólo desde un punto de vista cualitativo sino cuantitativo, a la vez que se hace imprescindible en múltiples ocasiones poder inferir comportamientos futuros de los sistemas que son objeto de estudio.
El objetivo del curso es presentar una panorámica general, sobre todo desde el punto de vista de la aplicación de las técnicas presentadas en múltiples campos. En ese sentido, la idea principal de esta actividad es ilustrar a los alumnos sobre técnicas y métodos estadísticos mostrando una visión general de sus fundamentos así como una perspectiva de aplicaciones en diversos campos. Se hará especial hincapié sobre los fundamentos, condiciones de aplicabilidad e interpretación de resultados que ayuden a una mejor descripción de los fenómenos estudiados por los alumnos en el desarrollo de sus investigaciones. Otro de los objetivos del curso es el de mostrar la implementación de estas técnicas mediante R, introduciendo al alumno en el empleo de uno de los programas que mayor difusión ha adquirido en los últimos años.
- Programa:
1. Principios generales de inferencia. Modelos básicos: Problema de una muestra. Problema de dos muestras independientes y apareadas. Contrastes paramétricos y no paramétricos para una y dos muestras. M. Mar Rueda. 4 horas. 18 de febrero.
2. Análisis de datos categóricos: Independencia y asociación en tablas bidimensionales. Independencia condicional y asociación parcial. Metodología de Mantel-Hanzel. Ana Aguilera. 4 horas. 19 de febrero.
3. Modelos de regresión: Fco. De Asis Torres. 6 horas. 22 y 23 de febrero.
a. Regresión lineal simple y múltiple.
b. Regresión logística binomial y multinomial. Regresión de Poisson. Regresión de Cox.
4. Técnicas de Análisis Multivariante: Modelo Lineal Multivariante: modelo de Regresión lineal múltiple multivariante y técnicas tipo MANOVA. Técnicas de reducción de dimensiones. Técnicas de clasificación automática. Beatriz Cobo. 6 horas. 24 y 25 de febrero.
- Actividades paralelas:
Se propondrá a los alumnos la realización de ejemplos de aplicación para la realización de prácticas individualizadas y tutorizadas de forma personalizada. De forma alternativa, esas prácticas podrían consistir en el asesoramiento estadístico sobre problemas concretos relacionados con el desarrollo de su tesis doctoral. Esta parte constituirá la evaluación final que determinará el grado de aprovechamiento del curso. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado.
- Carga docente total imputable: 2.5 créditos
- Ponentes:
Dra. María del Mar Rueda García. Carga docente: 0.5 créditos.
Dra. Ana María Aguilera del Pino. Carga docente: 0.5 créditos.
Dra. Beatriz Cobo Rodríguez. Carga docente: 1 crédito.
Dr. Francisco de Asís Torres Ruiz. Carga docente: 0.5 créditos.
EDCTI LECTURE SERIES: Crónicas de la Tierra
- Ciclo de Conferencias ”Crónicas de la Tierra”
Organizado por la Academia de Ciencias Matemáticas, Físico-Químicas y Naturales de Granada y la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías de la UGR.
Debido a medidas sanitarias, el evento se ofrecerá en línea.
El público deberá silenciar su micrófono al conectarse (desconectar la cámara es opcional). Con posterioridad a cada conferencia se abrirá un turno de preguntas y debate entre el conferenciante y los asistentes.
Por razones de logística, no se ofrecerá certificado de asistencia
- 1.- Martes 29 de Septiembre 2020, 17.00 h. "Auto-organización mineral en la Tierra primitiva"
Por: Juan Manuel García Ruiz. Profesor de Investigación. Instituto Andaluz de Ciencias de la Tierra (CSIC). Académico.
- 2.- Miércoles 30 de Septiembre 2020, 17.00 h. "La ruta del Jade pre-colombino en Mesoamérica-Caribe"
Por: Antonio García Casco. Catedrático de Petrología y Geoquímica de la UGR. Director de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías.
- 3.- Miércoles 4 de Noviembre 2020, 17.00 h. “La desconocida infancia del planeta Tierra”
Por: Fernando Bea Barredo. Catedrático de Petrología y Geoquímica de la UGR. Académico.
- 4.- Jueves 5 de Noviembre 2020 (día por concretar), 17.00 h. "La investigación geológica española en el Sahara Occidental”
Por: Francisco González Lodeiro. Profesor Emérito. Dpto. de Geodinámica de la UGR. Académico.
III Edición. Curso Básico de Análisis de Datos en R (ACTIVIDAD CANCELADA)
- Profesorado:
- Antonio Jesús Muñoz Pajares (Dpto. Genética)
- Ana María Aguilera del Pino (Dpto. Estadística e I.O.)
- José María Conde Porcuna (Dpto. Ecología)
- Juan Lorite Moreno (Dpto. de Botánica)
- Rafael Rubio de Casas (Dpto. Ecología)
- María del Mar Rueda García (Dpto. Estadística e I.O.)
- Francisco de Asís Torres Ruiz (Dpto. Estadística e I.O.)
- Coordinador: José María Conde Porcuna (--LOGIN--34ed1bd877cef421e1bb543eb83410ccugr[dot]es )
- Duración del curso (horas teóricas/prácticas):
36 horas (29 horas de clases teórico-prácticas + 7 horas tutorías)
Horas no presenciales de los estudiantes: 25 horas de estudio/trabajo
- Calendario y horario:
Durante el año 2020 se impartirán las clases presenciales en junio-julio (por determinar en función de la evolución de la situación del coronavirus)
Posteriormente, se llevará a cabo la supervisión del trabajo de los alumnos de forma personalizada. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado según las afinidades previamente establecidas durante el curso.
- Lugar de impartición: Por determinar
- Material necesario: Ordenadores portátiles
- Plazas y perfil (año de matriculación en doctorado): 20 plazas. Es posible inscribirse durante cualquier año del doctorado.
- Necesidad de acreditación de conocimientos previos: No es necesario acreditar conocimientos previos
- Evaluación: Se evaluarán los análisis realizados por los estudiantes durante el periodo de supervisión de trabajos y se podrá valorar la actitud en clase y tutorías.
- Justificación académica:
La obtención de datos de diverso tipo, tanto de manera experimental como observacional, requiere necesariamente unos conocimientos estadísticos suficientes para su adecuado análisis, y así obtener las conclusiones pertinentes. En este curso de doctorado, los alumnos podrán aprender las técnicas más comunes para el análisis de datos y podrán aplicar los conocimientos que adquieran sobre los ficheros de datos que dispongan para la realización de sus Tesis doctorales. Los análisis que hagan con dichos ficheros serán supervisados inicialmente por el profesorado de la asignatura.
- Objetivos educativos, profesionales y competencias generales adquiridas:
El objetivo del curso es que los estudiantes de doctorado conozcan y apliquen los métodos estadísticos más utilizados, fundamentalmente en Biología, para que puedan utilizarlos durante la realización de sus Tesis doctorales. En las clases se utilizarán datos reales como ejemplos para una mejor comprensión.
- El alumno sabrá:
- Construir ficheros para análisis de datos
- Utilizar determinadas herramientas de análisis según su tipo de datos
- Los paquetes de R necesarios para distintos análisis de datos fundamentales
- Los scripts de R necesarios para distintos análisis de datos fundamentales
- Ejecutar distintos análisis estadísticos de datos
- El alumno será capaz de:
- Diseñar estudios experimentales
- Utilizar de forma básica el paquete estadístico R
- Interpretar resultados experimentales y/o observacionales básicos
- Localizar variables/factores relacionadas con nuestras variables de interés
- Elaborar modelos predictivos
- Programa formativo:
Día 1, 9:00-12:00 (JM Conde)
Presentación del curso
Estadística básica.
Diseño experimental. Pseudoreplicación y pseudofactorialismo
Tipos de datos
Día 1, 12:30-14:30 (AJ Muñoz)
Estadística básica
Introducción a R
Correlaciones paramétricas y no paramétricas
Día 2, 9:00-11:00 (MM Rueda)
Inferencia básica
Problema de una muestra.
Problema de dos muestras independientes y apareadas.
Contrastes paramétricos y no paramétricos para una y dos muestras.
Día 2, 11:30-13:30 (F Torres)
Modelos lineales generales: Regresión lineal simple
Ajuste e interpretación de resultados.
Predicción. Calibración lineal.
Contraste de linealidad para datos repetidos.
Comprobación de asunciones
Día 3, 9:00-11:00 (F Torres)
Modelos lineales generales: Regresión lineal múltiple
Ajuste e interpretación de resultados.
Restricciones lineales.
Selección de regresores.
Día 3, 11:30-13:30 (MM Rueda)
Modelos lineales generalizados: variables explicativas cuantitativas
Regresión logística binomial y multinomial. Selección de regresores.
Regresión de Poisson.
Día 4, 9:00-11:00 (AM Aguilera)
Análisis de datos categóricos
Independencia y asociación en tablas bidimensionales.
Día 4, 11:30-13:30 (AM Aguilera)
Análisis de datos categóricos
Independencia condicional y asociación parcial.
Metodología de Mantel-Hanzel
Día 5, 9:00-11:00 (J Lorite)
Diseño de experimentos y análisis de la varianza (ANOVA).
Diseños completamente aleatorizados.
Diseños en bloques. Cuadrados latinos y grecolatinos.
ANOVA paramétrico
Día 5, 11:30-13:30 (J Lorite)
Diseño de experimentos y técnicas Anova asociadas.
ANOVA de medidas repetidas
Diseños anidados
Día 6, 9:00-11:00 (AJ Muñoz)
Contrastes múltiples no paramétricos
Muestras independientes: Análisis de Kruskal-Wallis
Muestras dependientes: Análisis de Friedman y Prueba de Cochran
Día 6, 11:30-13:30 (JM Conde)
Modelos lineales: variables explicativas cuantitativas y cualitativas
ANCOVA
Modelos y selección de modelos: AIC y AICc
Día 7, 9:00-11:00 (R Rubio)
Correlación y regresión de matrices de distancia
¿Qué es una matriz de distancia?
Análisis espacial: Análisis de Mantel simple
Día 7, 11:30-13:30 (R Rubio)
Correlación y regresión de matrices de distancia
Análisis de mantel parcial
Regresión múltiple de matrices (MRM)
Otras actividades: De manera no presencial, los alumnos irán trabajando con ficheros de datos de sus Tesis doctorales (si aún no dispusieran de ellos, se les entregarían ficheros de datos). Durante aproximadamente un mes, se llevará a cabo la supervisión del trabajo de los alumnos de forma personalizada. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado según las afinidades previamente establecidas.
Herramientas de búsqueda y gestión de información para el desarrollo de la Investigación(2020)
- Profesores/as que la imparten: Anne-Vinciane Doucet, Antonio Fernández Porcel, Mª Ángeles García Gil, Esteban López García y Daniel Marín Conesa
- Duración: 10-13 horas
- Fechas de realización: Del 25 al 27 de mayo de 2021
- Plazo de solicitud: 3-9 mayo 2021
- Forma de inscripción: mediante este formulario.
- Lugar de realización: Aula B1 del Aulario de Posgrado (Ubicación Avenida de Madrid)
- Horario: de 10:00 a 13:00
- Perfil: Dirigido a alumnos/as de primer año
- Nº Alumnos: 40
- Programa de la actividad:
El curso consta de tres módulos:
1. Perfil de investigador:- El perfil de investigador. Utilidad y necesidad.
- Necesidad de normalización del nombre de investigador.
-Números de identificación: ORCID, ResearcherID (WoS), Author ID (Scopus).
-Perfil y difusión de la investigación: ventajas y “herramientas”: UGR-Investiga, Google Scholar, Academia.edu, ResearchGate. Dialnet.
-El perfil de investigador y la evaluación de la producción científica. ANECA, DEVA y SICA. El CVN.
2. Bases de datos:- Bases de datos en: Ciencias, Tecnologías e Ingenierías y Ciencias de la Salud: JCR-Science, JCR-Social Science WOS, SCOPUS
- Bases de datos en: Humanidades, Ciencias Sociales y Jurídicas: JCR-Social Science, Arts and Humanities Citation Index, Dialnet
3. Gestores bibliográficos:- Introducción a los gestores bibliográficos
- Gestores bibliográficos: Mendeley, Flow, Endnote
Scientific writing(2020)
A cargo del Centro de Lenguas Modernas
Duración: 30 h
- 20 h instrucción-producción
- 10 h tutorización individual
Fechas
- CURSO 1: Del 12 al 23 de abril, 9.00-11.00 h
- CURSO 2: Del 21 de junio a 2 de julio, 9.00-11.00 h
Lugar
- Instrucción-producción: online sobre plataforma Moodle: AulaVirutal CLM
- Tutorización individual: medios electrónicos
Nota: En función de la evolución de las regulaciones académicas, el curso 2 podría impartirse de forma presencial
Plazo de inscripción
- Curso 1: del 2 al 26 marzo
- Curso 2: del 14 de mayo al 4 de junio
Forma de inscripción
A través del formulario accesible siguiente:
ENLACE DE INSCRIPCIÓN
Plazas
- 25 plazas por curso
Selección y requisitos
- La selección se realizará atendiendo a los puntos siguientes y por estricto orden de llegada de solicitudes.
- Matrícula en segundo año o superior (quedan excluidos alumnos de primer año).
- El solicitante deberá indicar en el formulario de solicitud si dispone de certificado de un nivel lingüístico en inglés igual o superior a B2. En caso de ser seleccionado, deberá enviar antes de empezar el curso dicho certificado a --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es . En caso de no hacerlo, perderá el puesto.
- Tendrán preferencia los que acrediten B2 o superior. No obstante, en caso de plazas vacantes el CLM llevará a cabo una prueba de nivel por orden de llegada de solicitudes hasta cubrir las plazas.
- No se guardarán plazas en lista de espera para ediciones subsiguientes en el mismo curso académico y en cursos siguientes.
Programa de la actividad
- 1. Introduction.
1.1 English as a lingua franca in the scientific world. 1.2 Types of papers.
- 2. Organization.
2.1 Sections. 2.2 Content. 2.3 Format and Layout. 2.4 Common errors.
- 3. Language.
3.1 Syntax and sentence structure. 3.2 Semantics and terminology. 3.3 Style and punctuation. 3.4 Common errors.
- 4 Strategies.
4.1 Keeping notes, annotations, notekeeping systems. 4.2 Keeping track of references. 4.3 Translation: problems and pitfalls. 4.4 Revising. 4.5 Expectations: Style guides, avoiding plagiarism, bibliography. 4.6 Useful links and tools.
Multivariate Exploratory Data Analysis (MEDA): Understanding by looking at data(2020)
- Date: 12-16th July 2021
- Participants: 30
- Deadline for application: 24th May - 14th June 2021
- How to apply: Use this application form.
- NOTES
- Depending on the Covid situation, the course will be held presentailly or virtually.
- The course will be held in English.
It is necessary to have at least a B1 level (preferably B2 or higher). You can indicate in the “Observations” section your level of English and, if it is the case, if you have a certificate. / Este curso se impartirá íntegramente en inglés. Es necesario contar como mínimo con un nivel B1 (preferentemente B2 o superior). Pude indicar en el apartado “Observaciones” su conocimientos de inglés y en su caso si dispone de certificado para acreditarlo.
- It is requiered basic knowledge of MatLab. Those students who can provide certification of that knowledge will have preference in admission.
- Course Goal
Do you have complicate data? Difficult to understand? With thousands of variables/observations? Or with too little observations? Missing data? Time series? Multiple sources? Big Data?
The course goal is to introduce the students to very powerful data visualization techniques to look into your data set. There is a bunch of Machine Learning (ML) methods that can do difficult tasks (like classification, modelling and prediction) using a black-box approach over data, deep learning being a popular example. This course shows a totally different approach to handling data, using ML only as an instrument (as a means) to understand your data. MEDA will show you how to look into your data set, regardless its complexity, so that you can find groups of individuals and classify them, understand relationships among measured quantities, detect anomalies, find parsimonious models, etc.
The course is led by Professor Rasmus Bro, world leading professor on data analysis in biological and food sciences, and his collaborator at the UGR Dr. José Camacho, specialist on data analysis in Big Data and Exploratory Data Analysis.
- Teaching hours: 30
- Teachers:
Professor Bro is a prominent figure in the field of data analysis and in particular in multivariate analysis. During the last two decades, Prof. Bro has been a principal actor in the development of multivariate analysis in chemical and biological applications in the chemometrics area, in which according to google scholar is the second top researcher. His vast research work is outstanding, presenting an H index equal to 65. Prof. Bro is the author of the most referenced tutorial of PARAFAC (1933 citations), the developer of an extensively used multi-way version of Partial Least Squares (N-PLS) and co-author of more than 200 publications mainly related to the use of multi-way analysis in real life applications. His contributions to the use of constrained modelling are also very relevant, including the use of sparse methodologies for data analysis, and he has co-authored relevant articles to the problem of data fusion, a main challenge in Big Data analyses. The international influence in the community of his course “Multi-way Analysis” and his monograph “Multi-way Analysis: applications in the chemical sciences” is widely recognized. Prof. Bro has taught courses on data analysis in dozens of public and private organizations around the world. From 2001, he is the head of ODIN, an industrial research consortium offering courses, workshops, international contacts and student collaboration.
José Camacho is an associate professor in the Department of Signal Theory, Networking and Communications and researcher in the Information and Communication Technologies Research Centre, CITIC for its initials in Spanish, and in the Network Engineering & Security Group (NESG), both at the University of Granada, Spain. His research interests include exploratory data analysis, anomaly detection and optimization with multivariate techniques applied to data of very different nature, including industrial processes, chemometrics and communication networks. He is especially interested in the use of exploratory data analysis to Big Data.
- Examination:
Every person analyze their own data under supervision of the teacher and writes a report. The report must be short and concise. A short description of the data and their background must be provided. A short description of aim of the present work must be provided. This aim is not necessarily the overall aim of the project from which the data stem (although this is of course nice). Rather the purpose should be chosen in order to test and evaluate the students’ ability to use the methods taught at the course. It is important to discuss in detail how the models have been critically used for the stated purposes.
- Schedule: ONLINE
Day 1: PCA (Prof. Bro & Dr. Camacho)
| 8:30-9:30 | Welcome (Bro & Camacho) |
| 9:30-10:00 | Introduction and algebra without tears |
| 10:00-11:15 | Principal Component Analysis – PCA |
| 11:15-11:30 | Break |
| 11:30-12:00 | Software introduction (demos/hands-on) |
| 12:00-12:30 | Exercises – PCA |
| 12:30-13:30 | Validation, outliers – PCA |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises – PCA |
Day 2: PLS (Prof. Bro)
| 9:00-9:15 | PCA summary |
| 9:15-10:30 | Multivariate calibration - PLS |
| 10:30-10:45 | Break |
| 10:45-11:30 | Exercises – Multivariate calibration |
| 11:30-13:00 | Validation and outliers incl. exercises |
| 13:00-15:00 | Lunch |
| 15:00-16:00 | Preprocessing and nice to know |
| 16:00-16:15 | Break |
| 16:15-18:00 | Competition! |
Day 3: MEDA Toolbox (Dr. Camacho)
| 9:00-10:00 | Introduction to the MEDA Toolbox |
| 10:00-11:15 | Using the command line interface |
| 11:15-11:30 | Break |
| 11:30-12:30 | Advanced Exploratory Data Analysis |
| 12:30-13:30 | Exercises & Examples |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 4: Big Data (Dr. Camacho)
| 9:00-11:00 | Extensions to Big Data: Big Observations |
| 11:00-11:30 | Break |
| 11:30-12:30 | Exercises |
| 12:30-13:30 | Extensions to Big Data: Big Variables |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 5: Playing with your data I (Prof. Bro & Dr. Camacho)
Time will be devoted to analyze your own data under the supervision of the course monitors, who will guide you through different analysis techniques to pursue your goals.
| 9:00-14:00 | Playing with your data |
Curso de LaTeX Avanzado
Curso 2020/2021
Hay vida después de Word y PowerPoint!. Este curso está orientado al uso avanzado de LaTeX (software libre), para el maquetado de alta calidad de documentos técnicos y científicos. Se profundizará en la elaboración de material gráfico de interés en diferentes áreas de la Ciencia, Tecnología, e Ingeniería. Está especialmente orientado a alumnos de Doctorado y Master que necesitan publicar artículos, informes técnicos, proyectos, Tesis o Libros.
- Fechas y horario: 10 a 21 de mayo 2021 Lunes - Viernes, 9-11 hrs
- Plazas: 20.
- Lugar: VIRTUAL
- Modo de solicitud: del 12 al 22 de abril a través del formulario disponible en este ENLACE (se activará una vez iniciado el plazo de solicitud):
LaTeX Avanzado: Aplicación en Ciencias, Tecnologías e Ingenierías
- Motivación:
El curso surge para dotar al alumnado de doctorado y máster de unas herramientas informáticas apropiadas para aumentar su productividad científica. Tiene como objetivo facilitar el proceso de elaboración de los resultados de investigación, haciendo hincapié en la generación de material gráfico. LaTeX es la herramienta ideal, pero debido a la gran cantidad de opciones disponibles, puede parecer difícil de dominar. Este curso tiene como principal objetivo guiar al alumnado de una manera sencilla y gradual para que se conviertan en usuario avanzado de LaTeX.
- Requisitos previos:
Conocimientos básicos de LaTeX. Que preferentemente deberían incluir: instalación, compilación, visor/editor de documentos. Se recomienda saber elaborar un documento básico, y conocer funcionalidades elementales como: tablas, bloques, comandos básicos, etc.
- Perfil:
El curso está dirigido a estudiantes de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías (EDCTI)
- Contenidos:
- Módulo 1: Maquetación de textos en LaTeX y Beamer para presentaciones.
- Módulo 2: Gráficos Vectoriales y uso de paquetes CTAN en LaTeX Ciencias, Tecnologías e Ingenierías.
- Módulo 3: Herramientas avanzadas en plantillas de LaTeX
- Duración:
20 hrs lectivas presenciales (teórico prácticas), y 32 hrs de trabajo del alumno (2 créditos ECTS). Clases de 2 hrs/diarias. Horario de mañana durante 2 semanas.
- Profesorado responsable:
- Jose A. Dobado Catedrático de Univ.). Dpto. Química Orgánica. Fac. de Ciencias.
- Isaac Vidal Daza (Escala Técnica Informática). Apoyo a la Docencia. CSIRC
- Evaluación:
La superación del curso requerirá:
- Asistencia de al menos 70 % de las sesiones (50 % puntuación).
- Elaboración de un documento maquetado con LaTeX (25 % puntuación).
- Defensa oral con Beamer del trabajo realizado. (25 % puntuación).
- Objetivos de Aprendizaje:
- Adquirir un nivel avanzado en la maquetación de textos científicos.
- Desarrollo de destrezas informáticas orientadas a la mejora de la productividad en el desarrollo de las tareas investigadoras.
- Programa:
MÓDULO 1: Uso Avanzado de LaTeX para maquetación de textos y Beamer para presentaciones (8 hrs)
Día 1: LaTeX avanzado (2 hrs)
- diseño de tablas, trabajo con imágenes y creación de gráficos
- ecuaciones y fórmulas
- funcionalidades avanzadas en LaTeX
Día 2: Generación de presentaciones con Beamer (2 hrs)
- uso de temas y apariencia, organización de contenido
- creación de diapositivas, ventanas, bloques y entornos
- plantillas de presentaciones y contenido dinámico
Día 3: Bases de datos con Biber y BibTeX (2 hrs)
- estilos bibliográficos, personalización
- bases de datos bibliográficas
- uso de internas/externas/varias
Día 4: Uso de plantillas con LaTeX para el maquetado de los resultados de la investigación (2 hrs)
- Plantillas de artículos científicos (ACS, RSC, Wiley, Elsevier, etc.)
MÓDULO 2: Gráficos vectoriales y uso de paquetes de LaTeX en Ciencias, Tecnologías e Ingeniería (6 hrs)
Día 5: PGF/TikZ (2 hrs)
- elementos básicos, líneas, caminos, sombreado, formas, colores
- otros comandos: nodos, variables, contadores, ciclos, recorte, alcance
- uso de librerías y ejemplos de dibujos
Días 6-7: Paquetes CTAN de CIENCIAS, TECNOLOGÍAS E INGENIERÍAS (4 hrs)
- dibujo de fórmulas química, reacciones y moléculas.
- gráficas de alineado de nucleótidos, péptidos, etc
- dibujo de circuitos eléctricos.
- escritura de algoritmos, códigos y diagramas de flujo
- dibujo de diagramas en ingeniería civil y de una planta química
MÓDULO 3: Herramientas avanzadas en plantillas de LaTeX y presentación de trabajos (6 hrs)
Días 8-9: Maquetación avanzada en LaTeX (4 hrs)
- Tesis Doctorales
- técnicas avanzadas de índices y glosarios
Día 10: Presentación de trabajos (2 hrs)
- mini-exposiciones de trabajos orales y escritos
- discusión de resultados
- Contacto:
Jose A. Dobado Facultad de ciencias
http://www.ugr.es/local/dobado
dobado@ugr.es
Introducción a Python: Elementos básicos del lenguaje(2020)
- Profesorado: Patricia Ruano Roca (UGR)
- Duración: 20 horas presenciales
- Fechas y horario: del 31 de mayo al 11 de junio 2021 de 12:00 a 14:00h.
- Lugar: VIRTUAL
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas/edición. Dirigido preferentemente a alumnos/as de primer año de doctorado.
- Inscripción: 4 a 14 de mayo 2021 a través de este formulario.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje esté ganando cada vez más popularidad entre científicos e ingenieros.
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Los elementos básicos de un lenguaje de programación
2.- Tipos de variables y su manipulación
3.- Manipulación de listas, tuplas y diccionarios
4.- Flujos condicionales if y recursivos for
5.- Funciones básicas del lenguaje
6.- Creación de funciones propias
7.- Control de código y manejo excepciones
El alumno será capaz de:
1.- Crear scripts en python para resolver problemas
2.- Leer y analizar un programa escrito en Python
3.- Manejar los principales entornos de programación con IPython (Spyder y Jupyter)
4.- Leer y escribir datos en ficheros de texto
5.- Diseñar algoritmos para la resolución secuencial de problemas
6.- Depurar programas y reconocer los principales tipos de errores
- Programa:
Tema 1. Introducción (1h) Introducción a los lenguajes de programación Historia de Python Descarga e instalación de anaconda. La consola de Python. Partes principales del IDE Spyder.
Tema 2. Tipos básicos, variables y expresiones (4h) Tipos de datos en Python. Variables, operadores y expresiones. Instalar, importar y utilizar módulos en Python. Listas, tuplas y diccionarios.
Tema 3. Operadores y funciones (4h) Operador lógico if. Bucles for. Bucles while. Creación y utilización de funciones en Python.
Tema 4. Operación de entrada/salida y optimización de código (3h) Lectura de ficheros de texto. Escritura en archivos de texto. Módulos os y sys. Control de ficheros y directorios. Optimización de código. Tipos de errores principales en Python. Control de código y manejo excepciones.
Python avanzado para ciencia e ingeniería(2020)
- Profesorado: José Vicente Pérez Peña (UGR)
- Duración: 20 horas presenciales.
- Fechas y horario: 14 a 25 junio 2021 de 12:00 a 14:00h
- Lugar: VIRTUAL
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
- Plazo de inscripción: 14 a 28 de mayo 2021
- Forma de inscripción: rellenar este formulario.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad. Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes. La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos. Una lista completa de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Manejo de matrices multidimensionales con numpy
2.- Funciones básicas para la creación y utilización de matrices de numpy
3.- Lectura-escritura en disco de datos
4.- Creación y representación de funciones matemáticas
5.- Creación de distintos gráficos con matplotlib
6.- Modificación de símbolos y leyendas
7.- Análisis de imagen con scipy
El alumno será capaz de:
1.- Crear y modificar gráficos
2.- Integrar LaTeX directamente en un gráfico
3.- Representar funciones y resolver ecuaciones matemáticas
4.- Entender la documentación de las librerías de Python
5.- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
- Programa formativo:
Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas. Representación de nube de puntos Representación de histogramas y boxplots. Definiendo colores y símbolos. Añadiendo leyendas y etiquetas. Control de ejes. Representación de múltiples figuras.
Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage.
Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Curso 2019/2020
International Research and Educational Collaboration. Strategies 1st Workshop
- Actividad cancelada
- Objetivos:
En este Workshop se pretende poner en contacto por primera vez a las Universidades de Granada y Jiangsu University of Technology, China, después de la forma del acuerdo marco de colaboración, para progresar hacia una relación formal y mantenida en investigación y en formación doctoral. El profesor Cabrerizo participó en abril de 2019 en el “International Research and Education Forum” celebrado en la Jiangsu University of Technology en la ciudad de Changzhou en la República Popular China.
Los contenidos de esta primera reunión se refieren a los aspectos más generales de las estrategias en investigación conjunta. Los ponentes incluyen:
• Prof. Miguel A. Cabrerizo, Universidad de Granada
• Prof. Alidad Amirfazli, University of North York, Toronto, Canadá
• Prof. Wen Li, Jiangsu University of Technology
• Prof. Miguel A. Rodríguez Valverde, Universidad de Granada
todos ellos con amplia experiencia en investigación y experiencia de trabajo conjunto.
- Interés para los/as estudiantes de la EDCTI:
El establecimiento de vías de colaboración internacional es objetivo prioritario de la Escuela de Posgrado y de todos los Programas de Doctorado. Este Workshop puede contribuir a ese propósito, abriendo posibilidades de doctorados en cotutela, intercambios, estancias breves, etc., tanto de estudiantes como de profesorado.
- Fechas: por confirmar
- Programa provisional:
| Time | Activity | Instructor |
|---|---|---|
| por confirmar | Registration | |
| Introduction and Welcome | Prof. Cabrerizo | |
| Strategic Thinking about Research | Prof. Amirfazli | |
| Break | ||
| Conducting International Research Collaboration (A perspective from fast evolving China) | Prof. Li | |
| Afternoon break | ||
| Path to Publication - part 1 | Prof. Amirfazli | |
| Path to Publication - part 2 | Prof. Li |
| Time | Activity | Instructor |
|---|---|---|
| por confirmar | Registration | |
| Proposal writing (hands-on examples) | Prof. Rodríguez-Valverde Prof. Amirfazli |
|
| Break | ||
| Working & Research with Industry | Prof. Li | |
| Afternoon break | ||
| Recognition and Awards | Prof. Amirfazli | |
| Mentoring Principles | Prof. Li |
Writing a research paper in English: strategies and techniques
- Profesorado: Dra. Pamela Faber Benítez, Catedrática Departamento de Traducción e Interpretación. Universidad de Granada.
- Duración: 31 horas (10 h presenciales + 21 trabajo personal).
- Fechas: 20 al 24 de enero de 09:00 a 11:00h.
- Lugar: aula de informática de la Facultad de Derecho (edif. San Pablo).
- Plazas y perfil: 24 plazas.
Dirigido preferentemente a alumnos/as de segundo año de Doctorado.
Para el buen aprovechamiento los alumnos deben tener un nivel razonable de inglés tanto hablado como escrito (al menos, B2).
Aquellos solicitantes que adjunten al correo de solicitud certificación del nivel de inglés (B2 o equivalente) tendrán preferencia sobre el resto para la participación en el curso.
- Plazo de inscripción: del 7 al 12 de enero 2020.
- Forma de inscripción: enviar un correo a --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es indicando en el Asunto ”[EDCTI] Inscripción curso Writing a research paper in English”. Al correo se adjuntara acreditación del nivel de inglés.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción. IMPORTANTE adjuntar certificado del nivel de inglés (ver apartado “Plazas y perfil”).
- Programa:
1. Introduction.
1.1 English as a lingua franca in the scientific world
1.2 The need to publish
1.3 Types of paper
2. Organization.
2.1 Sections
2.2 Content
2.3 Format and Layout
2.4 Common errors
3. Language.
3.1 Syntax and sentence structure
3.2 Semantics and terminology
3.3 Style and punctuation
3.4 Common errors
Introducción a Python: Elementos básicos del lenguaje(2019)
- Profesorado: Patricia Ruano Roca (UGR)
- Duración: 20 horas presenciales.
- Fechas y horario:
| Fechas | Horario |
|---|---|
| 12, 13, 19, 20, 26 y 27 de febrero de 2020 | de 16:30 a 18:30 |
| 10, 11, 17 y 18 de marzo de 2020 | de 16:30 a 18:30 |
- Lugar: aula Juan Campos (Facultad de Ciencias).
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas/edición. Dirigido preferentemente a alumnos/as de primer año de doctorado.
- Inscripción: del 3 al 6 de febrero, rellenando el siguiente FORMULARIO
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad.
Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje esté ganando cada vez más popularidad entre científicos e ingenieros.
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Los elementos básicos de un lenguaje de programación
2.- Tipos de variables y su manipulación
3.- Manipulación de listas, tuplas y diccionarios
4.- Flujos condicionales if y recursivos for
5.- Funciones básicas del lenguaje
6.- Creación de funciones propias
7.- Control de código y manejo excepciones
El alumno será capaz de:
1.- Crear scripts en python para resolver problemas
2.- Leer y analizar un programa escrito en Python
3.- Manejar los principales entornos de programación con IPython (Spyder y Jupyter)
4.- Leer y escribir datos en ficheros de texto
5.- Diseñar algoritmos para la resolución secuencial de problemas
6.- Depurar programas y reconocer los principales tipos de errores
- Programa:
Tema 1. Introducción (1h) Introducción a los lenguajes de programación Historia de Python Descarga e instalación de anaconda. La consola de Python. Partes principales del IDE Spyder.
Tema 2. Tipos básicos, variables y expresiones (4h) Tipos de datos en Python. Variables, operadores y expresiones. Instalar, importar y utilizar módulos en Python. Listas, tuplas y diccionarios.
Tema 3. Operadores y funciones (4h) Operador lógico if. Bucles for. Bucles while. Creación y utilización de funciones en Python.
Tema 4. Operación de entrada/salida y optimización de código (3h) Lectura de ficheros de texto. Escritura en archivos de texto. Módulos os y sys. Control de ficheros y directorios. Optimización de código. Tipos de errores principales en Python. Control de código y manejo excepciones.
Python avanzado para ciencia e ingeniería(2019)
- Profesorado: José Vicente Pérez Peña (UGR)
- Duración: 20 horas presenciales.
- Fechas y horario:
| Fechas | Hora |
|---|---|
| 19, 20, 26 y 27 de Marzo de 2020 | 16:30 a 18:30 |
| 2, 3, 16, 17, 23 y 24 de Abril de 2020 | 16:30 a 18:30 |
- Lugar: Aula Juan Campos (Facultad de Ciencias).
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
- Plazo de inscripción: 2 al 8 de marzo 2020.
- Forma de inscripción: rellenar el siguiente FORMULARIO.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad.
Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos.
NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes.
La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos.
Una lista completa de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Manejo de matrices multidimensionales con numpy
2.- Funciones básicas para la creación y utilización de matrices de numpy
3.- Lectura-escritura en disco de datos
4.- Creación y representación de funciones matemáticas
5.- Creación de distintos gráficos con matplotlib
6.- Modificación de símbolos y leyendas
7.- Análisis de imagen con scipy
El alumno será capaz de:
1.- Crear y modificar gráficos
2.- Integrar LaTeX directamente en un gráfico
3.- Representar funciones y resolver ecuaciones matemáticas
4.- Entender la documentación de las librerías de Python
5.- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
- Programa formativo:
Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas. Representación de nube de puntos Representación de histogramas y boxplots. Definiendo colores y símbolos. Añadiendo leyendas y etiquetas. Control de ejes. Representación de múltiples figuras
Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage
Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Multivariate Exploratory Data Analysis (MEDA)(2019): Understanding by looking at data
- May 26th-29th 2020
- Deadline for application: 29th April 2020 - 7th May 2020
- How to apply: https://forms.gle/VKmD8AsSrMXPTXsd7
- NOTES
- Course on line.
- The course will be held in English.
- It is requiered basic knowledge of MatLab. Those students who can provide certification of that knowledge will have preference in admission.
- Course Goal
Do you have complicate data? Difficult to understand? With thousands of variables/observations? Or with too little observations? Missing data? Time series? Multiple sources? Big Data?
The course goal is to introduce the students to very powerful data visualization techniques to look into your data set. There is a bunch of Machine Learning (ML) methods that can do difficult tasks (like classification, modelling and prediction) using a black-box approach over data, deep learning being a popular example. This course shows a totally different approach to handling data, using ML only as an instrument (as a means) to understand your data. MEDA will show you how to look into your data set, regardless its complexity, so that you can find groups of individuals and classify them, understand relationships among measured quantities, detect anomalies, find parsimonious models, etc.
The course is led by Professor Rasmus Bro, world leading professor on data analysis in biological and food sciences, and his collaborator at the UGR Dr. José Camacho, specialist on data analysis in Big Data and Exploratory Data Analysis.
- Teaching hours: 30
- Teachers:
Professor Bro is a prominent figure in the field of data analysis and in particular in multivariate analysis. During the last two decades, Prof. Bro has been a principal actor in the development of multivariate analysis in chemical and biological applications in the chemometrics area, in which according to google scholar is the second top researcher. His vast research work is outstanding, presenting an H index equal to 65. Prof. Bro is the author of the most referenced tutorial of PARAFAC (1933 citations), the developer of an extensively used multi-way version of Partial Least Squares (N-PLS) and co-author of more than 200 publications mainly related to the use of multi-way analysis in real life applications. His contributions to the use of constrained modelling are also very relevant, including the use of sparse methodologies for data analysis, and he has co-authored relevant articles to the problem of data fusion, a main challenge in Big Data analyses. The international influence in the community of his course “Multi-way Analysis” and his monograph “Multi-way Analysis: applications in the chemical sciences” is widely recognized. Prof. Bro has taught courses on data analysis in dozens of public and private organizations around the world. From 2001, he is the head of ODIN, an industrial research consortium offering courses, workshops, international contacts and student collaboration.
José Camacho is an associate professor in the Department of Signal Theory, Networking and Communications and researcher in the Information and Communication Technologies Research Centre, CITIC for its initials in Spanish, and in the Network Engineering & Security Group (NESG), both at the University of Granada, Spain. His research interests include exploratory data analysis, anomaly detection and optimization with multivariate techniques applied to data of very different nature, including industrial processes, chemometrics and communication networks. He is especially interested in the use of exploratory data analysis to Big Data.
- Examination:
Every person analyze their own data under supervision of the teacher and writes a report. The report must be short and concise. A short description of the data and their background must be provided. A short description of aim of the present work must be provided. This aim is not necessarily the overall aim of the project from which the data stem (although this is of course nice). Rather the purpose should be chosen in order to test and evaluate the students’ ability to use the methods taught at the course. It is important to discuss in detail how the models have been critically used for the stated purposes.
- Schedule: ONLINE
Day 1: PCA (Prof. Bro & Dr. Camacho)
| 8:30-9:30 | Welcome (Bro & Camacho) |
| 9:30-10:00 | Introduction and algebra without tears |
| 10:00-11:15 | Principal Component Analysis – PCA |
| 11:15-11:30 | Break |
| 11:30-12:00 | Software introduction (demos/hands-on) |
| 12:00-12:30 | Exercises – PCA |
| 12:30-13:30 | Validation, outliers – PCA |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises – PCA |
Day 2: PLS (Prof. Bro)
| 9:00-9:15 | PCA summary |
| 9:15-10:30 | Multivariate calibration - PLS |
| 10:30-10:45 | Break |
| 10:45-11:30 | Exercises – Multivariate calibration |
| 11:30-13:00 | Validation and outliers incl. exercises |
| 13:00-15:00 | Lunch |
| 15:00-16:00 | Preprocessing and nice to know |
| 16:00-16:15 | Break |
| 16:15-18:00 | Competition! |
Day 3: MEDA Toolbox (Dr. Camacho)
| 9:00-10:00 | Introduction to the MEDA Toolbox |
| 10:00-11:15 | Using the command line interface |
| 11:15-11:30 | Break |
| 11:30-12:30 | Advanced Exploratory Data Analysis |
| 12:30-13:30 | Exercises & Examples |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 4: Big Data (Dr. Camacho)
| 9:00-11:00 | Extensions to Big Data: Big Observations |
| 11:00-11:30 | Break |
| 11:30-12:30 | Exercises |
| 12:30-13:30 | Extensions to Big Data: Big Variables |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
Day 5: Playing with your data I (Prof. Bro & Dr. Camacho)
Time will be devoted to analyze your own data under the supervision of the course monitors, who will guide you through different analysis techniques to pursue your goals.
| 9:00-14:00 | Playing with your data |
Taller de escritura de textos científicos con LaTeX y control de versiones con Git(2019)
- Profesorado:
Miguel Burgos Poyatos. Dpto. de Genética. Facultad de Ciencias.
- Duración del curso (horas teóricas/prácticas):
20 horas en modalidad virtual + 20 horas no presenciales/trabajo personal
- Calendario y horario:
6, 8, 10, 13, 15, 17, 20 de abril 2020 de 11:00 a 14:00 todos los días excepto el viernes 17 que será de 12:00 a 14:00.
- Lugar de impartición:
Virtual.
- Plazas y perfil (año de matriculación en doctorado):
El límite de plazas se establecerá conforma a las posibilidades técnicas. Es posible inscribirse durante cualquier año del doctorado. El taller está abierto tanto a doctorandos, tanto a tiempo completo como parcial.
- Necesidad de acreditación de conocimientos previos:
No es necesario acreditar conocimientos previos
- Evaluación:
Los alumnos crean un repositorio Git para el curso en http://Bitbucket.org donde trabajan durante todo el taller y lo comparten con el profesor que, de esta forma puede seguir todo el trabajo que realizan los alumnos tanto durante las horas presenciales como en las no presenciales. Además, un Foro en la plataforma MOODLE permite la comunicación entre todos los participantes y la resolución de dudas y cuestiones de forma abierta y visible para todos los alumnos. Al final del taller el repositorio deberá contener la presentación de un texto científico que incluya bibliografía y diversos tipos de índices así como el historial de cambios de los archivos generados y situados bajo el control de Git. Siendo evaluado por el profesor responsable de la actividad.
- Inscripción:
La inscripción se realizará a través del siguiente enlace:
http://mendel.ugr.es/genetica/course/index.php?categoryid=14
Desde el 19/03/2020 hasta completar el límite de plazas.
- Justificación académica:
El taller está directamente enfocado a la escritura de la Tesis Doctoral. Los alumnos aprenden a utilizar el sistema de composición de textos LaTeX para escribir textos científicos, manejo automático de la bibliografía, y generar documentos en distintos formatos a partir del código fuente. Asimismo aprenden a utilizar el sistema de control de versiones Git, que resulta de especial interés para la administración de trabajo colaborativo, como la redacción conjunta de artículos de investigación o las correcciones de la memoria de la Tesis doctoral por parte de sus directores, por lo que es recomendable que tanto alumnos como sus directores asistan conjuntamente a este taller.
II Granada Meeting on Coastal Systems
- Date: 7th February 2020
- Organization:
Andalusian Inter-University Institute for Earth System Research
Doctoral Programme in Biogeochemical Flow Dynamics and Its Applications - Doctoral School in Science, Technology and Engineering – University of Granada
- Programme:
| I. Vulnerability of coastal ecosystems to climate change | ||
|---|---|---|
| 9:30-10:15 | Rafael Muñoz Carpena Professor of Hydrology and Environmental Modeling at the University of Florida, USA |
|
| 10:15-10:45 | María Ángeles Serrano García Postdoctoral researcher at the University of Granada, Spain |
|
| 10:45-11:15 | Break | |
| II. Soils and marine sediments under global change | ||
| 11:15-12:00 | Juan Carlos Santamarina Professor of Energy Resources and Petroleum Engineering at King Abdullah University of Science and Technology, Saudi Arabia |
|
| 12:00-12:30 | Pilar Díaz Carrasco Postdoctoral researcher at the University of Granada, Spain |
|
| 12:30-12:45 | Break | |
| III. Spatio-temporal dynamics of flood risk | ||
| 12:45-13:30 | Andreas P. Zischg Associate Professor at the Institute of Geography of the University of Bern, Switzerland |
|
| 13:30-14:00 | Andrea Lira Loarca Postdoctoral researcher at the University of Granada, Spain |
|
| 14:00-16:00 | _ | Break |
| IV. Hands-on short course: “Risk Analysis: A Global Sensitivity and Uncertainty Analysis framework” | ||
| 16:00-18:00 | Rafael Muñoz Carpena Professor of Hydrology and Environmental Modeling at the University of Florida, USA |
|
- Forma de solicitud: entrada libre hasta completar aforo
- Más información en el siguiente enlace: https://gdfa.ugr.es/coastal-systems-2020
Cálculo Estocástico y Técnicas de Análisis Multivariante. Fundamentos y aplicaciones en Ciencias Experimentales
- Justificación académica del curso:
Es incuestionable la importancia que en las últimas décadas ha experimentado la aplicación de numerosas técnicas probabilístico-estadísticas en múltiples campos de aplicación. La razón última de ello viene motivada por la necesidad de describir y explicar la evolución de fenómenos, no sólo desde un punto de vista cualitativo sino cuantitativo, a la vez que se hace imprescindible en múltiples ocasiones poder inferir comportamientos futuros de los sistemas que son objeto de estudio.
Los fenómenos considerados por las Ciencias Experimentales consideran tanto situaciones estáticas como dinámicas, en las cuales el fenómeno estudiado evoluciona a lo largo del tiempo (o de una variable indexada según un criterio), lo cual motiva plantearse el estudio de variables temporales que respondan a situaciones concretas relacionadas con las variables estudiadas. Asimismo, dentro del ámbito estático lo habitual es tratar con múltiples variables que no pueden ser consideradas de forma aislada, sino formando parte de un diseño complejo.
Las dos situaciones descritas conllevan la necesidad de plantear un doble enfoque sobre el cual creemos que es interesante presentar una panorámica general, sobre todo desde el punto de vista de la aplicación de las técnicas presentadas en múltiples campos. En ese sentido, la idea principal de esta actividad es ilustrar a los alumnos sobre técnicas y métodos del Análisis Multivariante y de Cálculo Estocástico, mostrando una visión general de sus fundamentos así como una perspectiva de aplicaciones en diversos campos: Biología, Ecología, Recursos Energéticos,... Asimismo están previstas sesiones de prácticas en ordenador para ilustrar los métodos introducidos mediante implementaciones en R.
Por ello el curso se ha diseñado siguiendo dos bloques diferenciados:
1. Modelización mediante procesos estocásticos.
2. Técnicas de Análisis Multivariante.
- Contenidos:
1. Modelización mediante procesos estocásticos:
a. Visión general del concepto de proceso estocástico.
b. Cadenas de Markov y procesos de nacimiento y muerte.
c. Introducción a los procesos de difusión. Aplicación a la modelización de fenómenos de crecimiento. Inferencia y tiempos de primer paso.
2. Técnicas de Análisis Multivariante:
a. Modelo Lineal Multivariante: modelo de Regresión lineal múltiple multivariante y técnicas tipo MANOVA.
b. Técnicas de reducción de dimensiones. Técnicas de clasificación automática.
- Duración: 27 horas.
- Plazas: 20.
- Perfil: Dirigido a alumnos de doctorado de EDCTI (es posible inscribirse durante cualquier año del doctorado) y alumnos del Máster en Estadística Aplicada.
- Periodo de impartición y duración: 24, 25 y 26 de febrero; 2, 3, 4 y 5 de marzo.
- Calendario y horario:
| Fecha | Hora | Profesor/a | Lugar |
|---|---|---|---|
| Lunes 24/2 | 9:00-11:00 y 11:30-13:30 h | Prof.ª Pirozzi | Aula G17 |
| Martes 25/2 | 9:00-11:00 y 11:30-13:30 h | Prof.ª Pirozzi | Aula G17 |
| Miércoles 26/2 | 9:00-11:00 y 11:30-13:30 h | Doct. Ascione | Aula de ordenadores O06 |
| Lunes 2/3 | 10:00-11:30 y 12:00-13:30 h | Prof.ª Cobo | Aula de ordenadores O04 |
| Martes 3/3 | 10:00-11:30 y 12:00-13:30 h | Prof.ª Cobo | Aula de ordenadores O07 |
| Miércoles 4/3 | 9:00-11:00 h (1) | Prof. Barrera | Aula de ordenadores O01 (1) |
| 11:30-14:00 h (2) | Prof. Barrera | Aula de ordenadores O04 (2) | |
| Jueves 5/3 | 9:00-10:30 h | Prof. Barrera | Aula de ordenadores O01 |
| Jueves 5/3 | 11:00-14:00 h | Prof. Serrano | Aula de ordenadores O08 |
IMPORTANTE: las clases de los días 24, 25 y 26 de febrero se impartirán en inglés por lo que es necesario contar con un nivel adecuado del idioma para su correcto aprovechamiento. El resto de clases se impartirán en español.
- Ubicación de las aulas:
• Aula G17 (1ª planta sección de Geológicas).
• Aula de ordenadores O01 (ubicada en zona Biológicas junto al Decanato).
• Aula de ordenadores O08 (ubicada en zona Matemáticas).
- Profesores:
• Antonio Jesús Barrera García. Universidad de Málaga.
• Beatriz Cobo Rodríguez. Universidad Complutense de Madrid.
• Enrica Pirozzi. Università degli studi di Napoli Federico II.
• Giacomo Ascione. Università degli studi di Napoli Federico II.
• Juan José Serrano Pérez. Universidad de Granada.
- Plazo de solicitud: del 3 al 12 de febrero 2020.
- Forma de solicitud: rellenar el siguiente FORMULARIO
Herramientas para el desarrollo de la Investigación
- Profesores/as que la imparten: Anne-Vinciane Doucet, Antonio Fernández Porcel, Mª Ángeles García Gil, Esteban López García y Daniel Marín Conesa
Primera Edición
- Fechas de realización: del 3 al 5 de marzo de 2020
- Plazo de solicitud: del 10 al 16 de febrero de 2020
- Forma de inscripción: rellenar el siguiente FORMULARIO
Segunda Edición
- Fechas de realización: 31 de marzo, 1 y 2 de abril de 2020
- Plazo de solicitud: del 3 al 8 de marzo 2020
- Forma de inscripción: rellenar el siguiente FORMULARIO
- Lugar de realización: Aula Biblioteca Derecho (Ubicación Calle Duquesa)
- Horario: de 10:00 a 13:00
- Perfil: Dirigido a alumnos/as de primer año
- Nº Alumnos: 30
- Programa de la actividad:
1. Perfil de investigador:- El perfil de investigador. Utilidad y necesidad.
- Necesidad de normalización del nombre de investigador. -Números de identificación: ORCID, ResearcherID (WoS), Author ID (Scopus).-Perfil y difusión de la investigación: ventajas y “herramientas”: UGR-Investiga, Google Scholar, Academia.edu, ResearchGate. Dialnet-El perfil de investigador y la evaluación de la producción científica. ANECA, DEVA y SICA. El CVN.
2. Bases de datos:- Bases de datos en: Ciencias, Tecnologías e Ingenierías y Ciencias de la Salud: JCR-Science, JCR-Social Science WOS, SCOPUS
- Bases de datos en: Humanidades, Ciencias Sociales y Jurídicas: JCR-Social Science, Arts and Humanities Citation Index, Dialnet
3. Gestores bibliográficos:- Introducción a los gestores bibliográficos
- Gestores bibliográficos: Mendeley, Flow, Endnote
Taller Ómicas. Microbial diversity studies through 16S amplicon sequencing
- Profesorado:
Profesor 1: Juan Manuel Peralta Sánchez.
- El Dr. Juan Manuel Peralta Sánchez es investigador postdoctoral en el grupo de Carles Vilà, en la Estación Biológica de Doñana (CSIC). Su fuerte formación como biólogo evolutivo se ha complementado con conocimientos en comunidades bacterianas especialmente utilizando herramientas de secuenciación masiva. Su interés principal se focaliza en las relaciones que los vertebrados establecen con sus comunidades bacterianas, desde las comunidades de los huevos de las aves a los cambios en su microbiota intestinal.
Profesora 2: Sonia M. Rodríguez Ruano.
- La Dra. Sonia M. Rodríguez Ruano es actualmente investigadora postdoctoral en el Departamento de Parasitología de la Facultad de Ciencias de la University of South Bohemia (Ceske Budejovice, Czech Republic). Trabaja con diversos sistemas simbióticos bacterianos, especialmente estudiando la dinámica de las asociaciones entre microbiomas y hospedadores (parásitos hematófagos) en función de distintos factores ecológicos y fisiológicos (distribución geográfica, estacionalidad, capacidad vectorial…).
- Duración del curso (horas teóricas/ prácticas): Horas presenciales: 20h. Horas no presenciales: 20h.
- Calendario y Horario:
| Fecha | Hora | Lugar |
|---|---|---|
| Martes 7 de enero | 09:30 - 14:00 | Aula MS1 (ubicada en Sótano de Matemáticas) |
| Miércoles 8 de enero | 09:00 - 14:00 | Aula MS2 (ubicada en Sótano de Matemáticas) |
| Jueves 9 de enero | 09:00 - 14:00 | Aula MS2 (ubicada en Sótano de Matemáticas) |
| Viernes 10 de enero | 09:00 - 14:00 | Aula M02 (ubicada en Sección de Matemáticas) |
- Material necesario: Es necesario que los alumnos traigan su propio ordenador con Linux, o bien que instalen una máquina virtual de Linux (Ubuntu recomendado) si trabajan con otro sistema operativo. Los programas necesarios se instalarán en la primera sesión.
- Plazas y perfil (año de matriculación en doctorado): 15 plazas. Es posible inscribirse durante cualquier año del doctorado.
- Necesidad de acreditación de conocimientos previos: No es necesario acreditar conocimientos previos.
- Forma y plazo de Inscripción: Para inscribirse en el curso hay que enviar un correo al Dr. Manuel Martínez Bueno: --LOGIN--aa351977be402bbcd7a649d7a0acbcbfugr[dot]es del 20 de noviembre al 5 de diciembre de 2019.
- Objetivos: El curso se basa en herramientas bioinformáticas ampliamente empleadas en ecología microbiana, como QIIME2. Se proporcionará a las estudiantes la base para su uso en modo línea de comandos (en sistemas Linux), y se analizarán datos de ejemplo a través de los tutoriales de QIIME2, explicando cada uno de los pasos a seguir y su utilidad. Por último, se analizarán los resultados obtenidos para proporcionar a las estudiantes la capacidad de su interpretación de forma independiente una vez finalizado el curso.
El alumno sabrá:- Elaborar y validar archivos de metadatos para ecología microbiana;
- Reconocer y hacer una valoración inicial de los archivos originales obtenidos de sequenciadores tipo Illumina (raw data);
- Procesar las lecturas del secuenciador para obtener tablas de asignación de variantes microbianas por muestra;
- Analizar los datos obtenidos para comparar distintas variables ecológicas, tratamientos experimentales, etc.;
El alumno será capaz de:- Realizar acciones básicas en líneas de comandos basadas en UNIX;
- Instalar y utilizar las herramientas básicas de Qiime2;
- Diseñar estudios para evaluar y comparar diversidad microbiana mediante secuenciación del 16S;
- Interpretar los resultados básicos de este tipo de estudios;
- Programa formativo (Contenidos y Temas/Módulos):
1. Introducción al estudio de comunidades bacterianas y secuenciación masiva
2. Instalación de programas y breve introducción a la línea de comandos
3. Instalación de Qiime2
4. Análisis upstream: del archivo de secuencias a la tabla de OTUs
5. Análisis downstream I: breve introducción a la ecología de comunidades y la diversidad bacteriana
6. Análisis downstream II: análisis básicos de diversidad desde la OTU table
7. Análisis downstream III: análisis adicionales de diversidad bacteriana
8. Dudas, sugerencias y despedida
- Trabajo no presencial:
Los alumnos deberán de presentar un trabajo fin de curso con los resultados de tareas que se les encomienden fuera de las horas presenciales. Los alumnos podrán realizar estas actividades mediante comunicación virtual con los profesores encargados del curso.
Ejercicio 1 – Sesión 1. Los alumnos instalarán el programa Sublime Text 3, un procesador de texto donde irán guardando los scripts que vayan corriendo. Esta instalación la realizarán desde la terminal UNIX. Deberán de crear un archivo log.sh como cuaderno de prácticas, donde irán guardando los comandos que han usado.
Ejercicio 2 – Sesión 2. Los alumnos crearan desde la terminal un árbol de carpetas y diferentes archivos con información adquirida con el uso de los comandos en la terminal UNIX. Importarán una pequeña base de datos con secuencias a QIIME2, realizaran la unión de secuencias forward y reverse y decidirán si el solapamiento es suficiente para seguir con él, o deberían de seguir los análisis posteriores solo con las secuencias forward. Este es el paso clave 1 en el análisis de secuencias.
Ejercicio 3 – Sesión 3. Los alumnos deberán de hacer un clustering de secuencias. La mitad de los alumnos la realizarán con Deblur y la otra mitad siguiendo DADA2. Tendrán que decidir qué tamaño de secuencia eligen para perder el mínimo de secuencias, pero con un tamaño razonable para la asignación taxonómica. Este es el paso clave 2 en el análisis de secuencias.
Ejercicio 4 – Sesión 4. Realizarán análisis de diversidad alfa y beta, y decidirán el nivel de rarefacción elegido, para maximizar el número de muestras, pero con un numero de secuencias con significado biológico. Este es el paso clave 3 en el análisis de secuencias.
Ejercicio 5 – Sesión 5. Realizaran análisis adicionales de diversidad (ANCOM, gneiss, heatmaps…). Importarán las figuras de diversidad y las añadirán a un archivo Word.
- Evaluación: Se evaluarán los análisis realizados por los estudiantes durante el periodo de supervisión de trabajos y se podrá valorar la actitud en clase y tutorías.
Taller Some tips/rules for Scientific Writing in English
- AVISO IMPORTANTE: Por circunstancias sobrevenidas se pospone la realización del Taller. Próximamente informaremos de la nueva fecha y lugar de su celebración. Rogamos disculpen las molestias que les pueda suponer.
- 6 de junio de 2019, 11:00, Sala Eniac (Edificio Mecenas). Esta sala tiene capacidad para unas 100 personas.
- Ponente: Dr. Andrew S. Kowalski. Andrew S. Kowalski se doctoró en ciencias atmosféricas en la Universidad Estatal de Oregon (1996), y trabajó como post-doc en Bélgica (3 años) y Francia (2 años) antes de aterrizar en España con un contrato Ramón y Cajal en la Universidad de Granada. Ahora es catedrático de micrometeorología en el Departamento de Física Aplicada, y lidera un grupo investigando los intercambios de gases de efecto invernadero entre la atmósfera y los ecosistemas terrestres. Sus publicaciones científicas tratan un rango amplio de disciplinas, abarcando las metodologías para caracterizar los intercambios turbulentos de gases, la propagación de errores en dichas mediciones, los intercambios netos de vapor de agua y de CO2 y sus determinantes ambientales, y la respuesta de los ecosistemas al cambio climático. Ha publicado más de 75 artículos, de los cuales 28 han estado citadas >27 veces (índice-H de 28; WoS). Es editor de la revista Scientific Reports, y hace frecuentemente de referee para las revistas Biogeosciences, Global Change Biology y Agricultural and Forest Meteorology. Ha actuado como investigador principal o responsable en numerosos proyectos de investigación, financiados por la Junta de Andalucía, el Ministro relevante en Madrid, y la Unión Europea, atrayendo más de 750000€ de financiación externa a la UGR. https://www.ugr.es/~andyk.
- Dirigido a Alumnos de doctorado de EDCTI y personal investigador en general.
- Contenido: Este taller ofrece unas líneas para la preparación de manuscritos científicos en inglés. Empezará con una introducción con factores para tener en cuenta antes de empezar a redactar. Luego, presentará unas ideas importantes sobre la estructura, tanto de un artículo científico como de un párrafo. Hablará de las diferentes secciones de un artículo, y de los estilos y estructuras apropiadas para cada sección. Sintetizará el procedimiento de someter un artículo a la revisión del editor y los referees. Finalmente, ofrecerá unas sugerencias sobre estilo, gramática, y ortografía que ha seleccionado para los autores cuyo idioma nativo es el castellano. Como esta charla ha evolucionado durante muchos años de su presentación, y se ha mejorado con sugerencias de numerosos doctorandos durante años anteriores, se anima al público que interrumpan con cuestiones y sugerencias en cualquier momento.
- Programa: Charla de una hora y media, más sesión de preguntas y discusión. La actividad se desarrollará en castellano, con diapositivas en inglés.
- No es necesaria inscripción previa. La entrada al taller es libre hasta completar aforo (100 plazas).
NO SE EMITIRÁ CERTIFICADO DEL CURSO A LOS ASISTENTES.
- Contacto: Andrew Kowalski (Departamento de Física Aplicada; --LOGIN--46b8c5d0f3f3cf6d5511ba9da7bf2d59ugr[dot]es )
EDCTI LECTURE SERIES: Hyperspectral Imaging: the jump from single-point inspection to two dimensional spectral measurement for agri-food applications
- Dr Tassos Koidis. Institute for Global Food Security, Queen’s University Belfast.
- Room B-1; Biology Section, Faculty of Sciences, Friday October 25, 2019, 9:30 - 10:30 am.
- Organized by PhD Programme in Chemistry and master Khemia
Entrada libre hasta completar aforo. Aquellos asistentes que deseen que se certifique su asistencia deben descargar el documento de asistencia disponible en el Portal de seguimiento académico de doctorandos (pestaña “DAD”), cumplimentar el mismo y llevarlo a la conferencia para que el organizador de la actividad se lo firme.
- Abstract. Hyperspectral imaging (HIS) is an emerging, multi-parametric, non-destructive analytical technique capable of acquiring both spatial and spectral information from a target by combining traditional imaging and spectroscopy methods. Firstly developed for a military, hyperspectral imaging allows characterisation of a sample's spectral (spectroscopic component) and surface properties (imaging component) producing for each point of the image acquired full spectral information at all wavelengths of the analytical spectral range (UV–Visible, NIR or IR). All these is making it a powerful tool for many food and agricultural applications. Data obtained by HSI are firstly mathematically pre-processed to extract analytical information from spectra and remove non-chemical biases and then subjected to chemometric elaboration through the application of complex multivariate analytical tools, such as principal component analysis (PCA), partial least squares (PLS), linear discriminant analysis (LDA), multi-linear regression (MLR) and artificial neural networks (ANN), and to highlight possible significant differences between analysed samples. Several studies concerning the application of this technique for the quality sensing of agricultural and food products are reported in the literature. Most of the hyperspectral imaging research, mostly in reflectance mode, has been conducted in the VIS-NIR (400–1000 nm) or NIR (1000–1700 nm) region, and has been used to detect defects, contaminants and quality parameters of various food products (fruits, vegetables, meat products).
- Dr Tassos Koidis his MSc in Food Technology and Quality Assurance in the University of Reading, School of Food Biosciences Reading, UK and his PhD in Chemistry at the Aristotle University of Thessaloniki, Dept. of Chemistry. In 2008-2009 he was Research Officer, TEAGASC (Irish Agriculture and Food Development Authority). Ashtown Food Research Centre. Dublin, Ireland and in 01/01/2010 became Lecturer in Food Science and Nutrition at the Institute for Global Food Security. School of Biological Sciences, Queen’s University Belfast. His research interest is focussed on food authenticity and detection of fraud using a combination of state-of-the-art analytical methods (spectroscopic incl. imaging and chromatographic), Vegetable oils and Lipid Chemistry: olive oil; palm oil. Role of minor constituents (authenticity and quality), Multivariate data analysis & Chemometrics: novel classification techniques; quantification, multivariate modelling, decision making tools, Novel/functional food bioactives: their sources, isolation and bioactivity assessment, and Novel Food processing technologies for quality and safety of ready-to-eat foods. In these areas he has co-ordinated or participated in 9 of national and international research projects 3 of them in EC Horizon 2020 and EC FP7.
EDCTI LECTURE SERIES: Common and distinct components in data fusion
- Age K. Smilde, University of Amsterdam, Swammerdam Institute for Life Sciences, Amsterdam, The Netherlands, a.k.smilde@uva.nl. #http://www.bdagroup.nl/#
Wednesday October 30, 2019
10:30 - 11:30 am
Salón de Grados de la ETSIIT
https://goo.gl/maps/fjnv5LYpbz3gCtYo8
- All PhD programs of the Doctoral School of Science, Technology and Engineering.
- Abstract. One of the active research topics in both chemometrics and systems biology is data fusion. This is also called data integration in systems biology and multiset analysis in chemometrics and psychometrics. Although this field has already a long history (especially in chemometrics and psychometrics), it has recently attracted a lot of attention in systems biology due to the availability of large genomics data sets. One of the topics within data fusion is to separate common from distinct components in these data sets. This is important since it cleans up the exploratory process by the ability to focus on these components. There are several methods to distinguish common from distinct components and some of these will be discussed. We will also address the fusion of data of different measurements scales and how to find common and distinct components in these types of data.
- Keywords. Measurement Scales, Multiset Data, Data Fusion, Common, Distinct, Unique Variation.
- Age K. Smilde Age K. Smilde received his MSc in Econometrics and his PhD in Analytical Chemistry at the University of Groningen. In June 1993 became full professor of Process Analysis and Chemometrics at the Faculty of Science of the University of Amsterdam. In January 2004, he became professor of Biosystems Data Analysis (BDA). As of June 1, 2013, Age has been appointed as a part-time professor of Computational Systems Biology at the University of Copenhagen at the Faculty of Sciences. He is the Eastern Analytical Symposium 2006 Award Recipient for Achievements in Chemometrics. In 1996 he was chairman of the Gordon Research Conference on Statistics in Chemistry and Chemical Engineering in Oxford (UK). Together with Rasmus Bro and Paul Geladi he wrote the book Multiway Analysis: Applications in the Chemical Sciences. His research interest is multiset data analysis and its implementation in different fields of biology; such as medical biology, nutritional science, biotechnology and systems biology. He has also a profound interest in philosophy in general and in the philosophy of science in particular. He also likes traveling and hiking.
- Plazo de inscripción: del 17 al 24 de octubre de 2019
- Forma de inscripción: Los interesados deben solicitarlo cumplimentando el siguiente FORMULARIO
EU H2020 Programme Marie Skłodowska-Curie action ETN SMARTI Autumn Doctoral School AUTOMATED TRANSPORT INFRASTRUCTURES
Abierto a los estudiantes del Programa de Doctorado en Ingeniería Civil y de las Escuelas de Doctorado de UGR.
En el marco del proyecto europeo SMARTi_ETN (Sustainable, Multifunctional, Automated, Resilient Transport Infrastructures, https://www.smartietn.eu/), la semana del 30 de septiembre a 4 de octubre de 2019, se celebrará en la ETSICCP de la UGR, la Autumn School (Training week) titulada “AUTOMATED TRANSPORT INFRASTRUCTURES” abierto a doctorandos del Programa de Ingeniería Civil y de las Escuelas de Doctorado de UGR.
Inscripción. La asistencia a las sesiones formativas es gratuita (aforo limitado). Los interesados en asistir deben enviar email a Ana Jiménez del Barco (ajbc@ugr.es) indicando nombre y apellidos, titulación, programa de doctorado al que pertenece y sesiones en las que está interesado asistir.
Las sesiones abiertas a investigadores externos a SMARTi son las siguientes (subrayados los de interés general):
- El lunes 30 de septiembre, en horario de 9:30 a 13:30 (salón de Grados, planta -2), los 15 proyectos de investigación que conforman SMARTi, se expondrán públicamente por parte de los investigadores que los desarrollan y serán debatidos por representantes de la industria y administraciones públicas.
- Martes 1 de octubre a las 15:00 horas (salón de Grados, planta -2), el profesor Andrew Dawson de la Universidad de Nottingham, dará una conferencia titulada “So you want to produce a perfect thesis…” (duración 40 minutos).
- Miércoles 2 de octubre, de 9:30 a 11:00 horas (seminario 2, planta 4) se impartirán las conferencias:
- 09:30 “Distributed _bre optic sensing in roads and transport infrastructures” Massimo Facchini from Iridis Solutions GmbH (Swizertland)
- 10:30 “Sensors: technologies, installation and measurement treatment”. Pierre Hornych from Iffstar (France)
- Jueves 3 de octubre, de 9:30 a 18:00h (seminario 2, planta 4), (breaks at 11:00 and 13.30), tendrá lugar la scientific training on “Automated Transport Infrastructures”, by Nizar Lanef from Michigan State University (USA)
- Viernes 4 de octubre, de 9:30 a 18:00h (seminario 2, planta 4), tendrán lugar las siguientes conferencias:
- 09:00 “Risk assessment in R&D projects” German Martinez Montes. UGR
- 10:00 “Patents and Intellectual property” Juan Antonio Muñoz Orellana. UGR
- 11:30 “Skilled Professionals and Organizational Success: where are you?” Rafael Muñoz. UGR
- 12:30 “Funding opportunities to develop you R&D career” Maria Ros. UGR
Curso 2018/2019
II Edición. Curso Básico de Análisis de Datos en R
- Profesorado: Antonio Jesús Muñoz Pajares (Dpto. Genética), Ana María Aguilera del Pino (Dpto. Estadística e I.O.), José María Conde Porcuna (Dpto. Ecología), Juan Lorite Moreno (Dpto. de Botánica), Rafael Rubio de Casas (Dpto. Ecología), María del Mar Rueda García (Dpto. Estadística e I.O.), Francisco de Asís Torres Ruiz (Dpto. Estadística e I.O.).
- Coordinador: José María Conde Porcuna (Emai: --LOGIN--34ed1bd877cef421e1bb543eb83410ccugr[dot]es )
- Duración del curso (horas teóricas/prácticas): 36 horas (29 horas de clases teórico-prácticas + 7 horas tutorías). Horas no presenciales de los estudiantes: 25 horas de estudio/trabajo.
- Calendario y horario: Durante el curso 2019-2020 se impartirán las clases presenciales en septiembre los días 12 (9:00-12:00 y 12:30-14:30), 13 (9:00-11:00 y 11:30-13:30), 18 (9:00-11:00 y 11:30-13:30), 20 (9:00-11:00 y 11:30-13:30), 26 (9:00-11:00 y 11:30-13:30), y 27 (9:00-11:00 y 11:30-13:30); y en octubre el día 4 (9:00-11:00 y 11:30-13:30). Posteriormente, desde el 9 de octubre hasta el 15 de noviembre de 2019, se llevará a cabo la supervisión del trabajo de los alumnos de forma personalizada. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado según las afinidades previamente establecidas el 8 de octubre de 2019.
- Lugar de impartición: Seminario de Matemáticas 2 (2º planta del edificio de Matemáticas de la Facultad de Ciencias).
- Material necesario: Ordenadores portátiles.
- Plazas y perfil (año de matriculación en doctorado): 20 plazas. Es posible inscribirse durante cualquier año del doctorado.
- Necesidad de acreditación de conocimientos previos: No es necesario acreditar conocimientos previos.
- Modo y plazo de solicitud: del 15 de julio al 4 de septiembre rellenando el siguiente FORMULARIO.
- Evaluación: Se evaluarán los análisis realizados por los estudiantes durante el periodo de supervisión de trabajos y se podrá valorar la actitud en clase y tutorías.
- Justificación académica: La obtención de datos de diverso tipo, tanto de manera experimental como observacional, requiere necesariamente unos conocimientos estadísticos suficientes para su adecuado análisis, y así obtener las conclusiones pertinentes. En este curso de doctorado, los alumnos podrán aprender las técnicas más comunes para el análisis de datos y podrán aplicar los conocimientos que adquieran sobre los ficheros de datos que dispongan para la realización de sus Tesis doctorales. Los análisis que hagan con dichos ficheros serán supervisados inicialmente por el profesorado de la asignatura.
- Objetivos educativos, profesionales y competencias generales adquiridas: El objetivo del curso es que los estudiantes de doctorado conozcan y apliquen los métodos estadísticos más utilizados, fundamentalmente en Biología, para que puedan utilizarlos durante la realización de sus Tesis doctorales. En las clases se utilizarán datos reales como ejemplos para una mejor comprensión.
- El alumno sabrá: Construir ficheros para análisis de datos. Utilizar determinadas herramientas de análisis según su tipo de datos. Los paquetes de R necesarios para distintos análisis de datos fundamentales. Los scripts de R necesarios para distintos análisis de datos fundamentales. Ejecutar distintos análisis estadísticos de datos.
- El alumno será capaz de: Diseñar estudios experimentales. Utilizar de forma básica el paquete estadístico R. Interpretar resultados experimentales y/o observacionales básicos. Localizar variables/factores relacionadas con nuestras variables de interés. Elaborar modelos predictivos
- Programa formativo:
12 de septiembre (jueves), 9:00-12:00 (JM Conde). Presentación del curso. Estadística básica. Diseño experimental. Pseudoreplicación y pseudofactorialismo. Tipos de datos.
12 de septiembre (jueves), 12:30-14:30 (Antonio Jesús Muñoz Pajares). Estadística básica. Introducción a R. Correlaciones paramétricas y no paramétricas.
13 de septiembre (viernes), 9:00-11:00 (MM Rueda). Inferencia básica. Problema de una muestra. Problema de dos muestras independientes y apareadas. Contrastes paramétricos y no paramétricos para una y dos muestras.
13 de septiembre (viernes), 11:30-13:30 (F Torres): Modelos lineales generales: Regresión lineal simple. Ajuste e interpretación de resultados. Predicción. Calibración lineal. Contraste de linealidad para datos repetidos. Comprobación de asunciones.
18 de septiembre (miércoles), 9:00-11:00 (F Torres): Modelos lineales generales: Regresión lineal múltiple. Ajuste e interpretación de resultados. Restricciones lineales. Selección de regresores.
18 de septiembre (miércoles), 11:30-13:30 (MM Rueda): Modelos lineales generalizados: variables explicativas cuantitativas. Regresión logística binomial y multinomial. Selección de regresores. Regresión de Poisson.
20 de septiembre (viernes), 9:00-11:00 (AM Aguilera): Análisis de datos categóricos. Independencia y asociación en tablas bidimensionales.
20 de septiembre (viernes), 11:30-13:30 (AM Aguilera): Análisis de datos categóricos. Independencia condicional y asociación parcial. Metodología de Mantel-Hanzel.
26 de septiembre (jueves), 9:00-11:00 (J Lorite): Diseño de experimentos y análisis de la varianza (ANOVA). Diseños completamente aleatorizados. Diseños en bloques. Cuadrados latinos y grecolatinos. ANOVA paramétrico.
26 de septiembre (jueves), 11:30-13:30 (J Lorite): Diseño de experimentos y técnicas Anova asociadas. ANOVA de medidas repetidas. Diseños anidados.
27 de septiembre (viernes), 9:00-11:00 (Antonio Jesús Muñoz Pajares): Contrastes múltiples no paramétricos. Muestras independientes: Análisis de Kruskal-Wallis. Muestras dependientes: Análisis de Friedman y Prueba de Cochran.
27 de septiembre (viernes), 11:30-13:30 (JM Conde): Modelos lineales: variables explicativas cuantitativas y cualitativas. ANCOVA. Modelos y selección de modelos: AIC y AICc.
4 de octubre (viernes), 9:00-11:00 (R Rubio): Correlación y regresión de matrices de distancia. ¿Qué es una matriz de distancia? Análisis espacial: Análisis de Mantel simple.
4 de octubre (viernes), 11:30-13:30 (R Rubio): Correlación y regresión de matrices de distancia. Análisis de mantel parcial. Regresión múltiple de matrices (MRM).
Otras actividades: De manera no presencial, los alumnos irán trabajando con ficheros de datos de sus Tesis doctorales (si aún no dispusieran de ellos, se les entregarían ficheros de datos). Desde el 9 de octubre hasta el 15 de noviembre de 2019, se llevará a cabo la supervisión del trabajo de los alumnos de forma personalizada. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado según las afinidades previamente establecidas el 8 de octubre de 2019.
Magnetic field effects on water and aqueous solution of surfactants
- Prof. Emil CHibowski, Department of Physical Chemistry – Interfacial Phenomena, Faculty of Chemistry, Maria Curie-Sklodowska University, Lublin, Poland.
- Room M01, Faculty of Sciences, Thursday June 27, 2019, 12.00
- Organized by PhD Programme in Physics and Space Science
- Abstract. The effects of magnetic field (MF) on water treatment have been studied for over a half century in various aspects and they still attract many researchers. Originally the studies were focused on protection of industrial installations or home heating systems against hard scale formation at elevated temperatures. Later on and up to now, the MF effects in the liquid phase have been studied in various fundamental aspects, as well as possible practical applications. Nevertheless, some of the results are still debatable or even incompatible. Among various investigated MF effects a number of papers deal with the pure water, where the changes in its evaporation rate, surface tension, viscosity and other parameters have been observed. The authors reported an increase in water evaporation rate caused by MF which depended also on the experiment setup used. However, only few papers have been published which deal with the investigations of magnetic field effects on the systems in which a surfactant was present. On the other hand, surfactants are present in the surface and waste waters, soil, and many industrial waters, sewage treatment plants, laundry, etc. Therefore it seemed to us interesting to learn whether MF effects would appear in the aqueous solution of surfactants and whether any differences would be observed for an anionic and cationic surfactant solution. Moreover, the question was whether in natural laboratory environment the effects would be reproducible for a possible practical applications. The presented results show the effects of static MF on the changes of water rate evaporation and the surface tension from pure water, as well from the anionic and cationic surfactant solutions. Possible explanation of the observed changes will be discussed based on Gibbs’ adsorption equation and Lorentz force in a gradient MF. Nevertheless, the results are somehow preliminary ones and the hypotheses have to be verified by more systematic studies. Because so far no MF effects dealing with the surfactant solutions were published, hence there are no data for a comparison. Therefore more experiments are needed to better understand the observed changes.
Emil Julian Chibowski was born on May 14, 1943 in the Podlasie region of the Lublin district. In 1989 Emil Chibowski obtained scientific degree ‘professor of chemistry’. Then in 1993 he was nominated as a head of the Department of Physical Chemistry, which was later renamed as the Chair of Physical Chemistry and constituted of four Departments and he hold this position until 2012. Professor Emil Chibowski until now continues his researches in the Department of Interfacial Phenomena. Generally, he focuses his investigations on the interfacial phenomena occurring at solid/liquid, liquid/gas and liquid/liquid interfaces, involving electrochemical phenomena, intermolecular and interfacial interaction, floatability of minerals, wettability and adhesion, contact angles and contact angle hysteresis, surface free surface energy and its components of solids, stability of dispersed systems, emulsion stability, influence of the external radio-frequency and magnetic electric fields on the properties of dispersed systems, effects of solid surface plasma treatment, and superhydrophobic surfaces. Professor Emil Chibowski is author of 233 research papers published mostly in international top journals, including five chapters in books, of which over 60 are joined papers with foreign co-authors.
- Certificate of attendance will be issued. Contact:
Seminario Pathways towards a sustainable solution of climate change
- 10 de septiembre de 2019, 11:00, Sala Eniac (Edificio Mecenas). Esta sala tiene capacidad para unas 100 personas.
- Ponente: Dr. Ivan Janssens. Ivan Janssens se doctoró en biología en la Universidad de Amberes (1999), donde es profesor en el grupo de investigación de ecología de las plantas desde 2003. Lidera el Centro de Excelencia denominado “Ecología del Cambio Global” y dirige un grupo de investigación en procesos edáficos, la biogeoquímica de los ecosistemas, los balances de gases de efecto invernadero, y la respuesta de los ecosistemas al cambio climático y a la contaminación atmosférica. Esta investigación está equilibrada entre trabajo experimental (manipulaciones, trabajo de campo), y modelización y síntesis de bases de datos globales. Ha publicado 240 artículos, sobre todo en Global Change Biology (n=38) y Agricultural and Forest Meteorology (n=20), pero también en revistas muy impactantes como del grupo Nature, Science, y PNAS (n=32). Ha recibido más de 18000 citas (2500 en 2017), con 37 de sus artículos citados más de 100 veces; su índice-H es de 59 (WoS). Desde 2013, ha recibido más de 10M€ en financiación, y actualmente disfruta de un ERC Synergy Grant (3.6M€; sept 2014 – agosto 2020). Es editor de varias revistas de alto impacto, y es altamente activo en actividades de transferencia, y de dirección de numerosos doctorandos. https://www.uantwerpen.be/en/staff/ivan-janssens
- Dirigido a Alumnos de doctorado de EDCTI y personal investigador en general.
- Contenido: In this presentation, Ivan Janssens will provide an overview of the impact on society and the Earth of 1.5°C versus 2°C warming. He will then present the main issues that need to be overcome in order to achieve the Paris agreement's warming target of 2°C, and introduce the new ambitious proposal by the European Commission for a climate-neutral Europe by 2050.
- Programa: Charla de una hora, más sesión de preguntas. La actividad se desarrollará en inglés
- No es necesaria inscripción previa. La entrada al taller es libre hasta completar aforo (100 plazas).
NO SE EMITIRÁ CERTIFICADO DEL CURSO A LOS ASISTENTES.
- Contacto: Andrew Kowalski (Departamento de Física Aplicada; --LOGIN--46b8c5d0f3f3cf6d5511ba9da7bf2d59ugr[dot]es )
Taller de escritura de textos científicos con LaTeX y control de versiones con Git(2018)
- Profesorado y contacto: Miguel Burgos Poyatos. Dpto. de Genética. Facultad de Ciencias.Email: --LOGIN--1d0e97490c9df16aec1f7b4944313e5eugr[dot]es .
- Duración del curso (horas teóricas/prácticas): 20 horas presenciales y 20 no presenciales.
- Calendario y horario: Durante el curso 2018/19 se imparte los siguiente días: Abril: lunes 22 (biblioteca del Dpto. de Genética), miércoles 24 y viernes 26 (aula G22), lunes 29 (Aula MS2). Mayo: viernes 3, lunes 6 y miércoles 8 (biblioteca del Dpto. de Genética) de 11:00 a 14:00 todos los días. Los horarios se encuentran publicados en la Web: http://doctorados.ugr.es/biologiafundamentalydesistemas/pages/nuevo/actividadesi#latex
- Material necesario: Ordenador portátil.
- Plazas y perfil (año de matriculación en doctorado): 15 plazas. Es posible inscribirse durante cualquier año del doctorado. El taller está abierto tanto a doctorandos, tanto a tiempo completo como parcial, como a sus directores y profesores del programa ya que se aprende a realizar el trabajo de forma colaborativa con Git.
- Necesidad de acreditación de conocimientos previos: No es necesario acreditar conocimientos previos
- Evaluación: Los alumnos crean un repositorio Git para el curso en http://Bitbucket.org donde trabajan durante todo el taller y lo comparten con el profesor que, de esta forma puede seguir todo el trabajo que realizan los alumnos tanto durante las horas presenciales como en las no presenciales. Además, un Foro en la plataforma MOODLE (http://mendel.ugr.es/genetica/course/index.php?categoryid=14) permite la comunicación entre todos los participantes y la resolución de dudas y cuestiones de forma abierta y visible para todos los alumnos. Al final del taller el repositorio deberá contener la presentación de un texto científico que incluya bibliografía y diversos tipos de índices así como el historial de cambios de los archivos generados y situados bajo el control de Git. Siendo evaluado por el profesor responsable de la actividad.
- Inscripción: Durante el curso 2018-19 y anteriores los alumnos se han inscrito en una plataforma Moodle del Departamento de Genética donde se encuentra alojado todo el material del curso: http://mendel.ugr.es/genetica/course/index.php?categoryid=14
- Justificación académica: El taller está directamente enfocado a la escritura de la Tesis Doctoral. Los alumnos aprenden a utilizar el sistema de composición de textos LaTeX para escribir textos científicos, manejo automático de la bibliografía, y generar documentos en distintos formatos a partir del código fuente. Asimismo aprenden a utilizar el sistema de control de versiones Git, que resulta de especial interés para la administración de trabajo colaborativo, como la redacción conjunta de artículos de investigación o las correcciones de la memoria de la Tesis doctoral por parte de sus directores, por lo que es recomendable que tanto alumnos como sus directores asistan conjuntamente a este taller.
- Objetivos educativos, profesionales y competencias generales adquiridas: Los alumnos aprenderán a utilizar LaTeX, no solo para la escritura de su teis doctoral, sino también para la confección de pósters para Congresos a los que puedan presentar los resultados de su tesis, y también aprenden a generar documentación con membrete, espacio para firma, etc. que le es de utilidad para la gestión de su estancia en el programa. Aprenden que TeX es un sistema de preparación de documentos creado por Donald E. Knuth. TeX no es un procesador de textos tradicional, sino que mas bien se parece a un lenguaje de programación. En lugar de ver nuestro documento tal como se verá impreso, debemos crear un archivo con instrucciones sobre como queremos que nuestro documento se vea. TeX utiliza un formato abierto. De hecho, los documentos en TeX son archivos de texto, que se pueden editar con nuestro editor favorito, y procesar con herramientas estándar. TeX es multiplataforma: se puede utilizar en GNU/Linux, MS-Windows (Miktex) o Mac OS. Existen varios dialectos de TeX (o mejor dicho distintos paquetes de macros) tales como plain TEX(TeX sin agregados). LaTeX, paquete de macros creado por Leslie Lamport. AmsTeX, dialecto de TeX creado por la A.M.S. (American Mathematical Society). AmsLaTeX (extensión de LaTeX de la AMS). LaTeX se puede extender mediante el uso de paquetes. Durante el taller se utiliza BibTeX, que es un paquete que permite manejar la bibliografía. Las bases de datos de bibliografía se mantienen con Jabref que es un programa capaz de exportar bases de datos de bibliografía a formato bibtex. Además, la tutela de los alumnos se extiende frecuentemente hasta varios años una vez realizado el curso ya que la escritura de su tesis suele realizarse varios años después de asistir al curso, y se les proporciona soporte y ayuda durante todo este tiempo. El taller se complementa con un curso en una plataforma MOODLE propia (mendel.ugr.es/genetica/course/index.php?categoryid=14) En donde se incluyen todos los contenidos e información adicional.
- El alumno sabrá:
• Construirse un entorno de trabajo eficiente mediante el uso de diferentes herramientas informáticas • Dar formato a un documento LaTeX mediante el uso de paquetes y comandos en el preámbulo del documento. • Un conjunto de comandos y entornos de LaTeX que le permitirá la redacción de sus tesis doctoral y, por tanto cualquier otro documento científico. • Un conjunto de comandos de Git necesario para la gestión de versiones de su trabajo. • Un conjunto básico de órdenes de Bash para realizar las operaciones más comunes destd el terminal de Git. • Manejar bases de datos de bibliografía, importando citas directamente desde internet e incluirlas de forma automática en el texto y la lista de bibliografía. • Generar índices automáticos como tablas de contenidos, listas de figuras y de tablas. • Llevar el control de cambios de su trabajo mediante el sistema de control de versiones Git y trabajar con él de forma colaborativa con otras personas. • Algunas normas básicas de tipografía que le permitirán formatear el texto de forma profesional. • Crear pósteres para congresos con LaTeX. • Crear todo tipo de documentos, como cartas con membrete y espacio para firma y distribuir diferentes elementos en posiciones concretas dentro de la página. • Crear presentaciones dinámicas en pdf mediante el uso de beamer. El alumno será capaz de: • Utilizar JabRef para la gestión de bibliografía y su integración con LaTeX mediante el uso del paquete bibtex, así como con el editor utilizado para la escritura dle texto • Manejar el editor TexStudio para la composición de textos con LaTeX pósteres, cartas y todo tipo de documentos. • Moverse desde el terminal de Git por los diferentes directorios de su ordenador y crear direcorios nuevos, renombrar archivos, etc. • Crear todo tipo de documentos que incluyan tablas, grśficos, índices, referencias internas en el documento etc... • Mantener una distribución de LaTeX adecuada para su sistema operativo. • Trabajar de forma colaborativa usando Git como sistema de control de versiones.
Programa formativo (contenidos y horas, por temas/módulos): Bloque 1. Herramientas del curso • Instalación de LaTeX • Instalar LaTeX • The TeXLive Guide • ¿Cómo instalar LaTeX en Windows, Ubuntu y OS X? • The MacTeX Distribution • proTeXt • Editores • TeXworks • TeXstudio (Recomendado para principiantes) • vim (recomendado para expertos) • Instalación de Git • Instalar Git y obtener una cuenta en BitBucket Página • git-cola (un interfaz de git altamente cafeinado) • Manejo de bibliografía • Jabref (BibTeX) • Lista es-tex Bloque 2 • Introducción a vim • Vim: Referencia rápida (por Joaquín Ataz López) • Breve tutorial de vi/vim • Vim ’Cheat Sheets’ • Ejemplo de .vimrc Bloque 3 • Sesión de trabajo con git • Tutoriales de Git • git - the simple guide • Curso gratuito de Git en Udemy Bloque 4 • Manuales de LaTeX • LaTeX para humanidades • La Introducción no tan corta a LaTeX • Estructura de un documento LaTeX • Organización del documento • Comprehensive latex symbol list • detexify Bloque 5 • Tablas • Tablas en colores • Manual sobre tablas • Figuras Bloque 6 • Entornos matemáticos • speadtab (hojas de cálculo simples en LaTeX) Bloque 7 • Base de datos BibTex • Estilo de bibliografía • Preparar el archivo tex para el uso de bibliografía • Citar artículos dentro del texto • Manejar la Bibliografía con JabRef • Insertar citas desde JabRef • Estilos de bibliografía de revistas Bloque 8 • Manual de beamer • Tutorial de beamer • Otro tutorial • Tutorial en Inglés • Galería de temas • Temas de Beamer en una tabla • Beamer en CTAN • Temas de usuarios • Algunos temas de powerpoint hechos en beamer • Un tema moderno minimalista • Ejemplo de uso del tema minimalista • Colección de enlaces a más temas • Ejemplo para practicar Bloque 9 • Compilar con rubber • Compilar con cmake • Plantilla para tesis • Ejemplo de póster • Ejemplo de carta • Calendario • a0poster • a0size Bloque 10 • Catálogo de fuentes • Paquetes para cargar fuentes • Ejemplos de Fuentes (tex) • Ejemplos de fuentes (pdf) • Importar fuentes TrueType a LaTeX • Importar fuentes TrueType en LaTeX(2) • tex fonts cheat sheet • Cambiar nombres de índices y bibliografía
Advanced courses in Biomathematics & Life Sciences
La actividad se compone de cuatro cursos, cada uno compuesto de 3 horas de exposición de resultados junto con dos horas de tutorías y discusión y evaluación propuestas de investigación.
La actividad se desarrollará en inglés y está dirigida a estudiantes de doctorado interesados en biomatemáticas, biofísica modelado de ecuaciones en derivadas parciales (EDP) y análisis de EDP.
Programa:
- Tomás Alarcón, CRM-Barcelona (Spain). An introduction to the mathematical modelling of epigenetics
- Vincent Calvez, U. Lyon (France). Asymptotic methods in evolutionary biology
- Miguel Ángel Herrero, U. Complutense Madrid (Spain). Populations, decisions, algorithms
1. Immune response: emergent properties resulting from individual decisions
2. The advantages of knowledge: model - driven vaccine design
3. The algorithmic nature of bone remodeling
- Christina Surulescu, TU Kaiserslautern. Mathematical modeling of cancer invasion: The influence of the tumor microenvironment.
Los cursos se celebrarán en el aula de FisyMat de la Facultad de Ciencias entre los días 12 y 14 junio de 2019.
Contacto: Juanjo Nieto (email: --LOGIN--eba634be1a5e32535e9e3fb30f0b1c74ugr[dot]es ).
Forma de inscripción y más información:
IV Edición del curso: Técnicas de Caracterización
Fecha: 3 al 5 de Junio de 2019
Plazo de inscripción: 17 al 26 de Mayo de 2019
Horario y lugar de celebración:
| Fecha | Horario | Lugar |
|---|---|---|
| Lunes 3 de junio | de 9h a 14h de 16h a 20h | Aula G22 (Facultad de Ciencias) |
| Martes 4 de junio | de 9h a 14h de 16h a 20h | Aula G22 (Facultad de Ciencias) |
| Miércoles 5 de junio | de 9 h a 14h de 16 a 20 h | Aula G22 (Facultad de Ciencias) |
Número de plazas: 20.
Dirigido a: doctorandos de todos los programas de la EDCTI
Forma de inscripción: Rellenar el siguiente FORMULARIO
Duración: 20 horas.
Para cualquier información contactar con Prof. Antonio Rodríguez Diéguez (antonio5@ugr.es) o Francisco Carrasco Marín (fmarin@ugr.es). Departamento de Química Inorgánica, Universidad de Granada.
La información se actualizará en la página del Programa de Doctorado en Química: http://doctorados.ugr.es/quimica
El Programa de Doctorado en Química y la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías organizan este curso para alumnos pertenecientes a cualquiera de los programas de doctorado de la Universidad de Granada. El objetivo del mismo es dar a conocer al alumno las principales técnicas de caracterización químicas y biológicas, que serán fundamentales para el desarrollo de sus correspondientes trabajos de investigación científica.
PROGRAMA
1. TÉCNICAS DE CARACTERIZACIÓN ESTRUCTURAL. DIFRACCIÓN DE RAYOS X. Preparación de la muestra. Difracción de rayos X en polvo. Difracción de Rayos X de monocristal. Programas para resolución estructural. Wingx, un interfaz veloz para la resolución. Mercury, análisis fiable estructural. Pov-ray, el diseño a la vanguardia.
2. CARACTERIZACIÓN INTEGRAL DE MATERIALES NANOESTRUCTURADOS. Orden mesoscópico en difracción de rayos X de polvo. Adsorción de gases inertes y tipos de isotermas. Composición y comparación de técnicas para la determinación de componentes elementales. Técnicas termogravimétricas para la cuantificación de carga en materiales funcionalizados. Técnicas de microscopía e imagen. Determinación de morfología y tamaño de partícula.
3. CARACTERIZACIÓN DE QUÍMICA SUPERFICIAL DE MATERIALES NANOESTRUCTURADOS. Movilidad electroforética. Propiedades ácido-base superficiales. Espectroscopia infrarroja (FTIR). Microcalorimetría de inmersión. Hidrofobicidad. Desorción a Temperatura Programada / espectroscopia de desorción térmica. Espectroscopia de fotoelectrónica de rayos-X (XPS).
4. CARACTERIZACIÓN FÍSICO-QUÍMICA DE CATALIZADORES. Conceptos generales. Porosidad y distribución de tamaños de poros -Fisisorción de gases a baja temperatura y porosimetría de mercurio-. Dispersión y naturaleza de la fase activa -Difracción de rayos-X, quimisorción, microscopía electrónica de transmisión, espectroscopia fotoelectrónica de rayos-X y reducción u oxidación a temperatura programada-. Determinación de la química superficial mediante moléculas sonda. Otras técnicas de caracterización.
5. CARACTERIZACIÓN DE NANOPARTÍCULAS. Panorámica general de las técnicas de análisis de nanopartículas (espectroscópicas y no espectroscópicas). Tamaño y distribución de tamaños: microscopía y medidas de dispersión de luz (Dynamic Light Scatetring y Nanoparticle Tracking Analysis). Técnicas espectroscópicas. Técnicas de separación (Cromatografía líquida (HPLC), Cromatografía de exclusión por tamaño (SEC), Hidrodinámica de flujo asistido (FFF)). Como abordar un problema en nanotoxicología: aspectos claves a tener en cuenta en un diseño experimental.
6. TÉCNICAS DE CARACTERIZACIÓN CELULAR. Características físico-químicas de las células. Cultivo celular y alteraciones fisiológicas en las membranas (pH, estrés oxidativo). Ensayos para la determinación de la citotoxicidad de un compuesto (Ensayo de reducción del MTT, XTT y MTS, Tinción con resazurina, Tinción con DAPI, Separación celular por citometría de flujo). Distribución intracelular de un compuesto mediante técnicas de microscopía de fluorescencia (Microscopía de epifluorescencia, Medida intracelular de iones (Ca2+, Fe2+) mediante sondas fluorescentes, Fluorescencia de reflexión interna total (TIRF), Inmunofluorescencia, Microscopía confocal). Técnicas de separativa (Tipos de cromatografía). Análisis y cuantificación de imágenes mediante el uso del image-J.
Profesorado: Antonio Rodríguez Diéguez. Alfonso Salinas Castillo. Luisa María Pastrana Martínez. Sergio Morales Torres. María Belén Fernández López. María Camprubí Robles. Santiago Gómez Ruiz.
Seminarios de formación en TIC 2019
+Info web del PD TIC
- Javier Pérez Florido (Universidad Pablo de Olavide)
- Título: Hacia la medicina personalizada en el sistema andaluz de salud
- Resumen
En 2011, la comunidad de Andalucía lanzó el primero proyecto genómico de España, el Proyecto Genoma Médico. Más de 1000 exomas entre controles sanos y pacientes de más de 30 enfermedades fueron secuenciados, adquiriendo una enorme experiencia en la gestión, manejo y análisis de datos genómicos. Esta experiencia en combinación con la mayor población de Europa (8'5 millones de personas) cubierta por una historia digital de salud, ha promovido recientemente la iniciativa andaluza de medicina personalizada. La novedad de esta iniciativa radica en la implementación de herramientas bioinformáticas dentro del sistema corporativo del servicio andaluz de salud (SAS) para unir los datos genómicos con la historia clínica del paciente. De esta forma, el sistema corporativo del SAS se convierte en un inmenso estudio clínico prospectivo en el que datos genómicos y datos de pacientes se van acumulando con el paso del tiempo, pudiendo ser explotados por sistemas inteligentes.
Para este fin, se está desarrollando el módulo de medicina personalizada (MMP) y su introducción en el sistema corporativo del SAS. MMP es una herramienta web que permite un diagnóstico semi-automático de enfermedades de origen genético y que está construido sobre tres importantes proyectos software: openCGA, Cellbase e IVA, utilizados en el proyecto de los 100.000 genomas de Reino Unido y desarrollados entre el área de bioinformática clínica de Andalucía y la Universidad de Cambridge.
- Justificación de su interés general
Esta charla está indicada a estudiantes de doctorado relacionados con las TIC en general. Se abordarán las diferentes etapas de análisis de datos genómicos provenientes de tecnologías de secuenciación masiva, así como las herramientas software desarrolladas para el diagnóstico genético y basadas en sistemas inteligentes, escalables y de alto rendimiento.
- Fecha: 29 de abril de 2019, a las 12:30h. Lugar: Sala de Conferencias del CITIC-UGR.
- Gregorio Sainz Palmero (Universidad de Valladolid)
- Título: Inteligencia Artificial y Construcción: nuevas oportunidades y retos.
- Resumen y justificación
La introducción de IA& ML en el dominio de la construcción está abriendo un amplio abanico de oportunidades de I+D+I y transferencia en un sector, como es el de la construcción, con un fuerte impacto económico y social no solo en España, sino también a nivel internacional, que además funciona de tractor de otros sectores industriales.
La búsqueda de mejoras en los procesos mediante estas tecnologías, y en general, en todo la actividad del sector, muy variada y amplia desde el punto de vista industrial y tecnológico, hace que sea un sector de futuro prometedor para la IA&ML.
Hasta el momento la penetración de estas técnicas en este sector de actividad ha sido muy limitado, lo que hace que existan buenas perspectivas de nuevas oportunidades tanto en la actividad I+D+I, como para los futuros investigadores involucrados tanto en IA& ML, como en ingeniería civil, construcción, etc...
- Fecha: 30 de abril de 2019, a las 12:30h. Lugar: Sala de Conferencias del CITIC-UGR.
- Manuel Muñoz Megías (Civica Software)
- Título: Pasado, presente y perspectivas del Big Data... ¿tiene futuro Hadoop?
- Resumen
Han pasado 10 años desde la irrupción de Hadoop en el panorama tecnológico. En una era donde los datos son un activo muy valioso y una ventaja competitiva clara, las empresas se están enfrentando al completo reto de obtener, manejar, gobernar y extraer valor real de una creciente cantidad de datos (de muy distinta naturaleza). Hadoop apareció como una promesa que iba a solucionar este problema... ¿ha sido así realmente? ¿Cuál es la situación actual de este ecosistema y como se prevé su evolución futura?
- Justificación del interés
El ecosistema Hadoop está compuesto por múltiples tecnologías relacionadas entre sí. Es complejo el mero hecho de conocerlas, evaluar su uso potencial, ventajas e inconvenientes, alternativas,... etc. Además de lo anterior, han surgido diversas tecnologías alternativas que complementan o compiten con las propuestas del ecosistema Hadoop. ¿Cuál debe ser la elección de una empresa ante este escenario tan abierto? ¿Podemos anticipar cual será la evolución futura de este escenario?
- Fecha: 2 de mayo de 2019, a las 12:30h. Lugar: Sala de Conferencias del CITIC-UGR.
- Claudia Villalonga Palliser (Universidad Internacional de la Rioja)
- Título: H2020 SME Instrument: Visión de una evaluadora
- Resumen
Europa necesita innovaciones radicales que permitan crear nuevos mercados, mejoren la productividad y la competitividad de las empresas, generen nuevos puestos de trabajo y ayuden a incrementar la calidad de vida de las personas. Para ello la Comisión Europea, dentro del programa de trabajo Horizon 2020, desarrolla una iniciativa llamada EIC Accelerator pilot (SME Instrument). Esta iniciativa proporciona financiación a startups y PYMES con un alto perfil innovador, que tienen una idea disruptiva y pretenden llevarla al mercado. Estas ideas que suelen implicar un alto riesgo y tienen un alto potencial deben permitir la creación de nuevos productos, servicios o modelos de negocio.
En esta charla se va a presentar la visión de una evaluadora de propuestas del EIC Accelerator pilot (SME Instrument).
* Justificación de su interés general
Para los doctorandos TIC esta charla puede ser interesante si pretenden crear su propia empresa o startup al concluir su doctorado y así llevar al mercado alguna de las ideas innovadoras que están desarrollando en su tesis.
* Fecha: 7 de mayo de 2019, a las 12:30h. Lugar: Sala de Conferencias del CITIC.
- Raquel Hervás Ballesteros (Universidad Complutense de Madrid)
- Título: Tecnologías lingüísticas aplicadas a la accesibilidad con un enfoque centrado en el usuario
- Resumen
Los avances actuales en el campo de las tecnologías lingüísticas están teniendo un alto impacto en distintos ámbitos de la sociedad. Desde los asistentes personales hasta la manipulación de noticias, estas herramientas están cambiando la forma en la que nos comunicamos y vivimos nuestro día a día. Entre estos ámbitos está el campo de la accesibilidad. Uno de los grandes obstáculos que encuentran las personas con discapacidad es la dificultad de comunicación, ya sea por la imposibilidad de uso del lenguaje natural, o por las dificultades de comprensión del mismo. El amplio abanico de tecnologías lingüísticas disponibles en la actualidad puede en este sentido mejorar la comunicación de este colectivo y mejorar su vida diaria. En esta charla veremos cómo algunas de estas tecnologías lingüísticas pueden tener un impacto en el desarrollo de herramientas de apoyo para personas con discapacidad. En estos desarrollos tiene gran importancia la adopción de metodologías centradas en el usuario, siempre adaptadas al marco concreto de la discapacidad.
- Justificación de interés general
La charla es altamente transversal ya que cubre tres áreas de investigación con gran interés en la actualidad: el procesamiento de lenguaje natural, la accesibilidad y el diseño centrado en el usuario. En la charla se verá a alto nivel cuál es el estado actual de cada una de ellas, y cómo las sinergias entre las mismas permiten el desarrollo de herramientas de apoyo para el colectivo de las personas con discapacidad.
- Fecha: 8 de mayo de 2019, a las 12:30h. Lugar: Sala de Conferencias del CITIC.
- José Carlos Calvo Tudela (Intelligenia)
- Título: Going Global
- Resumen y justificación
En España generamos muchos y muy buenos perfiles basados en el conocimiento, en contraposición al tejido empresarial, que no está tan preparado para absorber y poner en valor dichos perfiles. En cambio ocurre lo opuesto en otros países, donde existe un gran tejido empresarial, pero tienen escasez de talento. Esto es un paradigma muy habitual, ya que cuando hay recursos de sobra, la gente no necesita hacer grandes carreras académicas para prosperar en el ecosistema en el que viven, en cambio cuando el país no es capaz de generar empleo suficiente, las personas tienen a seguir formándose para poder conseguir un futuro.
Debemos aprovechar nuestra coyuntura para hacernos globales. Estas son las grandes variables a nuestro favor:
- Los estudios superiores en España son de alta calidad.
- La formación es muy barata, en contraposición a otros países donde una carrera puede suponer 200.000 €.
- Nuestra cultura (latina - mediterránea) nos permite adaptarnos a la realidad en cada momento, y ser resolutivos.
- Solo nos falta creérnoslo, aprender inglés, y lanzarnos a sacarle provecho a nuestro conocimiento más allá de nuestras fronteras.
- Cuando competimos en mercados más grandes, nuestro talento se pone de manifiesto
- Fecha: 9 de mayo de 2019, a las 12:30h. Lugar: Sala de Conferencias del CITIC.
Asphalt pavement research seminar
Research trends in asphalt pavement engineering; Achievements and future challenges
This seminar has been thought for PhD students that are nowadays conducting research on different aspects of asphalt materials. The seminar has been organized in two days, starting with a lecture in which renowned academic experts with a wide expertise in this field will expose their view on how to face the upcoming challenges in asphalt pavements considering sustainability criteria. After the lectures, the PhD students will have the possibility to briefly present their research work, specially the research methodology in order the get a feedback that might help them to reach the best results possible.
- 3rd June
17:00 – 17:45 Lecture 1. Future trends and challenges in asphalt pavements. Prof. Manfred Partl. Academic Guest of Empa
17:45 – 18:30 PhD students’ Work outreach. Supervised by Prof. Manfred Partl.
- 4th June
17:00 – 17:45 Lecture 2. Improving the sustainability of asphalt pavements. Prof. John Harvey. Department of Civil and Environmental Engineering. University of California.
17:45 – 18:30 PhD students’ Work outreach. Supervised by Prof. John Harvey.
- Venue: Escuela Técnica Superior de Ingeniería de Caminos, Canales y Puertos, C/Severo Ochoa s/n, 18071 Granada.
- Registration. Send an email to Miss Paulina Leiva (pleiva@ugr.es) indicating: name, surname, university where the PhD is registered, and if the PhD is linked to the UGR Civil Engineering Studies Program, SMARTi ETN or SAFERUP ETN. Please do so before the 20th of March. Attendance is free of charge. Total of 15 places.
Writing a research paper in English: strategies and techniques(2018)
- Profesorado: Dra. Pamela Faber Benítez, Catedrática Departamento de Traducción e Interpretación. Universidad de Granada.
- Duración: 31 horas (10 h presenciales + 21 trabajo personal).
- Lugar: Facultad de Derecho (edificio San Pablo, Plaza de la Universidad, s/n) - Aula de informática
- Plazas y perfil: 24 plazas.
Dirigido preferentemente a alumnos/as de segundo año de Doctorado.
Para el buen aprovechamiento los alumnos deben tener un nivel razonable de inglés tanto hablado como escrito (al menos, B2).
Aquellos solicitantes que adjunten al correo de solicitud certificación del nivel de inglés (B2 o equivalente) tendrán preferencia sobre el resto para la participación en el curso.
Primera Edición
Fechas: 11, 13, 14, 18, y 21 de marzo de 2019 de 09:00 a 11:00h
Plazo de inscripción: del 1 al 25 de febrero al de 2019.
Forma de inscripción: Los alumnos deben mandar un email a la Escuela de Doctorado --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es indicando en el Asunto “EDCTI-Writing a research paper in English”.
Segunda Edición
Fechas: 27 al 31 de mayo de 2019 de 09:00 a 11:00h
Forma de inscripción: Durante el mes de abril se solicitará confirmación de asistencia, por correo electrónico, a la lista de suplentes de la edición anterior.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción. IMPORTANTE adjuntar certificado del nivel de inglés (ver apartado “Plazas y perfil”).
* Programa:
1. Introduction.
1.1 English as a lingua franca in the scientific world
1.2 The need to publish
1.3 Types of paper
2. Organization.
2.1 Sections
2.2 Content
2.3 Format and Layout
2.4 Common errors
3. Language.
3.1 Syntax and sentence structure
3.2 Semantics and terminology
3.3 Style and punctuation
3.4 Common errors
Python avanzado para ciencia e ingeniería(2018)
- Profesorado: José Vicente Pérez Peña (UGR)
- Duración: 12 horas presenciales (6 horas no presenciales).
- Fechas:
26 y 28 de Marzo y 2, 4, 9 y 11 de Abril, de 2019 de 16:00 a 18:00h.
- Lugar: Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias).
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
- Inscripción: Los alumnos deben mandar un email a la Escuela de Doctorado --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es indicando en el Asunto “EDCTI-Inscripción curso Python AVANZADO para Ciencia e Ingeniería”.
- Plazo de inscripción: del 7 al 15 de marzo 2019.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad.
Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos.
NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes.
La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos.
Una lista completa de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Manejo de matrices multidimensionales con numpy
2.- Funciones básicas para la creación y utilización de matrices de numpy
3.- Lectura-escritura en disco de datos
4.- Creación y representación de funciones matemáticas
5.- Creación de distintos gráficos con matplotlib
6.- Modificación de símbolos y leyendas
7.- Análisis de imagen con scipy
El alumno será capaz de:
1.- Crear y modificar gráficos
2.- Integrar LaTeX directamente en un gráfico
3.- Representar funciones y resolver ecuaciones matemáticas
4.- Entender la documentación de las librerías de Python
5.- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
- Programa formativo:
Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas. Representación de nube de puntos Representación de histogramas y boxplots. Definiendo colores y símbolos. Añadiendo leyendas y etiquetas. Control de ejes. Representación de múltiples figuras
Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage
Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Introducción a Python: Elementos básicos del lenguaje(2018)
- Duración: 12 horas presenciales (6 horas no presenciales).
- Fechas:
Primera Edición: 5, 7, 12, 14, 19 y 21 de Febrero de 2019, de 16:00 a 18:00h
- Lugar: Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias).
Se necesita portátil propio (Mac o PC).
- Plazas y perfil: 15 plazas/edición. Dirigido preferentemente a alumnos/as de primer año de doctorado.
- Inscripción: del 14 al 27 de enero de 2019 los alumnos deben mandar un email a la Escuela de Doctorado --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es indicando en el Asunto “EDCTI-Inscripción curso Introducción a Python: Elementos básicos del lenguaje”.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
- Justificación académica:
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad.
Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje esté ganando cada vez más popularidad entre científicos e ingenieros.
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
- Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
1.- Los elementos básicos de un lenguaje de programación
2.- Tipos de variables y su manipulación
3.- Manipulación de listas, tuplas y diccionarios
4.- Flujos condicionales if y recursivos for
5.- Funciones básicas del lenguaje
6.- Creación de funciones propias
7.- Control de código y manejo excepciones
El alumno será capaz de:
1.- Crear scripts en python para resolver problemas
2.- Leer y analizar un programa escrito en Python
3.- Manejar los principales entornos de programación con IPython (Spyder y Jupyter)
4.- Leer y escribir datos en ficheros de texto
5.- Diseñar algoritmos para la resolución secuencial de problemas
6.- Depurar programas y reconocer los principales tipos de errores
- Programa:
Tema 1. Introducción (1h) Introducción a los lenguajes de programación Historia de Python Descarga e instalación de anaconda. La consola de Python. Partes principales del IDE Spyder.
Tema 2. Tipos básicos, variables y expresiones (4h) Tipos de datos en Python. Variables, operadores y expresiones. Instalar, importar y utilizar módulos en Python. Listas, tuplas y diccionarios.
Tema 3. Operadores y funciones (4h) Operador lógico if. Bucles for. Bucles while. Creación y utilización de funciones en Python.
Tema 4. Operación de entrada/salida y optimización de código (3h) Lectura de ficheros de texto. Escritura en archivos de texto. Módulos os y sys. Control de ficheros y directorios. Optimización de código. Tipos de errores principales en Python. Control de código y manejo excepciones.
Herramientas de búsqueda y gestión de información para el desarrollo de la Investigación
Profesores: Anne-Vinciane Doucet, Antonio Fernández Porcel, Mª Ángeles García Gil y Esteban López García
Fecha de realización: 5, 6 y 7 de Marzo (PRIMERA EDICIÓN)
Lugar de realización: Biblioteca Derecho (Calle Duquesa)
Horario: de 10 a 13 horas
Plazo de Inscripción: del 18 al 24 de febrero de 2019
Forma de Inscripción: Los alumnos deben mandar un email a --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es indicando en el asunto “EDCTI-Inscripción a curso Herramientas de búsqueda y gestión de información para el desarrollo de la Investigación”. Deberán incluir nombre completo y/o pasaporte o DNI en el texto del mensaje.
Perfil: Dirigido a alumnos/as de primer año.
Nº Alumnos: 30 por grupo
Programa:
- Perfil de investigador:
El perfil de investigador. Utilidad y necesidad.
Necesidad de normalización del nombre de investigador.
- Números de identificación: ORCID, ResearcherID (WoS), Author ID (Scopus).
- Perfil y difusión de la investigación: ventajas y “herramientas”: UGR-Investiga, Google Scholar, Academia.edu, ResearchGate, Dialnet
- El perfil de investigador y la evaluación de la producción científica. ANECA, DEVA y SICA. El CVN.
- Bases de datos:
Bases de datos en Ciencias, Tecnologías e Ingenierías y Ciencias de la Salud: JCR-Science, JCR-Social Science WOS, SCOPUS
Bases de datos en Humanidades, Ciencias Sociales y Jurídicas: JCR-Social Science, Arts and Humanities Citation Index, Dialnet
- Gestores bibliográficos:
Introducción a los gestores bibliográficos
Gestores bibliográficos: Mendeley, Flow, Endnote
Multivariate Exploratory Data Analysis (MEDA)(2018)
Teaching hours: 30
Date: Nov 5th-9th 2018. From 12th until 16th of November the lecturers will be available to solve out doubts about the course.
Place:
- Lunes 5 noviembre: aula de Informática de la Facultad de Trabajo Social (Edificio San Jerónimo) en la segunda planta. En dicha sesión del lunes se informará del lugar de celebración para el resto de días.
Registration date: 05th-24th October 2018
Number of students (max.): 20
How to apply: Students must send an email to --LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es with the subject “EDCTI-Multivariate Exploratory Data Analysis (MEDA)”. It is required basic knowledge on Matlab. Students with a certificate about Matlab knowledge, have to attached it to the application e-mail and they will have preference for the course admission. Also Doctoral students from second or third year will have preference in the admission.
Course Goal
Do you have complicate data? Difficult to understand? With thousands of variables/observations? Or with too little observations? Missing data? Time series? Multiple sources? Do you want to find groups of individuals? Understand variables relations? Classify? Detect anomalies? Predict? The course goal is to introduce the students to very powerful data analysis techniques with which they will be able to better understand the features of their data and how a data set should be treated and analyzed to pursue their specific goals. The course is led by Professor Rasmus Bro, world leading professor on data analysis in biological sciences, and his collaborator at the UGR Dr. José Camacho, specialist on data analysis in Big Data and Cybersecurity.
Teachers
Professor Bro is a prominent figure in the field of data analysis and in particular in multivariate analysis. During the last two decades, Prof. Bro has been a principal actor in the development of multivariate analysis in chemical and biological applications in the chemometrics area, in which according to google scholar is the second top researcher. His vast research work is outstanding, presenting an H index equal to 65. Prof. Bro is the author of the most referenced tutorial of PARAFAC (1933 citations), the developer of an extensively used multi-way version of Partial Least Squares (N-PLS) and co-author of more than 200 publications mainly related to the use of multi-way analysis in real life applications. His contributions to the use of constrained modelling are also very relevant, including the use of sparse methodologies for data analysis, and he has co-authored relevant articles to the problem of data fusion, a main challenge in Big Data analyses. The international influence in the community of his course “Multi-way Analysis” and his monograph “Multi-way Analysis: applications in the chemical sciences” is widely recognized. Prof. Bro has taught courses on data analysis in dozens of public and private organizations around the world. From 2001, he is the head of ODIN, an industrial research consortium offering courses, workshops, international contacts and student collaboration.
José Camacho is an associate professor in the Department of Signal Theory, Networking and Communications and researcher in the Information and Communication Technologies Research Centre, CITIC for its initials in Spanish, and in the Network Engineering & Security Group (NESG), both at the University of Granada, Spain. His research interests include exploratory data analysis, anomaly detection and optimization with multivariate techniques applied to data of very different nature, including industrial processes, chemometrics and communication networks. He is especially interested in the use of exploratory data analysis to Big Data for cybersecurity and networkmetrics.
Examination
Every person analyze their own data under supervision of the teacher and writes a report. The report must be short and concise. A short description of the data and their background must be provided. A short description of aim of the present work must be provided. This aim is not necessarily the overall aim of the project from which the data stem (although this is of course nice). Rather the purpose should be chosen in order to test and evaluate the students’ ability to use the methods taught at the course. It is important to discuss in detail how the models have been critically used for the stated purposes.
| Day 1: PCA (Prof. Bro) | |
|---|---|
| 9:00-9:15 | Welcome (Bro & Camacho) |
| 9:15-10:00 | Introduction and algebra without tears |
| 10:00-11:15 | Principal Component Analysis – PCA |
| 11:15-11:30 | Break |
| 11:30-12:00 | Software introduction (demos/hands-on) |
| 12:00-12:30 | Exercises – PCA |
| 12:30-13:30 | Validation, outliers – PCA |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises – PCA |
| Day 2: PLS (Prof. Bro) | |
|---|---|
| 9:00-9:15 | PCA summary |
| 9:15-10:30 | Multivariate calibration - PLS |
| 10:30-10:45 | Break |
| 10:45-11:30 | Exercises – Multivariate calibration |
| 11:30-13:00 | Validation and outliers incl. exercises |
| 13:00-15:00 | Lunch |
| 15:00-16:00 | Preprocessing and nice to know |
| 16:00-16:15 | Break |
| 16:15-17:45 | Competition! |
| Day 3: MEDA & Big Data | (Dr. Camacho) |
|---|---|
| 9:00-10:00 | Introduction to the MEDA Toolbox |
| 10:00-11:15 | Exploratory Data Analysis: Understanding Observations vs Variables |
| 11:15-11:30 | Break |
| 11:30-12:00 | Anomaly Detection with Multivariate Statistical Monitoring |
| 12:00-12:30 | Exercises |
| 12:30-13:30 | Extensions to Big Data |
| 13:30-15:30 | Lunch |
| 15:30-17:00 | Exercises |
| Day 4: Playing with your data I (Prof. Bro & Dr. Camacho) |
|---|
| Time will be devoted to analyze your own data under the supervision of the course monitors, who will guide you through different analysis techniques to pursue your goals. |
| Day 5: Playing with your data II (Prof. Bro & Dr. Camacho) |
|---|
| Time will be devoted to analyze your own data under the supervision of the course monitors, who will guide you through different analysis techniques to pursue your goals. |
Curso 2017/2018
Curso avanzado de análisis de datos en R
Número máximo de alumnos: 20
Fecha: Septiembre-Octubre 2018 (ver más abajo)
Lugar: Seminario de Matemáticas-2, Facultad de Ciencias
Forma y plazo de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (--LOGIN--522adeff6483f5d2baffecdfddcafe85ugr[dot]es ) indicando en el Asunto “Curso avanzado de análisis de datos en R”.
Plazo de inscripción: 13 de junio a 3 de julio de 2018. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Profesorado
Mohamed Abdelaziz (Dpto. Genética)
José María Conde Porcuna (Dpto. Ecología)
Beatriz Cobo Rodríguez (Dpto. Estadística e I.O.)
Juan Lorite Moreno (Dpto. Botánica)
Antonio Jesús Barrera García (Dpto. Matemática Aplicada, Universidad de Málaga)
Rafael Rubio de Casas (Dpto. Ecología)
Coordinador
José María Conde Porcuna --LOGIN--34ed1bd877cef421e1bb543eb83410ccugr[dot]es
Descripción
El objetivo del curso es que los estudiantes de doctorado que han cursado el Curso Básico de Análisis de Datos en R puedan profundizar en distintos aspectos específicos y avanzados en el análisis de datos que consideren necesarios para el desarrollo de sus Tesis doctorales. En el caso de no haber cursado el Curso Básico de Análisis de Datos en R, los estudiantes deberán tener conocimientos básicos de análisis de datos y haber utilizado con anterioridad el software R.
Programa y Horarios
- 13 de septiembre (jueves), 9:00-9:15 (JM Conde)
Presentación del Curso
- 13 de septiembre (jueves), 9:15-11:15 (B Cobo)
Modelos Lineales Multivariantes
Problema de una muestra.
Problema de dos muestras independientes y apareadas.
Regresión lineal múltiple multivariante.
- 14 de septiembre (viernes), 9:00-11:00 (B Cobo)
Modelos Lineales Multivariantes Diseños multivariantes. Manova
- 14 de septiembre (viernes), 11:30-13:30 (AJ Barrera)
Análisis multivariantes: Técnicas de reducción de dimensiones y Ordenación
Análisis de componentes principales. Análisis factorial. 21 de septiembre (viernes), 9:00-10:00 (J Lorite)
Análisis multivariantes: Técnicas de de reducción de dimensiones y Ordenación
Análisis multidimensional de ordenación espacial (NMDS)
- 21 de septiembre (viernes), 10:00-11:00 (JM Conde)
Análisis multivariantes: Técnicas de de reducción de dimensiones y Ordenación
Análisis de correspondencias (CA)
Análisis de correspondencia corregido (DCA)
- 21 de septiembre (viernes), 11:30-13:30 (J.M. Conde)
Análisis multivariantes: Técnicas de Interpretación.
Análisis de redundancia (RDA)
- 28 de septiembre (viernes), 9:00-11:00 (J.M. Conde)
Análisis multivariantes: Técnicas de Interpretación.
Análisis canónico de correspondencia (CCA)
Análisis canónico de correspondencia corregido (DCCA)
- 5 de octubre (viernes), 9:00-11:00 (R. Rubio)
Contrastes de matrices de distancias.
Análisis de similaridad (ANOSIM)
- 5 de octubre (viernes), 11:30-13:30 (R Rubio)
Contrastes de matrices de distancias.
Procedimiento de permutación de respuesta múltiple (MRPP)
Análisis multivariante de la varianza utilizando matrices (NPMANOVA, adonis)
- 11 de octubre (jueves), 9:00-11:00 (M. Abdelaziz)
Técnicas de clasificación
Árboles de regresión clasificación
Correlaciones de matrices de distancia: Alternativas a Mantel
- 11 de octubre (jueves), 11:30-13:30 (AJ Barrera)
Técnicas de clasificación
Análisis discriminante.
Análisis clúster jerárquico y no jerárquico.
- 19 de octubre (viernes), 9:00-11:00 (M. Abdelaziz)
Modelos mixtos lineales generales y generalizados (GLMM)
Métodos y técnicas de estimación
- 19 de octubre (viernes), 11:30-13:30 (J. Lorite)
Modelos mixtos lineales generales y generalizados (GLMM)
Selección de modelos
Significación de variables aleatorias
- 26 de octubre (viernes), 9:00-11:00 (R Rubio)
Inferencia Bayesiana: Modelos y técnicas de estimación
Introducción a la estadística bayesiana
Utilización de cadenas de Markov Monte Carlo (MCMC)
Información a priori
- 26 de octubre (viernes), 11:30-13:30 (R Rubio)
Inferencia Bayesiana: Modelos y técnicas de estimación
Interpretación
Modelos predictivos
- Otras actividades
De manera no presencial, los alumnos irán trabajando con ficheros de datos de sus Tesis doctorales (si aún no dispusieran de ellos, se les entregarían ficheros de datos).
Desde el 29 de octubre hasta el 14 de diciembre de 2018: Supervisión del trabajo de los alumnos de forma personalizada. Para dicha supervisión y evaluación, los estudiantes serán repartidos entre el profesorado según las afinidades previamente establecidas entre el 29 y el 31 de octubre de 2018.
Evaluación
Se evaluarán los análisis realizados por los estudiantes durante el periodo de supervisión de trabajos y se podrá valorar la actitud en clase y tutorías.
Carga docente
Horas presenciales: 34 horas (28 horas de clases teórico-prácticas + 6 horas tutorías)
Horas no presenciales: 25 horas de estudio/trabajo de los estudiantes y 1 hora tutorías electrónicas.
Curso inmunología frente a microorganismos y activación celular
Destinado a Alumnos de las Escuelas de Doctorado de Ciencias, Tecnologías e Ingenierías y de Ciencias de la Salud.
- Plazas: 40
- Número de horas: 10 horas (durante una semana en horario de tarde)
- Libre asistencia para estudiantes de master, Investigadores, profesores hasta completar el aforo.
- Lugar: Salón actos del CIC Campus de Fuentenueva o Salón de Actos del Edificio Mecenas
- Fecha: Por concretar
Forma y plazo de inscripción
Los alumnos deben mandar un email a la Escuela Internacional de Posgrado (actividadesdoctorado@ugr.es) indicando en el asunto “Curso inmunología frente a microorganismos y activación celular”.
En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según el orden de inscripción.
Profesorado
Ana Margarita Espino, profesora del Departamento de Microbiología, Facultad de Medicina de la Universidad de Puerto Rico, Campus de Rio Piedras. Puerto Rico.
Programa
1) Inmunidad contra los Microorganismos. A) Bacterias Intracelulares • Mecanismos de patogenicidad • Inmunidad innata • Inmunidad adaptativa • Mecanismos de evasión de la respuesta B) Bacterias extracelulares • Mecanismos a través de los cuales causan su patogenicidad • Inmunidad innata • Inmunidad adaptativa • Mecanismos de evasión de la respuesta C) Inmunidad a los Virus • Inmunidad innata y adaptativa • Mecanismos de evasión de la respuesta.
2) Receptores de tipo toll y su role en la inmunidad innata • Origen, estructura y distribución de TLRs • Ligando(s) y antagonistas para cada TLR • Rutas de señalización • TLRs y la susceptibilidad a las enfermedades • Funciones de los TLRs en el sistema nervioso central • Terapéuticas implicaciones de los TLRs.
3) Paradigma de la diferenciación de macrófagos en M1 y M2 • Origen de M1 y M2 y su contextualización inmunológica • Estímulos requeridos para M1 y para M2 • Selección de M1 y M2 en el contexto de las enfermedades infecciosas.
Modelos matemáticos de las Ciencias
- Coordinación: María Victoria Velasco Collado
- Lugar de realización del curso: Sede del IEMATH (Instituto de Matemáticas).
- Dirigido a los alumnos y doctorados de los Programas de Doctorado en Ciencias, Tecnologías e Ingenierías, y extensible a alumnos de programas de máster relacionados.
- Los seminarios se pueden seguir de forma independiente.
- Forma de inscripción: Contactar con la coordinación del curso
Contenido
SEMINARIO 1. MODELOS MATEMÁTICOS Y SU RESOLUCIÓN UTILIZANDO LA TEORÍA DE GRUPOS DE TRANSFORMACIONES 1.1 Selección del modelo matemático 1.2 Clasificar las simetrías de Lie de los sistemas considerados. 1.3 Obtener los sistemas óptimos de subálgebras. 1.4 Determinar las soluciones de similaridad. 1.5 Obtención de los sistemas reducidos. 1.6 Aplicaremos métodos directos de resolución de ecuaciones diferenciales ordinarias.
SEMINARIO 2. MODELOS MATEMÁTICOS EN MEDICINA. 2.1 Desarrollar modelos de crecimiento de neoplasias. 2.2 Desarrollar modelos predictivos de supervivencia y de respuesta al tratamiento. 2.3 Desarrollar modelos de resistencia al tratamiento. 2.4 Ajustar los parámetros a partir de la información biológica disponible. 2.5 Validar y realizar simulaciones numéricas de dichos modelos. 2.6 Realizar estudio teórico de dicho modelo y conocer sus propiedades tales como puntos de equilibrio, tipo de soluciones, etc.
SEMINARIO 3. QUÍMICA MATEMÁTICA. 3.1. ¿Qué es la Química Matemática? Historia Definición Química Matemática 3.2. Relaciones Cuantitativas Estructura Actividad: QSAR 3.3. Teoría de grafos e índices topológicos 3.4. Topología Molecular 3.5. Los modelos matemáticos de la mecánica cuántica
SEMINARIO 4. MODELOS MATEMÁTICOS Y HERRAMIENTAS ESTADÍSTICAS APLICADOS EN QUÍMICA: CONCEPTO DE QUIMIOMETRÍA. 4.1. Optimización de los procedimientos y metodologías de análisis 4.2. Tratamiento de las señales de medida 4.3. Propagación de errores y trazabilidad de la medida 4.4. Validación y calibración de los métodos de análisis 4.5. Concepto de repetibilidad, reproducibilidad y tests de contrates 4.6. Tratamiento multivariante de los resultados 4.7. Definición de pautas de comportamiento de variables/muestras/analitos.
SEMINARIO 5. MODELOS MATEMÁTICOS Y SU APLICACIÓN EN EL CAMPO DE LOS FLUIDOS SUPERCRÍTICOS. 5.1. Termodinámica del equilibrio de fases 5.2. Extracción Supercrítica 5.3. Precipitación Supercrítica.
SEMINARIO 6. MODELOS MATEMÁTICOS DE LA MECÁNICA CUÁNTICA. 6.1. Sobre la formalización matemática de la Mecánica Cuántica. Espacios de Hilbert y álgebras de operadores. 6.2. Las álgebras no asociativas como modelos matemáticos de la Mecánica Cuántica. 6.3. Futuros desarrollos, retos y problemas.
SEMINARIO 7. MODELOS MATEMÁTICOS DE LA GENÉTICA. 7.1. Formalización matemática de las Leyes de Mendel 7.2. Modelos matemáticos algebraicos de la genética mendeliana y no mendeliana 7.3. Modelos matemáticos algebraicos de la Dinámica de poblaciones 7.4. Álgebras Genéticas. 7.5. Álgebras de evolución. 7.6. Interés y conexiones de las álgebras de evolución con distintas ramas de la Matemática y de la Ciencia. Futuras líneas de investigación
SEMINARIO 8. MODELOS MATEMÁTICOS DE LA DINÁMICA DE POBLACIONES. 8.1. Quadratic dynamical systems of bisexual population 8.2. Sex differentiation. 8.3. Dynamical systems generated by quadratic stochastic operators. 8.4. Results and open problems
SEMINARIO 9. ELABORACIÓN DE UNA PUBLICACIÓN CIENTÍFICA EN EL CAMPO DE LA MATEMÁTICA Y MATEMÁTICA APLICADA 9.1. A partir de una temática científica y la elaboración del survey, se enseñará al estudiante a elaborar un artículo científico. 9.2. Resolverá el modelo matemático planteado. 9.3. Seleccionará una revista para la posible publicación del mismo, descargándose los macros de la misma. 9.4. Se le mostrará los pasos que ha de seguir para el envío del artículo.
SEMINARIO 10. ELABORACIÓN DE UN “SURVEY” 10.1. Formulación de hipótesis de investigación 10.2. Diseño de la muestra 10.3. Recolección efectiva de los datos científicos. 10.4. Supervisión del trabajo de campo 10.5. Implementación de los datos 10.6. Análisis de los datos. 10.7. Elaboración del Informe de investigación con la presentación de los hallazgos de la investigación.
SEMINARIO 11. SIMETRIAS DE LIE PUNTUALES PARA PROBLEMAS LINEALES ASOCIADOS A ECUACIONES NO LINEALES INTEGRABLES EN DERIVADAS PARCIALES El método de determinación de las simetrías de Lie puntuales de una ecuación diferencial en derivadas parciales está perfectamente establecido. Igualmente establecido está el procedimiento para la determinación de las reducciones de similaridad asociadas a dichas simetrías. Como es bien sabido, una ecuación diferencial no lineal integrable lleva asociada un problema espectral lineal conocido como par de Lax. En este seminario pretendemos abordar el mucho menos estudiado problema de la determinación de las simetrías del problema lineal asociado a una PDE integrable. 11.1. Descripción del concepto de par de Lax 11.2. Simetrías de un par de Lax isoespectral 11.3. Simetrías de un par de Lax noisoespectral
SEMINARIO 12. SUPERFICIES DE CURVATURA MEDIA CONSTANTE EN ESPACIOS E(k,t) El objeto principal es dar una introducción a la teoría de superficies de curvatura media constante en espacios homogéneos riemannianos 3-dimensionales simplemente conexos con grupo de isometrías de dimensión 4. Dichos espacios están contenidos en una familia E(k,t), que depende de dos parámetros reales k y t, e incluye geometrías de Thurston como los espacios de curvatura constante R3 ,y S3, los productos H2xR, y S2xR, o los grupos de Lie Nil3, SU(2) y SL2 con ciertas métricas invariantes a izquierda. La teoría de superficies de curvatura media constante en E(k,t) es un campo de investigación muy activo que ha recibido una atención considerable durante las últimas décadas. 12.1. Propiedades básicas de los espacios E(k,t) 12.1.1. Clasificación de los espacios homogéneos 3-dimensionales. 12.1.2. Modelos para los espacios E(k,t) y estructuras de submersión de Killing. 12.1.3. Propiedades riemannianas: curvatura, geodésicas e isometrías. 12.1.4. Inmersiones isométricas y ecuaciones de compatibilidad. 12.1.5. Superficies totalmente umbilicales y superficies con curvaturas principales constantes. 12.2. Teoría conforme de superficies de curvatura media constante en E(k,t) 12.2.1. La diferencial de Abresch--Rosenberg. 12.2.2. Superficies invariantes y la clasificación de las esferas de curvatura media constante. 12.2.3. Aplicación de Gauss armónica para superficies de curvatura media crítica. 12.2.4. La deformación isométrica tipo Lawson 12.2.5. La dualidad conforme tipo Calabi. 12.3. Grafos, multigrafos y otras construcciones. 12.3.1. Multigrafos completos con curvatura media constante. 12.3.2. El problema de Bernstein para grafos de curvatura media crítica. 12.3.3. El problema de Jenkins--Serrin para grafos de curvatura media subcrítica. 12.3.4. Un breve recorrido por las superficies de curvatura media supercrítica.
SEMINARIO 13. MODELOS MATEMÁTICOS Y HERRAMIENTAS ESTADÍSTICAS APLICADOS EN FÍSICA 13.1 Conocimiento actual. Medida de datos experimentales. Magnitudes y unidades. Instrumentos de medida. 13.2 Error experimental. 13.3 Análisis de la distribución de datos. 13.4 Test estadísticos. 13.5 Ajuste de ecuaciones de datos experimentales
Programación de sesiones
Cuadro de Profesores por seminario
| SEMINARIO | PROFESOR/ES |
|---|---|
| 1 | Dra. Mª Luz Gandarias y Dra. Mª Santos Bruzón. UCA |
| 2 | Dr. Víctor Pérez UCLM |
| 3 | Dra. Concepción Fernández UCA |
| 4 | Dra. Dolores Galindo UCA |
| 5 | Dra. Clara Pereyra UCA |
| 6 | Dra. Mª Victoria Velasco UGR y Dr. Miguel Bustamente U.C.Dublin |
| 7 | Dra. Mª Victoria Velasco UGR |
| 8 | Dr. Miguel Piñar, UGR y Dra. Teresa Pérez UGR |
| 9 | Dra. Mª Victoria Velasco UGR y Dra. Mª Santos Bruzón de la UCA |
| 10 | Dra. Mª Victoria Velasco UGR y Dra. Mª Santos Bruzón de la UCA |
| 11 | Dra. Pilar García Estévez US |
| 12 | Dr. José Miguel Manzano (King’s College London) |
| 13 | Dr. José Luis Legido UVIGO |
Criterios de evaluación
Procedimientos para la evaluación: 1. Participación. 2. Análisis de contenido de los trabajos individuales y grupales realizados en las clases prácticas, en los seminarios de las actividades de evaluación y tutorías. 3. Otros procedimientos para evaluar la participación del estudiante en las diferentes actividades planificadas.
La calificación global responderá a la puntuación ponderada de los diferentes aspectos y actividades que integran el sistema de evaluación, de manera general se indica la siguiente ponderación, para cada uno de los seminarios: 1. Trabajos individuales y grupales: 40% 2. Prácticas y/o problemas: 30% 3. Actividades en seminarios: 15% 4. Otras actividades: 15%
Metodología
Para desarrollar este proyecto, serán impartidos unos 16 seminarios, de hora y media cada uno, por doctores de prestigio que pertenecen a distintas ramas de las ciencias experimentales, de la salud e ingenierías tales como Biología, Medicina, Química, Física, Informática, Ingeniería Química y Matemáticas. Entre ellos, se incluirá un seminario de carácter eminentemente práctico que versará sobre la elaboración y preparación de un artículo científico para su publicación. Como primera aplicación del mismo se invitará a los alumnos a la elaboración de un survey sobre alguna de las temáticas tratadas en los seminarios. También se tiene previsto la impartición de un seminario sobre las herramientas que se usan en la actualidad para medir los índices de impacto y de calidad de las publicaciones científicas, intentando en la medida de lo posible desvelar buenas prácticas para potenciar la valoración de nuestras publicaciones. La propuesta metodológica de presentación de los contenidos matemáticos de este Proyecto estará basada en el que se denomina modelización matemática como herramienta de enseñanza-aprendizaje y estará centrada en los siguientes puntos:
1. Presentación de una situación simplificada del mundo real.
2. Traducción de la situación en terminología matemática y obtención del modelo.
3. Trabajar sobre el modelo y resolución del problema.
4. Presentación de la solución en términos no matemáticos.
En la actualidad se utilizan los modelos matemáticos en la mayoría de los campos de las ciencias y la ingeniería. Para construir un modelo matemático que simule un problema real hay que recurrir a una serie de hipótesis que describen el fenómeno que se ha de representar. Para resolver el problema se utilizan técnicas matemáticas que conducen a la solución del problema. En algunos casos es posible obtener soluciones analíticas del modelo e incluso se puede realizar un análisis cualitativo de las soluciones analíticas del modelo. En otras ocasiones hay que recurrir a técnicas numéricas que proporcionan una solución aproximada del problema matemático. Los resultados obtenidos analíticamente, numéricamente y experimentalmente se comparan entre sí con objeto de validar las hipótesis sobre las que descansa el modelo. De esta forma se verifica si el modelo es adecuado o no lo es.
Objetivos
- Formar al alumno en el conocimiento de los modelos matemáticos que vienen descritos por ecuaciones diferenciales o datos experimentales.
- Desarrollar y aplicar métodos matemáticos a modelos matemáticos descritos por ecuaciones en derivadas parciales. Acercar al alumno a modelos matemáticos que surgen en otras ramas de las ciencias.
- Interaccionar el intercambio de experiencias metodológicas y la modelización matemática como herramienta de enseñanza-aprendizaje.
- Combinar la experimentación en el laboratorio con herramientas matemáticas, entre los que destaca la combinación de modelización matemática y la simulación numérica.
- Obtener soluciones analíticas y numéricas del modelo. Elaborar un survey.
- Elaborar una publicación.
- Presentar a los alumnos los principales modelos matemáticos de los fenómenos de diversas áreas de las ciencias.
- Presentar a los alumnos los principales modelos matemáticos de los fenómenos químicos.
Bibliografía
• J. M. Smith, H. C. van Ness, M. M. Abbott, Introducción a la termodinámica en Ingeniería Química. McGraw-Hill (1997). • Supercritical Fluid Extraction. En “Separation and Purification Technologies in Biorefineries”, cap. 4, pp. 79-100. S. Ramaswamy, H. Huang, B. Ramarao (eds.). Edita: John Wiley & Sons (2013). ISBN: 978-0-470-97796-5. • Particles formation using supercritical fluids. En: Mass Transfer – Advanced Aspects, cap 20: 461-480. Ed. Hironori Nakajima. Publicado por InTech, Septiembre 2011. ISBN: 978-953-307-636-2 • Advances in Mathematical Chemistry and Applications. Volume 1 y 2. Basak S. C., Restrepo G., Villaveces J. L. (Bentham Science eBooks, 2015) • Molecular Descriptors for Chemoinformatics, by R. Todeschini and V. Consonni, Wiley-VCH, Weinheim, 2009. • Mathematical Chemistry Series, by D. Bonchev, D. H. Rouvray (Eds.), Gordon and Breach Science Publisher, Amsterdam, 2000. • Chemical Graph Theory, by N. Trinajstic, CRC Press, Boca Raton, 1992 • Mathematical Concepts in Organic Chemistry, by I. Gutman, O. E. Polansky, Springer-Verlag, Berlin, 1986. • Chemical Applications of Topology and Graph Theory, ed. by R. B. King, Elsevier, (1983). • A. Ankiewicz, Y. Wang, S. Wabnitz, and N. Akhmediev, Phys. Rev. E 89, (2014), 012907. • F. Calogero, Lett. Nuovo Cimento 14, 443 (1975). • P. G. Estevez, G. A. Hernaez, J. Nonlinear Math. Phys. 8, 106 (2001). • P. G. Estévez, M. L. Gandarias, J. Prada, Phys. Lett. A 343 (2005) 40-47. • P. G. Estévez J. D. Lejarreta, C. Sardón. Integrable 1+1 dimensional hierarchies arising from reduction of a non-isopectral problen in 2 + 1 dimensions, Applied Mathematics and Computation 224 (2013) 311-324. • P.G. Estévez, E. Diaz, F. Dominguez-Adame, Jose M. Cervero, E. Diez. Lump solitons in a higher-order nonlinear equation in 2+1 dimensions, Phys. Rev. E 93 (2016) 062219. • P. G. Estévez J. D. Lejarreta and C. Sardón. Symmetry computation and reduction of a wave model in 2 + 1 dimensions, Nonlinear Dyn. 87 (2017) 13-23. • R. Hirota, J. Math. Phys. 14, (1973), 805. • M. C. Nucci, The role of symmetries in solving differential equations. Math. Comput. Modelling 25, (1997), 181–193. • M. Lakshmanan, K. Porsezian, and M. Daniel, Phys. Lett. A 133, (1988), 483. • M. Legare, Symmetry Reductions of the Lax Pair of the Four-Dimensional Euclidean Self-Dual Yang-Mills Equations. J. Nonlin. Math. Phys. 3 (1996) 266-285. • S. Lie, Theorie der Transformationgruppen. 2, Teubner, Leipzig, (1890) 1 • P. J. Olver, Applications of Lie Groups to Differential Equations, Springer-Verlag, (1993). • L. V. Ovsiannikov, Group Analysis of Differential Equations, Academic Press New York (1982). • H. Stephani, Differential equations: their solution using symmetries. Cambridge University Press, Cambridge, (1990). • U. Abresch, H. Rosenberg. Generalized Hopf differentials. Mat. Contemp. 28 (2005), 1--28. • B. Daniel, L. Hauswirth, P. Mira, Constant mean curvature surfaces in homogeneous manifolds. Notes of the 4th KIAS Workshop on Differential Geometry, Seoul, (2009).
Python avanzado para ciencia e ingeniería
Profesorado
José Vicente Pérez Peña (UGR)
Duración, lugar y fecha
- 12 horas presenciales (6 horas no presenciales).
- 3, 4, 10, 11, 17 y 18 de mayo de 2018 de 16:00 a 18:00 h.
- Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias).
- Se necesita portátil propio (Mac o PC).
Plazas y perfil
15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado con conocimientos de Python.
- Para este curso es necesario acreditar un conocimiento básico del lenguaje Python 3. Con el fin de evaluar los conocimientos de Python requeridos, antes del inicio del curso se realizará un cuestionario online a los solicitantes. Los estudiantes que no superen la prueba, no se admitirán en el curso.
Justificación académica
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad.
Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos. La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes. La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos.
Una lista complete de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
- Manejo de matrices multidimensionales con numpy
- Funciones básicas para la creación y utilización de matrices de numpy
- Lectura-escritura en disco de datos
- Creación y representación de funciones matemáticas
- Creación de distintos gráficos con matplotlib
- Modificación de símbolos y leyendas
- Análisis de imagen con scipy
El alumno será capaz de:
- Crear y modificar gráficos
- Integrar LaTeX directamente en un gráfico
- Representar funciones y resolver ecuaciones matemáticas
- Entender la documentación de las librerías de Python
- Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
Programa formativo
- Tema 1. Manejo de datos con numpy (4h) Constantes y funciones de numpy. Arrays de numpy. Métodos para la creación de arrays. Operaciones con arrays. Indexado y slicing en arrays. Leer y guardar arrays en archivos de texto.
- Tema 2. Representación gráfica con matplotlib (4h) Representación básica de funciones Representación de varias curvas • Representación de nube de puntos Representación de histogramas y boxplots • Definiendo colores y símbolos • Añadiendo leyendas y etiquetas • Control de ejes • Representación de múltiples figuras
- Tema 3. Análisis numérico con scipy (2h) Ajuste e interpolación de datos. Tratamiento multidimensional de imágenes con ndimage
- Tema 4. Breve introducción a cython (2h). Creación y compilación de scripts usando Cython. Elementos básicos del lenguaje. Optimización de código con Cython.
Forma y plazo de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) indicando en el Asunto “Inscripción curso Python Avanzado para Ciencia e Ingeniería”.
Plazo de inscripción: 4-20 de abril de 2018. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Introducción a Python: Elementos básicos del lenguaje
Profesorado
Duración, lugar y fecha
- 12 horas presenciales (6 horas no presenciales).
- Primera Edición: 5, 6, 12, 13, 19 y 20 de Abril de 2018 de 16:00 a 18:00
- Segunda Edición: 4, 5, 9, 10, 11, 12 de Julio de 16:00 a 18:00
- Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias).
- Se necesita portátil propio (Mac o PC).
Plazas y perfil
15 plazas/edición. Dirigido preferentemente a alumnos/as de primer año de doctorado.
Justificación académica
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje este ganando cada vez más popularidad entre científicos e ingenieros
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
- Los elementos básicos de un lenguaje de programación
- Tipos de variables y su manipulación
- Manipulación de listas, tuplas y diccionarios
- Flujos condicionales if y recursivos for
- Funciones básicas del lenguaje
- Creación de funciones propias
- Control de código y manejo excepciones
El alumno será capaz de:
- Crear scripts en python para resolver problemas
- Leer y analizar un programa escrito en Python
- Manejar los principales entornos de programación con IPython (Spyder y Jupyter)
- Leer y escribir datos en ficheros de texto
- Diseñar algoritmos para la resolución secuencial de problemas
- Depurar programas y reconocer los principales tipos de errores
Programa
Tema 1. Introducción (1h) Introducción a los lenguajes de programación Historia de Python Descarga e instalación de anaconda. La consola de Python. Partes principales del IDE Spyder.
Tema 2. Tipos básicos, variables y expresiones (4h) Tipos de datos en Python. Variables, operadores y expresiones. Instalar, importar y utilizar módulos en Python. Listas, tuplas y diccionarios.
Tema 3. Operadores y funciones (4h) Operador lógico if. Bucles for. Bucles while. Creación y utilización de funciones en Python.
Tema 4. Operación de entrada/salida y optimización de código (3h) Lectura de ficheros de texto. Escritura en archivos de texto. Módulos os y sys. Control de ficheros y directorios. Optimización de código. Tipos de errores principales en Python. Control de código y manejo excepciones
Forma y plazo de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) indicando en el Asunto “Inscripción curso Introducción a Python: Elementos básicos del lenguaje”.
Plazo de inscripción: 19 de marzo 2 de abril de 2018. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Aplicaciones de los Sistemas de Información Geográfica a la Planificación Territorial, Urbana e Infraestructural (11/2017 - 12/2018 )
Profesorado
Duración, Lugar y Fechas
- Duración: 24 horas presenciales (6 horas no presenciales)
- Lugar: E.T.S. de Ingenieros de Caminos, Canales y Puertos de Granada
- Fecha: 27, 28, 29 y 30 de Noviembre, 4 y 5 de Diciembre de 2017 de 16:30 a 20:30
Plazas y Perfil
- Plazas: 25 Plazas
- Perfil: Alumnos/as de doctorado de los programas de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías.
Justificación Académica
Las disciplinas que trabajan con el territorio han estado muy vinculadas desde sus orígenes al empleo de diferentes cartografías necesarias para llevar a cabo análisis y diagnósticos territoriales, y para plasmar las propuestas de intervención recogidas en proyectos constructivos o de investigación o en diferentes informes técnicos o documentos y artículos propios del proceso investigador. La utilización generalizada de estas cartografías temáticas ‘en papel’ ha dado paso en los últimos años a una continua digitalización y vectorización de las mismas, generando una cantidad ingente de información cartográfica disponible en diferentes servidores web’s y bases de datos, conformando las llamadas Infraestructuras de datos espaciales (IDEs). Por otro lado, la utilización de esta información requiere de un software específico, los Sistemas de Información Geográfica (SIG), que permita no sólo su visualización, sino también su procesamiento, teniendo éste innumerables aplicaciones. Dada su aplicabilidad a la problemática territorial, en los últimos años el Departamento de Urbanística y Ordenación del territorio de la Universidad de Granada ha comenzado a utilizar software de este tipo en las asignaturas de la titulación de Ingeniería de Caminos, Canales y Puertos. La elección para este curso de dos softwares (QGIS y ArcGIS) pretende que el alumnado se familiarice con la forma de trabajar de los SIG independientemente del software elegido, de código abierto o comercial. Por todo ello, parece imprescindible trasladar a la comunidad académica, por un lado, el acceso a las fuentes de información cartográfica digital más importantes, y por otro, algunas nociones básicas de los programas que permitan su procesamiento, con el fin de mejorar su aprendizaje y hacer más eficiente su trabajo, en parte, por el considerable ahorro de tiempo que supone el empleo de estas TIC’s.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
- Acceder a la Información Geográfica disponible en la IDEs, cartografía vectorial y raster, ortofotografías aérea, Modelos digitales de terreno…
- Gestionar y analizar esta información mediante un SIG libre y SIG comercial.
- Aplicar toda la funcionalidad del motor de geoprocesamiento.
El alumno será capaz de:
- Entender el funcionamiento de un software SIG y sus diferencias con los CAD
- Desarrollar proyectos SIG utilizando información tanto raster como vectorial.
- Realizar salidas gráficas de calidad
Programa
- Base teórica: Conceptos básicos, modelos de datos, cartografía digital, Infraestructuras de Datos Espaciales…
- Introducción a ArcGis: Estructura de la Aplicación.
- Clasificación, simbolización y etiquetado con ArcMap
- Consultas a la base de datos. Selección Espacial.
- Georreferenciación
- Edición de entidades y tablas
- Herramientas básicas de Geoprocesamiento
- Composición de Mapas. Exportación y empaquetado del proyecto.
- Los Modelos Digitales de Terreno. Funcionalidades Raster
- Reclasificación y Superposición. Álgebra de Mapas.
- Análisis de un MDT. Cartografía derivada. Pendientes, orientaciones, cuencas visuales, red de drenaje..
- La aplicación ArcScene. El visor 3D de ArcGis
- Aplicaciones prácticas a la planificación territorial, urbana e infraestructural
- Fuentes de datos primarias. Del Cad al Gis.
- Catálogos y fuentes de datos
- Descarga de datos de la red, acceso remoto a servicios OGC: WMS, WFS, WCS..
- El software Qgis. Diferencias respecto a ArcGis
- Introducción a Qgis. Estructura de la aplicación.
- Activación de proveedores e instalación de plugins
- Clasificación, simbolización y etiquetado con Qgis desktop
- Consultas a la base de datos. Selección espacial.
- Edición de entidades y tablas.
- Herramientas básicas de geoprocesamiento.
- Composición de mapas. Exportación.
- Ejercicios de aplicación.
Evaluación
Se propone una evaluación continua compuesta de:
- Desarrollo por parte del alumno de forma individual, de un caso práctico real de aplicación del software ArcGIS o QGIS.
- Participación y actitud del alumno en las sesiones docentes.
Writing a research paper in English: strategies and techniques (01/2018)
Profesorado
Dra. Pamela Faber Benítez, Catedrática Departamento de Traducción e Interpretación. Universidad de Granada.
Duración, lugar y fecha
30 horas (9 h presenciales + 21 trabajo personal).
Lugar: Facultad de Traductores. Aula 14.
Fechas: 17, 24 y 26 de enero de 2018 de 16:30h a 19:30h.
Plazas y perfil
24 plazas.
Dirigido preferentemente a alumnos/as de segundo año de Doctorado.
Para el buen aprovechamiento de los alumnos, deben tener un nivel razonable de inglés tanto hablado como escrito (al menos, B2).
Programa
1. Introduction.
1.1 English as a lingua franca in the scientific world
1.2 The need to publish
1.3 Types of paper
2. Organization.
2.1 Sections
2.2 Content
2.3 Format and Layout
2.4 Common errors
3. Language.
3.1 Syntax and sentence structure
3.2 Semantics and terminology
3.3 Style and punctuation
3.4 Common errors
Herramientas de búsqueda y gestión de información para el desarrollo de la Investigación (02/2018 - 03/2018)
Profesores
Carmen Domínguez Fernández, Anne-Vinciane Doucet, Antonio Fernández Porcel, Mª Ángeles García Gil y Esteban López García
Fecha de realización
13 a 15 Febrero (PRIMERA EDICIÓN)
20-22 de Marzo (SEGUNDA EDICIÓN)
Plazas y perfil
Dirigido a alumnos/as de primer año.
Nº Alumnos: 30 por grupo
Duración y lugar
Lugar de realización Biblioteca Derecho (Ubicación Calle Duquesa)
Duración: 10-13 horas
Programa
- Perfil de investigador:
- El perfil de investigador. Utilidad y necesidad.
- Necesidad de normalización del nombre de investigador. -Números de identificación: ORCID, ResearcherID (WoS), Author ID (Scopus).-Perfil y difusión de la investigación: ventajas y “herramientas”: UGR-Investiga, Google Scholar, Academia.edu, ResearchGate. Dialnet-El perfil de investigador y la evaluación de la producción científica. ANECA, DEVA y SICA. El CVN.
- Bases de datos:
- Bases de datos en: Ciencias, Tecnologías e Ingenierías y Ciencias de la Salud: JCR-Science, JCR-Social Science WOS, SCOPUS
- Bases de datos en: Humanidades, Ciencias Sociales y Jurídicas: JCR-Social Science, Arts and Humanities Citation Index, Dialnet
- Gestores bibliográficos:
- Introducción a los gestores bibliográficos
- Gestores bibliográficos: Mendeley, Flow, Endnote
Curso 2016/2017
Preparación y elaboración de proyectos (02/2017)
Profesorado Vicerrectorado de Investigación y Transferencia
Duración, lugar y fecha
- Duración: 10 horas
- Lugar: Sala de conferencias del complejo administrativo Triunfo.
- Fechas: 7, 8 y 9 de Febrero de 2017 de 10 a 13 h.
Plazas y perfil
- Plazas: 30
- Perfil: Estudiantes de doctorado de 3º año y egresados recientes
Programa
1. Qué es un proyecto. Fases. Definición de objetivos. Planificación. Control. Justificación.
2. Principales convocatorias de financiación de proyectos de investigación para jóvenes doctores. Plan Estatal y Horizonte 2020.
3. Convocatorias de especialización posdoctoral en el Plan Estatal, Junta de Andalucía y Horizonte 2020.
4. Aspectos esenciales para la presentación de un proyecto con éxito.
5. Caso práctico de discusión y presentación de un proyecto.
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “inscripción a curso Elaboración de proyectos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
- 12 - 21 de enero de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Introducción a Python: Elementos básicos del lenguaje (03/2017)
Profesorado José Vicente Pérez Peña (UGR), Patricia Ruano Roca (UGR)
Duración, lugar y fecha
- 12 horas presenciales (6 horas no presenciales).
- 2, 3, 9, 10, 16, 17 de Marzo. Sesiones Jueves y Viernes de 16:00 a 18:00 h.
- Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias).
- Se necesita portatil propio (Mac o PC).
Plazas y perfil 15 plazas. Dirigido preferentemente a alumnos/as de primer año de doctorado.
Justificación académica Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje este ganando cada vez más popularidad entre científicos e ingenieros
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
Objetivos educativos, profesionales y competencias generales adquiridas El alumno sabrá: • Los elementos básicos de un lenguaje de programación • Tipos de variables y su manipulación • Manipulación de listas, tuplas y diccionarios • Flujos condicionales if y recursivos for • Funciones básicas del lenguaje • Creación de funciones propias • Control de código y manejo excepciones
El alumno será capaz de: • Crear scripts en python para resolver problemas • Leer y analizar un programa escrito en Python • Manejar los principales entornos de programación con IPython (Spyder y Jupyter) • Leer y escribir datos en ficheros de texto • Diseñar algoritmos para la resolución secuencial de problemas • Depurar programas y reconocer los principales tipos de errores
Programa Tema 1. Introducción (2h) • Introducción a los lenguajes de programación • Historia de Python • Elementos básicos de un lenguaje de programación • Descarga e instalación de anaconda con scipy • Python vs IPython • Partes principales de Spider • Introducción a los notebooks de IPython
Tema 2. Tipos básicos, variables y expresiones (4h) • Tipos de datos en Python • Variables, operadores y expresiones • Módulos math y random • Listas en Python • Métodos para la manipulación de cadenas de texto • Tuplas y diccionarios
Tema 3. Operadores y funciones (4h) • Operador lógico If • Bucles for • Bucles while • Creación y manejo de funciones • Ámbito de las variables • Funciones más importantes de Python
Tema 4. Operación de entrada/salida y optimización de código (4h) • Lectura de ficheros de texto • Escritura en archivos de texto • Módulos os y sys • Control de ficheros y directorios • Optimización de código • Tipos de errores principales en Python • Control de código y manejo excepciones
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
- Plazo de inscripción: 13-24 de febrero de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Taller de escritura/elaboración/preparación de un artículo científico (03/2017)
Writing a research paper in English: strategies and techniques
Profesorado Dra. Pamela Faber Benítez, Catedrática Departamento de Traducción e Interpretación. Universidad de Granada.
Duración, lugar y fecha
- 40 horas (10h presenciales + 30 trabajo personal).
- Lugar: Facultad de Traductores.
- Fechas: 13/15/20/22/27 de marzo de 13:00 a 15:00 h.
Plazas y perfil
- 30 plazas.
- Dirigido preferentemente a alumnos/as de segundo año de doctorado.
- Para el buen aprovechamiento de los alumnos, deben tener un nivel razonable de inglés tanto hablado como escrito (al menos, B2).
Programa 1. Introduction. 1.1 English as a lingua franca in the scientific world 1.2 The need to publish 1.3 Types of paper
2. Organization. 2.1 Sections 2.2 Content 2.3 Format and Layout 2.4 Common errors
3. Language. 3.1 Syntax and sentence structure 3.2 Semantics and terminology 3.3 Style and punctuation 3.4 Common errors
4 Strategies 4.1 Making notes 4.2 Keeping track of references 4.3 Translation: problems and pitfalls 4.4 Revising 4.5 Avoiding plagiarism
Competencias CA04 - Trabajar tanto en equipo como de manera autónoma en un contexto internacional o multidisciplinar. CA05 - Integrar conocimientos, enfrentarse a la complejidad y formular juicios con información limitada. CA06 - La crítica y defensa intelectual de soluciones. CB11 - Comprensión sistemática de un campo de estudio y dominio de las habilidades y métodos de investigación relacionados con dicho campo CB14 - Capacidad de realizar un análisis crítico y de evaluación y síntesis de ideas nuevas y complejas. CB15 - Capacidad de comunicación con la comunidad académica y científica y con la sociedad en general acerca de sus ámbitos de conocimiento en los modos e idiomas de uso habitual en su comunidad científica internacional.
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción EDCTI-Writing a research paper in English: strategies and techniques” en el asunto. Debe adjuntarse certificado de nivel de inglés, en su caso.
- Plazo de inscripción: 22 de febrero al 2 de marzo de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Python avanzado para ciencia e ingeniería (03-04/2017)
Profesorado José Vicente Pérez Peña (UGR)
Duración, lugar y fecha
- 12 horas presenciales (6 horas no presenciales).
- 23, 24, 30, 31 de Marzo y 6, 7 de Abril. Sesiones Jueves y Viernes de 16:00 a 18:00 h.
- Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias).
- Se necesita portátil propio (Mac o PC).
Plazas y perfil
- 15 plazas.
- Dirigido preferentemente a alumnos/as de segundo año de doctorado.
Justificación académica Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad.
Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos.
La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes.
La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos.
Una lista complete de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá: • Manejo de matrices multidimensionales con numpy • Funciones básicas para la creación y utilización de matrices de numpy • Lectura-escritura en disco de datos • Creación y representación de funciones matemáticas • Creación de distintos gráficos con matplotlib • Modificación de símbolos y leyendas • Funciones mátematicas de alto nivel y estadística con scipy
El alumno será capaz de: • Crear y modificar gráficos • Integrar LaTeX directamente en un gráfico • Representar funciones y resolver ecuaciones matemáticas • Entender la documentación de las librerías de Python • Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
Programa formativo
Tema 1. Manejo de datos con numpy (5h) • Constantes y funciones de numpy • Arrays de numpy • Métodos para la creación de arrays • Operaciones con arrays • Indexado y slicing en arrays • Leer y guardar arrays en archivos de texto
Tema 2. Representación gráfica con matplotlib (4h) • Representación básica de funciones • Representación de varias curvas • Representación de nube de puntos • Representación de histogramas y boxplots • Definiendo colores y símbolos • Añadiendo leyendas y etiquetas • Control de ejes • Representación de múltiples figuras
Tema 3. Análisis numérico con scipy (3h) • Ajuste e interpolación de datos • Tratamiento multidimensional de imágenes con ndimage
Tema 4. Estadística con scipy (2h) • Estadística básica • Análisis espacial y clúster • Procesado de señales e imágenes
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
- Plazo de inscripción: 1-15 de marzo de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Herramientas para el desarrollo de la Investigación (búsqueda y gestión información científica)
Duración, lugar y fecha 10 horas, CVUG. Del 9 a 11 de Febrero, de 10 a 13 h.
Plazas y perfil 25 plazas. Dirigido preferentemente a alumnos/as de primer año de doctorado
Programa El curso consta de tres módulos.
Perfil del Investigador - Utilidad y necesidad. (Necesidad de normalización del nombre de investigador) (Números de identificación: ORCID, ResearcherID (WoS), Author ID (Scopus)). - Perfil y difusión de la investigación: ventajas y “herramientas”: UGR-Investiga, Google Scholar, Academia.edu, ResearchGate, Digibug, Dialnet. - El perfil de investigador y la evaluación de la producción científica. ANECA, DEVA y SICA. El CVN.
Bases de datos - Web of Science (WOS). - JCR: Journal Citation Reports- Sciences y Social Sciences. - Indice de Artes y Humanidades, Arts and Humanities Citation Index. - Scopus. - Dialnet.
Gestores bibliográficos - Introducción a los gestores bibliográficos. - Refworks/Flow. - Mendeley. - Endnote.
Profesorado
Biblioteca General de la Universidad:
Carmen Domínguez Fernández, Anne-Vinciane Doucet, Antonio Fernández Porcel, Mª Ángeles García Gil, Esteban López García, Camila Molina Cantero, Ana Peregrín González.
Forma de inscripción Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
Plazo de inscripción: del 11 al 20 de Enero. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Introducción a Python: Elementos básicos del lenguaje
Profesorado
José Vicente Pérez Peña (UGR), Patricia Ruano Roca (UGR)
Duración, lugar y fecha 12 horas presenciales (6 horas no presenciales). 7, 8, 14, 15, 21 y 22 de Abril. Sesiones Jueves y Viernes de 15:30 a 17:30 h. Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias). Se necesita portatil propio (Mac o PC).
Plazas y perfil
15 plazas. Dirigido preferentemente a alumnos/as de primer año de doctorado.
Justificación académica
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. Alguna de las características que hacen de Python el lenguaje ideal para cálculos científicos son:
- Es un lenguaje muy fácil de aprender, siendo el lenguaje más recomendado para usuarios que no cuentan con conocimientos de programación.
- Es de código libre, por lo que no requiere una licencia para su uso.
- Es multiplataforma, pudiéndose utilizar en diferentes Sistemas Operativos com MAC, LINUX, Windows, etc.
- Python es un lenguaje de programación real, con todas las características de un lenguaje de programación orientado a objetos, a diferencia de otros lenguajes como matlab que carecen de algunas funcionalidades en este sentido.
- Tiene multitud de módulos y librerías externos que realizan numerosas funciones de gran utilidad para científicos e ingenieros. A este respecto, módulos específicos para realizar cálculos científicos como numpy, matplotlib y scipy, han hecho que este lenguaje este ganando cada vez más popularidad entre científicos e ingenieros
- Se integra perfectamente con LaTeX, permitiendo el formateo de ecuaciones y la realización de figuras para artículos científicos o informes técnicos.
- Es extensible y altamente configurable. Librerías como matplotlib permiten realizar infinidad de gráficos de muy alta calidad e interactivos.
En este curso se verán los elementos básicos de un lenguaje de programación como Python; sintaxis, funciones principales, flujos condicionales y bucles, etc. El conocimiento de las bases del lenguaje es un paso previo fundamental para poder sacar el mayor rendimiento de las librerías específicas más utilizadas en los ámbitos científico y técnico.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá: • Los elementos básicos de un lenguaje de programación • Tipos de variables y su manipulación • Manipulación de listas, tuplas y diccionarios • Flujos condicionales if y recursivos for • Funciones básicas del lenguaje • Creación de funciones propias • Control de código y manejo excepciones
El alumno será capaz de: • Crear scripts en python para resolver problemas • Leer y analizar un programa escrito en Python • Manejar los principales entornos de programación con IPython (Spyder y Jupyter) • Leer y escribir datos en ficheros de texto • Diseñar algoritmos para la resolución secuencial de problemas • Depurar programas y reconocer los principales tipos de errores
Programa
Tema 1. Introducción (2h) • Introducción a los lenguajes de programación • Historia de Python • Elementos básicos de un lenguaje de programación • Descarga e instalación de anaconda con scipy • Python vs IPython • Partes principales de Spider • Introducción a los notebooks de IPython
Tema 2. Tipos básicos, variables y expresiones (4h) • Tipos de datos en Python • Variables, operadores y expresiones • Módulos math y random • Listas en Python • Métodos para la manipulación de cadenas de texto • Tuplas y diccionarios
Tema 3. Operadores y funciones (4h) • Operador lógico If • Bucles for • Bucles while • Creación y manejo de funciones • Ámbito de las variables • Funciones más importantes de Python
Tema 4. Operación de entrada/salida y optimización de código (4h) • Lectura de ficheros de texto • Escritura en archivos de texto • Módulos os y sys • Control de ficheros y directorios • Optimización de código • Tipos de errores principales en Python • Control de código y manejo excepciones
Forma de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
Plazo de inscripción: 7-18 de marzo de 2016. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Macros en Excel (09/2017)
Profesorado José Vicente Pérez Peña (Departamento de Geodinámica)
Duración, lugar y fechas
- 20 horas lectivas y 10 horas de trabajo personal del alumno
- 7, 8, 14, 15, 21, 22, 28 y 29 de septiembre, de 16:00 a 19:00 h.
- Facultad de Ciencias. Aula Juan Campos.
- Se necesita portatil propio (Mac o PC).
Plazas y perfil
- 15 plazas.
- Dirigido preferentemente a alumnos/as de segundo año de doctorado.
Justificación académica Excel es uno de los programas más populares para gestión, tratamiento y análisis de datos científicos. Incluye multitud de utilidades y funciones que lo hacen una herramienta imprescindible para el científico. Además de toda la funcionalidad que incluye este programa, cuenta con la posibilidad de expandir su utilidad mediante la programación de macros.
La palabra macro es una abreviatura de “macroinstrucción”, es decir un conjunto de instrucciones que se ejecutan secuencialmente. Una macro es un pequeño programa que realiza una tarea específica a través de una serie de instrucciones. Este pequeño programa se encuentra dentro de la aplicación principal, y por lo tanto puede acceder a todas las funcionalidades de la misma. Es decir, una macro dentro de Excel podrá acceder a los libros, hojas, formulas, celdas, … de la aplicación principal.
Mediante la programación de macros podremos automatizar tareas que impliquen numerosos pasos, definir funciones a medida y utilizarías como las demás funciones incluidas en Excel, añadir funcionalidad extra mediante formularios, botones, menus, etc. Este curso está dirigido a estudiantes de doctorado que quieran expandir las posilbidades que MS Excel cuenta para el análisis y gestión de datos. En este curso se explorará la creación y edición de Macros, así como los fundamentos del leguaje Visual Basic y el modelo de objetos específico utilizado por Excel.
Objetivos educativos, profesionales y competencias generales adquiridas
- El alumno sabrá:
- Fundamentos de las macros en Excel; creación, edición, y ejecución de las mismas
- Tipos de variables, ámbito y manipulación en visual Basic
- Flujos condicionales if y bucles for
- Procedimientos y Funciones
- Programación orientada a objetos y modelo de objetos de MS Excel
- El alumno será capaz de:
- Crear, editar, y ejecutar macros en MS ExcelCreación
- Manejar el editor de Visual Basic incluido con Excel
- Conocer los fundamentos de la programación en Visual Basic
- Leer y analizar una Macro
- Trabajar con el modelo de objetos de Excel
- Creación de fórmulas a medida
- Creación de hojas de cálculo interactivas con botones, formularios, etc.
- Diseñar algoritmos para la resolución secuencial de problemas
- Depurar código e identificar errores de ejecución
Programa
- Introducción a las Macros en Excel. Creación de nuestra primera Macro. El entorno Visual Basic for Applications. Grabación automática de Macros. Análisis y ejecución de Macros
- Introducción a los elementos básicos de Visual Basic. Variables, operadores y expresiones. Flujos condicionales if. Bucles recursivos for y while. Funciones y procedimientos.
- Introducción a la programación orientada a objetos. Fundamentos de la POO. Creación y manipulación de objetos en Visual Basic.
- Modelo de objetos de MS Excel. Manipulación de celdas y rangos mediante el objeto Range. Manipulación de hojas y libros.
- Creación de elementos interactivos. Creación de menús, botones y barras de herramientas.
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) con la palabra “Inscripción a cursos, Macros Excel” en el asunto. En el cuerpo del mensaje debe indicarse el programa de doctorado a la que pertenece y el año de doctorado.
- Plazo de inscripción: 26 de junio al 7 de julio de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Curso de LaTeX y Git (10/2017)
Profesorado
- Ángel Pablo Hinojosa Gutiérrez ha sido durante varios años técnico en la Oficina de Software Libre. Durante ese tiempo ha impartido diferentes cursos, tanto presenciales como virtuales, sobre git y LaTeX. También ha publicado un libro, “Aprende git”, disponible en Amazon y que ha sido en varias ocasiones best seller dentro del área de programación.
- Renato Luis Ramírez Rivero es licenciado en Ciencias Físicas y técnico en la Oficina de Software Libre. Tiene experiencia docente de más de 15 años en diferentes áreas, incluyendo especialmente temas relacionados con la informática, y ha sido profesor en cursos de LaTeX tanto presenciales como virtuales.
Duración, lugar y fecha
- Duración: Curso de 20 horas, 10 horas presenciales y 10 horas virtuales (a través de Git o usando Prado).
- Lugar: Aula 0.4 de la Escuela Técnica Superior de Ingenierías Informática y de Telecomunicación (ETSIIT). Calle Periodista Daniel Saucedo Aranda s/n, http://etsiit.ugr.es/pages/escuela.
- Fechas y horario: 5, 6 de octubre. De 18.00 a 20.00 h. (El resto de fechas pendientes de asignar)
Plazas y perfil
- 25 plazas.
- Dirigido a alumnos/as de doctorado de los programas de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías. El orden de prioridad será decreciente según el número de años en el programa, es decir, tendrán menor prioridad los del primer año.
Justificación académica La mayoría de las revistas científicas aceptan, exclusiva o preferentemente, fuentes del sistema de creación de documentos LaTeX. La facilidad en la gestión de la bibliografía, la calidad de la tipografía y los gráficos hacen que se puedan crear con relativa facilidad documentos profesionales y sobre todo científicos.
En este curso se enseña a trabajar un documento científico en todos sus aspectos, desde el contenido hasta los gráficos y la bibliografía. Como normalmente este trabajo se hace en colaboración, aparte de herramientas como Authorea u Overleaf, se puede trabajar en local usando repositorios de código, que no sólo evitan conflictos, sino que permiten interaccionar fácilmente a los investigadores, asignar tareas y expresar la terminación de tales tareas. La combinación de las dos herramientas, que se explica en este curso, permitirá a los estudiantes trabajar de forma más eficiente, rápida y reproducible y crear documentos que se ajusten a los requisitos de revistas y congresos.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá:
- Las razones por las que desarrollar en equipo mejora el rendimiento y la velocidad de publicación.
- Los conceptos detrás de los procesadores de textos científicos.
- Los fundamentos de los sistemas de control de versiones distribuidos
El alumno será capaz de:
- Elaborar flujos de trabajo para elaboración de documentos científicos (trabajos o propuestas de proyectos) en un entorno de control de fuentes.
- Adaptar los documentos a los requerimientos de una revista o congreso.
- Resolver conflictos que aparezcan en el trabajo.
Programa Día 1. LaTeX: Nociones básicas de LaTeX y su funcionamiento. Procesadores de textos y su historia. Consiguiendo e instalando LaTeX. Instalando LaTeX en Windows. • ¿Problemas con la instalación de LaTeX? • Trabajando con LaTeX. Git: Introducción a Git. Sistemas de control de fuentes, por qué usarlos. Qué es Git, de dónde viene. • Introducción a la línea de comandos. Instalación y configuración de Git. Clientes GUI para Linux, Windows y Mac. • Uso básico de Git. Crear y usar repositorios locales. Flujo de trabajo. Archivo gitnore, tags. • Logs y herramientas de análisis, recuperar versiones anteriores.
Día 2. LaTeX: Primeros pasos. Estructura y creación de documentos. El estado mental correcto. Editor de LaTeX Texmaker. Estructura básica de un documento. Creando contenido. • Capítulos y secciones. Entornos. Fórmulas matemáticas. • Crear un documento básico. • Dudas o comentarios sobre el contenido del tema. Git: Trabajando con Ramas. Qué son las ramas y para qué sirven. Creación, fusión y trabajo con ramas. • Conflictos entre ramas, soluciones. Borrado de commits. Rebase. Editado de la historia.
Día 3. LaTeX: Avanzando en contenido y forma. Acentos y UTF-8. Caracteres especiales. Tipos de letra. Más tipos de letra. Cambiado el tamaño de la letra. Unidades de medida. Listas. Primeras tablas. Introducción a las cajas. Cambiando los márgenes de la página. Indentado y espacios entre párrafos. Tablas. Fórmulas matemáticas. • Discusión y debate: “Maldito sea el día en que me metí en esto”. Git: Trabajo remoto. Repositorios remotos. Creación, clonación y sincronización. Conflictos entre repositorios. Identificación, Claves SSH básicas. • Trabajo colaborativo. Esquemas de trabajo.
Día 4. LaTeX: Ampliación de entornos. Fórmulas matemáticas y símbolos especiales. Tablas. Tipos de documento: estilos. Partes de un documento: más entornos. Tipos de letras en fórmulas matemáticas. Símbolos encima de otros. Enfatizado. El uso de las llaves. Paquete amsfonts. Modo “display”. Símbolos especiales. Comandos propios. Más sobre tablas y cajas. • Inserción de gráficos. Ejercicio sobre imágenes, tablas y ecuaciones. Git: Introducción a GitHub. Cómo usar GitHub. Alta y uso básico. Github como red social. GitHub pages. Issues, forks, pull request. Otros repositorios.
Día 5. LaTeX: Bibliografía. Creación de bases de datos para BibTeX. Gestión de base de datos. Estilos en BibTeX. Inserción en un documento. Bibliografía sobre BibTeX. • Ejercicio sobre BibTeX. Git: GitHub avanzado. GitHub avanzado. Planificación del trabajo. Interacción y revisiones usando GitHub.
Evaluación La evaluación será remota y basada en un proyecto: Creación de un documento LaTeX mantenido en GitHub. El documento deberá incluir la mayoría de los conceptos de LaTeX incluidos en el curso.
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación del programa de doctorado al que pertenece también en el asunto.
- Plazo de inscripción: Del 17 de julio al 20 de septiembre de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Curso de Ciencia Abierta (10-11/2017)
Profesorado
- Juan Julián Merelo Guervós es catedrático de universidad en el Departamento de Arquitectura y Tecnología de computadores y director de la Oficina de Software Libre.
- Germán Martínez Maldonado es técnico en la Oficina de Software Libre, graduado en Ingeniería Informática y experto DevOps.
- José Alonso Arias es técnico en la Oficina de Software Libre, graduado en Ciencias Políticas y con un máster en Administraciones Públicas, aparte de técnico de grado superior en Sistemas Informáticos. Es uno de los encargados de la producción del portal de datos abiertos de la UGR.
- Manuel Cogolludo Vallejo es experto en software libre y ha trabajado como técnico en la Oficina de Software Libre.
Duración, lugar y fecha
- Duración: Curso de 20 horas, 10 horas presenciales y 10 horas virtuales (a través de Git o usando Prado).
- Lugar: Aula 0.4 de la Escuela Técnica Superior de Ingenierías Informática y de Telecomunicación (ETSIIT). Calle Periodista Daniel Saucedo Aranda s/n, http://etsiit.ugr.es/pages/escuela.
- Fechas y horario: 19, 20 de octubre, 6 de noviembre de 17.00 a 21.00 h y 7 de noviembre de 17:30 a 19:30
Plazas y perfil
- 25 plazas.
- Dirigido a todos los alumnos/as de doctorado de los programas de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías. El orden de prioridad será decreciente según el número de años en el programa, es decir, tendrán menor prioridad los del primer año.
Justificación académica Trabajar con una metodología de ciencia abierta no sólo permite cumplir una obligación ética de mantener a la sociedad informada de los desarrollos que se hacen con fondos públicos, también lleva una serie de buenas prácticas que resultan en flujos de trabajo más eficientes que permiten que el camino desde la idea a la publicación sea mucho más rápido. Al usar también una serie de herramientas que permiten publicar todo tipo de “artefactos”, desde código a gráficos pasando por comentarios a experimentos fallidos, crean una práctica de comunicación que se acerca más a la divulgación, pero que a la vez permite crear trabajos con revisión entre pares más fáciles de realizar y que, eventualmente cuando se publican, recibirán más atención y más citas al estar en abierto.
Este curso introduce la metodología, las prácticas habituales y los recursos usados en ciencia abierta, con el objetivo esencial de ayudar al estudiante a acercar la práctica a la sociedad y también mejorar sus propias prácticas de experimentación y de publicación de esos experimentos.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno:
- Sabrá qué es la ciencia abierta y como se relaciona con los conceptos de software libre y datos abiertos.
- Entenderá el concepto de licencia y como se aplica a contenido, software y datos.
- Comprenderá las motivaciones principales para abrir todo o parte de su trabajo y como contribuirá a su carrera científica.
El alumno será capaz de:
- Liberar contenido, software y datos de la forma adecuada y con el mayor impacto posible en su carrera.
- Trabajar con herramientas libres que permitirán establecer flujos y actualizaciones más eficientes.
- Entender el concepto de reproducibilidad y cómo se aplica a flujos de trabajo.
- Usar repositorios de datos abiertos para su propia investigación.
Programa
Día 1. Software libre y datos y conocimiento abierto. Hacia la ciencia abierta. Qué hace libre al software libre. Licencias de software libre. • Conocimiento abierto. Licencias creative commons y su uso en la universidad y biblioteca. Qué liberar y cómo hacerlo. • Datos abiertos: uso de los mismos, licencias, datos abiertos en la UGR.
Día 2. Git y Github, claves para el desarrollo en abierto. El estado mental correcto. Por qué usar git y GitHub. Flujos de trabajo básicos. Colaboración a través de repositorios de código.
Día 3. Más allá del trabajo científico: ciencia de bitácora abierta. Más allá del PDF, elaboración de publicaciones con procesamiento de datos y presentación gráfica incluida. Rmarkdown. Knitr. Jupyter notebooks.
Día 4. Ciencia reproducible: buenas prácticas en el procesamiento de datos científicos. Buenas prácticas en el procesamiento de datos: publicación en abierto de los mismos. Creación de entornos de procesamiento de datos y experimentales reproducibles.
Día 5. Publicación en abierto: posibilidades y retorno. Publicación de todo tipo de artefactos experimentales (datos, código). Publicación de datos específicos. Publicación de flujos de trabajo. Publicación de borradores. Diferentes webs y sus posibilidades y retorno. Revisión en abierto.
Evaluación La evaluación será remota y basada en un proyecto: publicación de un informe de resultados reales procedentes del trabajo científico en alguna web de publicación en abierto.
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación del programa de doctorado al que pertenece también en el asunto.
- Plazo de inscripción: Del 17 de julio al 20 de septiembre de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Sesión formativa de IEEE: ¿Cómo publicar artículos en IEEE Xplore?
IEEE junto con la Biblioteca Universitaria ha organizado la siguiente sesión formativa Virtual: ¿Cómo publicar artículos en IEEE Xplore?
Duración, Lugar y Fecha:
- Fecha de realización: miércoles, 22 de noviembre de 2017
- Hora: 19:30 h.
- Duración: 1 h. y 30 minutos
Esta sesión formativa es de interés para los estudiantes de doctorado del área de ciencias, tecnologías e ingenierías, ya que IEEE es uno de lo editores más importantes en el ámbito de la ingeniería informática y ciencias afines.
Curso básico de análisis de datos en R (10-11/2017)
Profesorado Coordinador: José María Conde Porcuna (jmconde@ugr.es)
- Mohamed Abdelaziz (Dpto. Genética)
- Ana María Aguilera del Pino (Dpto. Estadística e I.O.)
- José María Conde Porcuna (Dpto. Ecología)
- Juan Lorite Moreno (Dpto. de Botánica)
- Rafael Rubio de Casas (Dpto. Ecología)
- María del Mar Rueda García (Dpto. Estadística e I.O.)
- Francisco de Asís Torres Ruiz (Dpto. Estadística e I.O.)
Lugar Sala de medios audiovisuales de la Facultad de Ciencias, excepto el 10 de octubre (que será en el aula A-20) y el 10 de noviembre (que será en A-10).
Es necesario llevar pórtatil, pc o mac
Carga docente
- Horas presenciales: 36 horas (26 horas de clases teórico-prácticas + 7 horas tutorías)
- Horas no presenciales: 25 horas de estudio/trabajo de los estudiantes.
Plazas y perfil
- Plazas: 20
- Dirigido a alumnos/as de doctorado de los programas de la Escuela de Doctorado de Ciencias, Tecnologías e Ingenierías.
Justificación académica
El curso pretende que los estudiantes de doctorado conozcan y apliquen los métodos estadísticos más utilizados en Biología. En las clases se utilizarán datos reales como ejemplos para una mejor comprensión. Los alumnos podrán aplicar los conocimientos adquiridos sobre los ficheros de datos que dispongan para la realización de sus Tesis doctorales. Los análisis que hagan con dichos ficheros serán supervisados inicialmente por el profesorado de la asignatura.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá utilizar análisis estadísticos fundamentales que permitan explicar la respuesta de variables de interés a diversos factores.
El alumno será capaz de diseñar e interpretar experimentos de campo y laboratorio para conocer los posibles factores y su efecto sobre variables de interés.
Programa, calendario y horario 6 de octubre (viernes), 9:00-12:00 (JM Conde). Presentación del curso. Estadística básica: Diseño experimental. Pseudoreplicación y pseudofactorialismo. Tipos de datos.
6 de octubre (viernes), 12:30-14:30 (M Abdelaziz). Estadística básica: Introducción a R. Correlaciones paramétricas y no paramétricas.
10 de octubre (martes), 9:00-11:00 (MM Rueda). Inferencia básica: Problema de una muestra. Problema de dos muestras independientes y apareadas. Contrastes paramétricos y no paramétricos para una y dos muestras.
10 de octubre (martes), 11:30-13:30 (F Torres). Modelos lineales generales: Regresión lineal simple: Ajuste e interpretación de resultados. Predicción. Calibración lineal. Contraste de linealidad para datos repetidos. Comprobación de asunciones.
20 de octubre (viernes), 9:00-11:00 (F Torres). Modelos lineales generales: Regresión lineal múltiple: Ajuste e interpretación de resultados. Restricciones lineales. Selección de regresores.
20 de octubre (viernes), 11:30-13:30 (MM Rueda). Modelos lineales generalizados: variables explicativas cuantitativas: Regresión logística binomial y multinomial. Selección de regresores. Regresión de Poisson.
25 de octubre (miércoles), 9:00-11:00 (AM Aguilera). Análisis de datos categóricos: Independencia y asociación en tablas bidimensionales.
25 de octubre (miércoles), 11:30-13:30 (AM Aguilera). Análisis de datos categóricos: Independencia condicional y asociación parcial. Metodología de Mantel-Hanzel.
3 de noviembre (viernes), 9:00-11:00 (J Lorite). Diseño de experimentos y análisis de la varianza (ANOVA): Diseños completamente aleatorizados. Diseños en bloques. Cuadrados latinos y grecolatinos. ANOVA paramétrico.
3 de noviembre (viernes), 11:30-13:30 (J Lorite). Diseño de experimentos y técnicas Anova asociadas: ANOVA de medidas repetidas. Diseños anidados.
10 de noviembre (viernes), 9:00-11:00 (M Abdelaziz). Contrastes múltiples no paramétricos: Muestras independientes: Análisis de Kruskal-Wallis. Muestras dependientes: Análisis de Friedman y Prueba de Cochran.
10 de noviembre (viernes), 11:30-13:30 (JM Conde). Modelos lineales: variables explicativas cuantitativas y cualitativas: ANCOVA. Modelos y selección de modelos: AIC y AICc.
16 de noviembre (jueves), 9:00-11:00 (R Rubio). Correlación y regresión de matrices de distancia: ¿Qué es una matriz de distancia? Análisis espacial: Análisis de Mantel simple.
16 de noviembre (jueves), 11:30-13:30 (R Rubio). Correlación y regresión de matrices de distancia: Análisis de mantel parcial. Regresión múltiple de matrices (MRM).
- Otras actividades
De manera no presencial, los alumnos irán trabajando con ficheros de datos de sus Tesis doctorales (si aún no dispusieran de ellos, se les entregarían ficheros de datos).
Semana del 27 de noviembre al 1 de diciembre: Supervisión del trabajo de los alumnos de forma personalizada (los alumnos serán repartidos entre los profesores según las afinidades previamente establecidas). Los horarios para la supervisión de notificarán a la finalización de las clases.
Evaluación Valoración final del trabajo individual a partir de una o varias bases de datos, considerando la estrategia seguida en el análisis de datos, la interpretación de resultados y la elaboración de conclusiones (100%).
Forma y plazo de inscripción
- Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación del programa de doctorado al que pertenece también en el asunto.
- Plazo de inscripción: Del 17 de julio al 20 de septiembre de 2017. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Forma de inscripción: Los alumnos deben mandar un email a la Escuela de Doctorado (actividadesdoctorado@ugr.es) con la palabra “Inscripción a curso Herramientas de búsqueda y gestión de información para el desarrollo de la Investigación ” en el asunto y con indicación del programa de doctorado al que pertenece también en el asunto.
Curso 2015/2016
Taller de escritura/elaboración/preparación de un artículo científico
Writing a research paper in English: strategies and techniques
Profesorado, duración, lugar y fecha
Dra. Pamela Faber Benítez, Catedrática Departamento de Traducción e Interpretación. Universidad de Granada. 40 horas (10h presenciales + 30 trabajo personal). Lugar: Aulario EIP (Antigua Facultad de Ciencias de la Salud); Aula de Informática nº 2. Fechas: 2, 4, 7, 9 y 11 de marzo, 8-10.00 h.
Plazas y perfil
30 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado. Así mismo, para el buen aprovechamiento de los alumnos, deben tener un nivel razonable de inglés tanto hablado como escrito (al menos, B2).
Programa
1. Introduction. 1.1 English as a lingua franca in the scientific world 1.2 The need to publish 1.3 Types of paper
2. Organization. 2.1 Sections 2.2 Content 2.3 Format and Layout 2.4 Common errors
3. Language. 3.1 Syntax and sentence structure 3.2 Semantics and terminology 3.3 Style and punctuation 3.4 Common errors
4 Strategies 4.1 Making notes 4.2 Keeping track of references 4.3 Translation: problems and pitfalls 4.4 Revising 4.5 Avoiding plagiarism
Competencias
CA04 - Trabajar tanto en equipo como de manera autónoma en un contexto internacional o multidisciplinar. CA05 - Integrar conocimientos, enfrentarse a la complejidad y formular juicios con información limitada. CA06 - La crítica y defensa intelectual de soluciones. CB11 - Comprensión sistemática de un campo de estudio y dominio de las habilidades y métodos de investigación relacionados con dicho campo CB14 - Capacidad de realizar un análisis crítico y de evaluación y síntesis de ideas nuevas y complejas. CB15 - Capacidad de comunicación con la comunidad académica y científica y con la sociedad en general acerca de sus ámbitos de conocimiento en los modos e idiomas de uso habitual en su comunidad científica internacional.
Forma de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto. Adjuntar certificado de nivel de inglés.
Plazo de inscripción: 18-29 de enero de 2016. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Python avanzado para ciencia e ingeniería
Profesorado
José Vicente Pérez Peña (UGR)
Duración, lugar y fecha
12 horas presenciales (+6 horas no presenciales). 5, 6, 12, 13, 19, 20 de Mayo. Sesiones Jueves y Viernes de 15:30 a 17:30 h. Aula Juan Campos (1ª planta del Hall de la Facultad de Ciencias). Se necesita portatil propio (Mac o PC).
Plazas y perfil
15 plazas. Dirigido preferentemente a alumnos/as de segundo año de doctorado.
Justificación académica
Python es uno de los mejores lenguajes para su uso científico y técnico. Tiene algunas características que lo hacen realmente interesante en este ámbito, como son; es interpretado, de alto nivel, muy fácil de aprender, fácilmente extensible y cuenta con una librería estándar con mucha funcionalidad. Este lenguaje está siendo actualmente utilizado por instituciones científicas como la NASA, JPL, y otras como Google, DreamWorks, Disney, etc. En el ámbito científico y técnico, python se está abriendo paso de forma firme gracias a librerías específicas como numpy, matplotlib y scipy. El uso de estas librerías ofrece a los usuarios de Python una infinidad de recursos matemáticos y científicos para la resolución de problemas complejos y la creación de gráficos de muy alta calidad.
Algunas de las operaciones básicas utilizadas en cálculo y programación científico-técnica incluyen matrices, integrales, ecuaciones diferenciales, estadística, etc. Python en su paquete básico no cuenta por defecto con funciones para realizar este tipo de cálculos directamente. Así mismo, los tipos básicos de variables de Python no están optimizados para el manejo de gran cantidad de datos. NumPy y SciPy son dos librerías muy potentes que cuentan con toda esta funcionalidad de la que carece el paquete básico de Python, y por tanto que posibilitan la utilización de este lenguaje para fines científicos y técnicos.
La librería de numpy se especializa en el procesado numérico utilizando matrices multidimensionales, y permite un cálculo matricial directo al igual que programas especializados como matlab. Así mismo cuenta con métodos y funciones para la creación, manejo, redimensionado, etc., de matrices, lo cual reduce considerablemente el esfuerzo de programación requerido en otros lenguajes.
La librería de matplotlib es una librería gráfica que toma todas las ventajas de numpy. Permite la creación de infinidad de gráficos de alta calidad (ráster y vectorial), así como la modificación de todas sus características. Matplotlib no solo se integra perfectamente con numpy, sino que permite el lenguaje de marcado de LaTeX, pudiendo crear gráficos de muy alta calidad para publicaciones científicas e informes técnicos.
SciPy va un paso más allá, y utiliza toda la funcionalidad de numpy para realizar cálculos matemáticos avanzados como la integración, diferenciación, algebra lineal, no lineal, etc. También cuenta con multitud de funciones de alto nivel para el tratamiento estadístico de los datos.
Una lista complete de todas las funciones de numpy, matplotlib y scipy ocuparía cientos de páginas, por lo que en este curso se tratarán las funciones más utilizadas. Se introducirá al alumno en las rutinas de trabajo con estas librerías y a la resolución de los problemas más comunes en ciencia e ingeniería. Con este curso también se pretende que el alumno tenga los conocimientos necesarios para entender la documentación de estas librerías con el fin de capacitarlo para poder utilizar funcionalidad específica de las mismas no tratada en este curso.
Objetivos educativos, profesionales y competencias generales adquiridas
El alumno sabrá: • Manejo de matrices multidimensionales con numpy • Funciones básicas para la creación y utilización de matrices de numpy • Lectura-escritura en disco de datos • Creación y representación de funciones matemáticas • Creación de distintos gráficos con matplotlib • Modificación de símbolos y leyendas • Funciones mátematicas de alto nivel y estadística con scipy
El alumno será capaz de: • Crear y modificar gráficos • Integrar LaTeX directamente en un gráfico • Representar funciones y resolver ecuaciones matemáticas • Entender la documentación de las librerías de Python • Realizar cálculos matemáticos de alto nivel y resolución de problemas complejos
Programa formativo
Tema 1. Manejo de datos con numpy (4h) • Constantes y funciones de numpy • Arrays de numpy • Métodos para la creación de arrays • Operaciones con arrays • Indexado y slicing en arrays • Leer y guardar arrays en archivos de texto
Tema 2. Representación gráfica con matplotlib (4h) • Representación básica de funciones • Representación de varias curvas • Representación de nube de puntos • Representación de histogramas y boxplots • Definiendo colores y símbolos • Añadiendo leyendas y etiquetas • Control de ejes • Representación de múltiples figuras
Tema 3. Análisis numérico con scipy (2h) • Integración numérica • Ecuaciones diferencias ordinarias • Ecuaciones algebraicas no lineales • Ajuste e interpolación
Tema 4. Estadística con scipy (2h) • Estadística básica • Análisis espacial y clúster • Procesado de señales e imágenes
Forma de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
Plazo de inscripción: 7-18 de marzo de 2016. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
Preparación y elaboración de proyectos
Profesorado, duración, lugar y fecha
Vicerrectorado de Investigación y Transferencia. 10 horas. Sala de conferencias del edificio CTT, Gran Vía 48, sexta planta. Del 4 a 6 de abril, de 10 a 13 h.
Plazas y perfil 30 plazas. Estudiantes de doctorado de tercer año y egresados recientes (dos años).
Programa
- 4 Abril.
10.00-11.30 h.
¿Qué es un proyecto?. Fases. Definición de objetivos. Planificación. Control. Justificación. Principales convocatorias de financiación de proyectos para jóvenes doctores. Plan Estatal y Horizonte 2020. Convocatorias de especialización posdoctoral en Plan Estatal. Junta de Andalucía y Horizonte 2020.
Por: Miguel Angel Guardia López y José Antonio Carrillo Miñán.
12-13 h.
Aspectos esenciales para la presentación de un proyecto de éxito (1). La evaluación del curriculum. 10 reglas de oro para la publicación de artículos científicos en revistas de impacto.
Por: Daniel Torres Salinas.
- 5 abril.
10.00-13.00 h.
Aspectos esenciales para la presentación de un proyecto de éxito (2). Los aspectos éticos. Los códigos de buenas prácticas en investigación y doctorado. La solicitud del proyecto. Principales apartados. La elaboración del presupuesto. La evaluación del proyecto. Criterios de evaluación. ¿Qué critican los evaluadores en una solicitud de proyecto? Casos prácticos de informes de evaluación de proyectos del Plan Nacional. El equipo de investigación. Integrarse en un equipo de investigación de forma activa. Motivación y liderazgo (“equipos emocionalmente inteligentes”).
Por: Miguel Angel Guardia López, María del Carmen Aguilar Luzón y Marian Gómez Letrán.
- 20 de abril.
10-13 h.
Caso práctico de discusión y presentación de un proyecto.
Por: Leandro di Stasi (Talent Hub, jóven investigador con proyectos activos y anteriormente postdoc en EEUU; Departamento de Psicología Experimental). Forma de inscripción
Los alumnos deben mandar un email a la Escuela de Doctorado (epdoctorado@ugr.es) con la palabra “Inscripción a cursos” en el asunto y con indicación de la escuela doctoral a la que pertenece también en el asunto.
Plazo de inscripción: Del 11 al 20 de Enero. En caso de que haya más solicitudes que plazas se seleccionarán los alumnos/as según su adecuación al perfil del curso y el orden de inscripción.
CONFERENCIA: Scientific Publication: How to Survive?
- Prof. Igor Vlahović, University of Zagreb, Croatia
igor.vlahovic@gmail.com
http://rgn.hr/~ivlahovi/ivlahovic_eng.htm
- Parte I: martes 8 de noviembre, 11–13:30 h.
- Parte II: miércoles 9 de noviembre, 11–13:30 h.
En ambos casos en el Salón de Grados de la Facultad de Ciencias
Lectures on the practical aspects of the preparation and writing of scientific papers, dealing with reviewers and editors, keeping motivation for writing, and keeping a good relationship and fruitful cooperation with PhD advisors.
Scientific publishing is focused on distribution of new results, enabling their visibility to wider scientific community, but also helping researchers to obtain their academic promotion and fundings of future projects. Constant pressure is well-described by a common expression 'publish or perish', and in order to survive every scientist should learn and master all phases of the process. That is today necessary because even the most original scientific results can be seriously and irreversibly neglected if not presented properly.
We will go through the entire process of scientific publication from different perspectives, not only from the author's corner but also from the editor's and reviewer's side, to see common mistakes more clearly and discuss how to avoid them. The most important questions addressed will include: Why, where and how to publish your scientific results? What is responsible conduct of research and how to avoid common mistakes, including plagiarism and autoplagiarism? How to cooperate and publish with your advisor? What questions to address while preparing a concept of your paper? What is the structure of the scientific paper and how to present your data? How to fight procrastination and finally finish the paper? How and when to choose a journal and how to prepare the final version of your manuscript for submission? How to successfully communicate with editors and reviewers? What to do after your paper is published and what to do if it is finally rejected?